+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7zj5 | ||||||
|---|---|---|---|---|---|---|---|
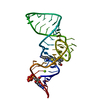
| タイトル | Unbound state of a brocolli-pepper aptamer FRET tile. | ||||||
 要素 要素 | brocolli-pepper aptamer | ||||||
 キーワード キーワード | RNA / origami / aptamer / fret | ||||||
| 機能・相同性 | : / RNA / RNA (> 10) / RNA (> 100) 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 | synthetic construct (人工物) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.55 Å | ||||||
 データ登録者 データ登録者 | McRae, E.K.S. / Vallina, N.S. / Hansen, B.K. / Boussebayle, A. / Andersen, E.S. | ||||||
| 資金援助 |  デンマーク, 1件 デンマーク, 1件
| ||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Structure determination of Pepper-Broccoli FRET pair by RNA origami scaffolding 著者: McRae, E.K.S. / Vallina, N.S. / Hansen, B.K. / Boussebayle, A. / Andersen, E.S. #1:  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018タイトル: Real-space refinement in PHENIX for cryo-EM and crystallography. 著者: Afonine, P.V. / Poon, B.K. / Read, R.J. / Sobolev, O.V. / Terwilliger, T.C. / Urzhumtsev, A. / Adams, P.D. #2:  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018タイトル: ISOLDE: a physically realistic environment for model building into low-resolution electron-density maps. 著者: Croll, T.I. #3:  ジャーナル: Nat Methods / 年: 2017 ジャーナル: Nat Methods / 年: 2017タイトル: cryoSPARC: algorithms for rapid unsupervised cryo-EM structure determination. 著者: Punjani, A. / Rubinstein, J.L. / Fleet, D.J. / Brubaker, M.A. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7zj5.cif.gz 7zj5.cif.gz | 269.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7zj5.ent.gz pdb7zj5.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  7zj5.json.gz 7zj5.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7zj5_validation.pdf.gz 7zj5_validation.pdf.gz | 1.1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7zj5_full_validation.pdf.gz 7zj5_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  7zj5_validation.xml.gz 7zj5_validation.xml.gz | 22.1 KB | 表示 | |
| CIF形式データ |  7zj5_validation.cif.gz 7zj5_validation.cif.gz | 32.4 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/zj/7zj5 https://data.pdbj.org/pub/pdb/validation_reports/zj/7zj5 ftp://data.pdbj.org/pub/pdb/validation_reports/zj/7zj5 ftp://data.pdbj.org/pub/pdb/validation_reports/zj/7zj5 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  14741MC  7zj4C M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: RNA鎖 | 分子量: 120700.953 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現) synthetic construct (人工物) / 発現宿主: synthetic construct (人工物) |
|---|---|
| #2: 化合物 | ChemComp-K / |
| 研究の焦点であるリガンドがあるか | N |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Unbound state of a brocolli-pepper aptamer FRET tile タイプ: COMPLEX / Entity ID: #1 / 由来: RECOMBINANT |
|---|---|
| 分子量 | 値: 0.12 MDa / 実験値: NO |
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 由来(組換発現) | 生物種: synthetic construct (人工物) |
| 緩衝液 | pH: 7.5 詳細: 40mM HEPES pH 7.5, 5mM MgCl2, 50mM KCl. Filtered through 0.22 um filter. |
| 試料 | 濃度: 2.5 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: Sample was purified by size exclusion chromatography. |
| 急速凍結 | 装置: LEICA EM GP / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 288 K 詳細: 3 uL sample, blotted onto double layer of whatman filter paper for 6 seconds. |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 700 nm / Cs: 2.7 mm |
| 撮影 | 電子線照射量: 60 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 1605 詳細: Collected with a calibrated pixel size of 0.647 Angstrom |
| 電子光学装置 | エネルギーフィルター名称: GIF Bioquantum / エネルギーフィルタースリット幅: 20 eV |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 478981 詳細: Picked from templates generated from an ab initio model | ||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 4.55 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 51278 / アルゴリズム: BACK PROJECTION 詳細: Local refinement was performed in cryoSPARC using a mask that covers the entire particle volume クラス平均像の数: 1 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: FLEXIBLE FIT / 空間: REAL | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 |
| ||||||||||||||||||||||||||||||||||||
| 精密化 | 交差検証法: NONE | ||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj