+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7p2e | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human mitochondrial ribosome small subunit in complex with IF3, GMPPMP and streptomycin | ||||||||||||
 要素 要素 |
| ||||||||||||
 キーワード キーワード | RIBOSOME / Initiation factor 3 / translation / antibiotic / streptomycin | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報mitochondrial translational initiation / mitochondrial ribosome binding / translation factor activity, RNA binding / mitochondrial ribosome assembly / positive regulation of mitochondrial translation / Mitochondrial translation elongation / Mitochondrial translation termination / Mitochondrial translation initiation / ribosome disassembly / negative regulation of mitotic nuclear division ...mitochondrial translational initiation / mitochondrial ribosome binding / translation factor activity, RNA binding / mitochondrial ribosome assembly / positive regulation of mitochondrial translation / Mitochondrial translation elongation / Mitochondrial translation termination / Mitochondrial translation initiation / ribosome disassembly / negative regulation of mitotic nuclear division / mitochondrial small ribosomal subunit / mitochondrial ribosome / mitochondrial translation / positive regulation of proteolysis / ribosomal small subunit binding / Mitochondrial protein degradation / translation initiation factor activity / apoptotic signaling pathway / fibrillar center / small ribosomal subunit rRNA binding / cell junction / ribosome binding / regulation of translation / ribosomal small subunit assembly / small ribosomal subunit / nuclear membrane / cell population proliferation / tRNA binding / mitochondrial inner membrane / rRNA binding / ribosome / mitochondrial matrix / structural constituent of ribosome / translation / protein domain specific binding / intracellular membrane-bounded organelle / mRNA binding / GTP binding / nucleolus / mitochondrion / RNA binding / nucleoplasm / nucleus / plasma membrane / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.4 Å | ||||||||||||
 データ登録者 データ登録者 | Itoh, Y. / Khawaja, A. / Singh, V. / Rorbach, J. / Amunts, A. | ||||||||||||
| 資金援助 |  スウェーデン, 2件 スウェーデン, 2件
| ||||||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2022 ジャーナル: Elife / 年: 2022タイトル: Structure of the mitoribosomal small subunit with streptomycin reveals Fe-S clusters and physiological molecules. 著者: Yuzuru Itoh / Vivek Singh / Anas Khawaja / Andreas Naschberger / Minh Duc Nguyen / Joanna Rorbach / Alexey Amunts /  要旨: The mitoribosome regulates cellular energy production, and its dysfunction is associated with aging. Inhibition of the mitoribosome can be caused by off-target binding of antimicrobial drugs and was ...The mitoribosome regulates cellular energy production, and its dysfunction is associated with aging. Inhibition of the mitoribosome can be caused by off-target binding of antimicrobial drugs and was shown to be coupled with a bilateral decreased visual acuity. Previously, we reported mitochondria-specific protein aspects of the mitoribosome, and in this article we present a 2.4-Å resolution structure of the small subunit in a complex with the anti-tuberculosis drug streptomycin that reveals roles of non-protein components. We found iron-sulfur clusters that are coordinated by different mitoribosomal proteins, nicotinamide adenine dinucleotide (NAD) associated with rRNA insertion, and posttranslational modifications. This is the first evidence of inter-protein coordination of iron-sulfur, and the finding of iron-sulfur clusters and NAD as fundamental building blocks of the mitoribosome directly links to mitochondrial disease and aging. We also report details of streptomycin interactions, suggesting that the mitoribosome-bound streptomycin is likely to be in hydrated gem-diol form and can be subjected to other modifications by the cellular milieu. The presented approach of adding antibiotics to cultured cells can be used to define their native structures in a bound form under more physiological conditions, and since streptomycin is a widely used drug for treatment, the newly resolved features can serve as determinants for targeting. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7p2e.cif.gz 7p2e.cif.gz | 3.1 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7p2e.ent.gz pdb7p2e.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  7p2e.json.gz 7p2e.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7p2e_validation.pdf.gz 7p2e_validation.pdf.gz | 1.8 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7p2e_full_validation.pdf.gz 7p2e_full_validation.pdf.gz | 1.8 MB | 表示 | |
| XML形式データ |  7p2e_validation.xml.gz 7p2e_validation.xml.gz | 164.5 KB | 表示 | |
| CIF形式データ |  7p2e_validation.cif.gz 7p2e_validation.cif.gz | 285.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/p2/7p2e https://data.pdbj.org/pub/pdb/validation_reports/p2/7p2e ftp://data.pdbj.org/pub/pdb/validation_reports/p2/7p2e ftp://data.pdbj.org/pub/pdb/validation_reports/p2/7p2e | HTTPS FTP |
-関連構造データ
| 関連構造データ |  13170MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-RNA鎖 , 1種, 1分子 A
| #1: RNA鎖 | 分子量: 306547.531 Da / 分子数: 1 / 由来タイプ: 天然 / 詳細: cell / 由来: (天然)  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
+28S ribosomal protein ... , 27種, 27分子 BCDEFGHIJKLMNOPQRSTUVWXYZ01
-タンパク質 , 4種, 4分子 2348
| #29: タンパク質 | 分子量: 13409.661 Da / 分子数: 1 / 由来タイプ: 天然 / 詳細: cell / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q96BP2 Homo sapiens (ヒト) / 参照: UniProt: Q96BP2 |
|---|---|
| #30: タンパク質 | 分子量: 22395.326 Da / 分子数: 1 / 由来タイプ: 天然 / 詳細: cell / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q9NWT8 Homo sapiens (ヒト) / 参照: UniProt: Q9NWT8 |
| #31: タンパク質 | 分子量: 78648.547 Da / 分子数: 1 / 由来タイプ: 天然 / 詳細: cell / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q96EY7 Homo sapiens (ヒト) / 参照: UniProt: Q96EY7 |
| #32: タンパク質 | 分子量: 32545.461 Da / 分子数: 1 / 由来タイプ: 組換発現 / 詳細: Natural variant Thr68Ile and Phe263Leu / 由来: (組換発現)  Homo sapiens (ヒト) / 解説: cell / 遺伝子: MTIF3, DC38 / 発現宿主: Homo sapiens (ヒト) / 解説: cell / 遺伝子: MTIF3, DC38 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: Q9H2K0 Homo sapiens (ヒト) / 参照: UniProt: Q9H2K0 |
-非ポリマー , 10種, 3176分子 
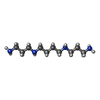

















| #33: 化合物 | ChemComp-NAD / | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| #34: 化合物 | ChemComp-SPM / | ||||||||||||
| #35: 化合物 | ChemComp-5I0 / [( | ||||||||||||
| #36: 化合物 | ChemComp-K / #37: 化合物 | ChemComp-MG / #38: 化合物 | ChemComp-ZN / | #39: 化合物 | #40: 化合物 | ChemComp-ATP / | #41: 化合物 | ChemComp-GNP / | #42: 水 | ChemComp-HOH / | |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 実験値: NO | ||||||||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||||||||
| 由来(組換発現) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||||||||||||||||||||
| 緩衝液 | pH: 7.5 | ||||||||||||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのタイプ: Quantifoil R2/1 | ||||||||||||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 297 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 4000 nm / 最小 デフォーカス(公称値): 500 nm / Cs: 2.7 mm / C2レンズ絞り径: 70 µm |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 4 sec. / 電子線照射量: 30 e/Å2 / 検出モード: COUNTING フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 実像数: 31773 |
| 電子光学装置 | エネルギーフィルター名称: GIF Quantum LS / エネルギーフィルタースリット幅: 20 eV |
| 画像スキャン | 動画フレーム数/画像: 20 / 利用したフレーム数/画像: 1-20 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 2487123 | ||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 885199 / アルゴリズム: BACK PROJECTION / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | 空間: REAL | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6RW4 Accession code: 6RW4 / Source name: PDB / タイプ: experimental model |
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj

















































