+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7ns0 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Bacilladnavirus capsid structure | |||||||||
 要素 要素 | Capsid protein VP2 | |||||||||
 キーワード キーワード | VIRUS / Jelly-roll / capsid | |||||||||
| 機能・相同性 | Uncharacterized protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Chaetoceros tenuissimus DNA virus type-II (ウイルス) Chaetoceros tenuissimus DNA virus type-II (ウイルス) | |||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.4 Å | |||||||||
 データ登録者 データ登録者 | Munke, A. / Okamoto, K. | |||||||||
| 資金援助 |  スウェーデン, スウェーデン,  日本, 2件 日本, 2件
| |||||||||
 引用 引用 |  ジャーナル: mBio / 年: 2022 ジャーナル: mBio / 年: 2022タイトル: Primordial Capsid and Spooled ssDNA Genome Structures Unravel Ancestral Events of Eukaryotic Viruses. 著者: Anna Munke / Kei Kimura / Yuji Tomaru / Han Wang / Kazuhiro Yoshida / Seiya Mito / Yuki Hongo / Kenta Okamoto /   要旨: Marine algae viruses are important for controlling microorganism communities in the marine ecosystem and played fundamental roles during the early events of viral evolution. Here, we have focused on ...Marine algae viruses are important for controlling microorganism communities in the marine ecosystem and played fundamental roles during the early events of viral evolution. Here, we have focused on one major group of marine algae viruses, the single-stranded DNA (ssDNA) viruses from the family. We present the capsid structure of the bacilladnavirus DNA virus type II (CtenDNAV-II), determined at 2.4-Å resolution. A structure-based phylogenetic analysis supported the previous theory that bacilladnaviruses have acquired their capsid protein via horizontal gene transfer from a ssRNA virus. The capsid protein contains the widespread virus jelly-roll fold but has additional unique features; a third β-sheet and a long C-terminal tail. Furthermore, a low-resolution reconstruction of the CtenDNAV-II genome revealed a partially spooled structure, an arrangement previously only described for dsRNA and dsDNA viruses. Together, these results exemplify the importance of genetic recombination for the emergence and evolution of ssDNA viruses and provide important insights into the underlying mechanisms that dictate genome organization. Single-stranded DNA (ssDNA) viruses are an extremely widespread group of viruses that infect diverse hosts from all three domains of life, consequently having great economic, medical, and ecological importance. In particular, bacilladnaviruses are highly abundant in marine sediments and greatly influence the dynamic appearance and disappearance of certain algae species. Despite the importance of ssDNA viruses and the last couple of years' advancements in cryo-electron microscopy, structural information on the genomes of ssDNA viruses remains limited. This paper describes two important achievements: (i) the first atomic structure of a bacilladnavirus capsid, which revealed that the capsid protein gene presumably was acquired from a ssRNA virus in early evolutionary events; and (ii) the structural organization of a ssDNA genome, which retains a spooled arrangement that previously only been observed for double-stranded viruses. #1:  ジャーナル: mBio / 年: 2022 ジャーナル: mBio / 年: 2022タイトル: Primordial capsid and spooled ssDNA genome structures reveal ancestral events of eukaryotic viruses 著者: Munke, A. / Kimura, K. / Tomaru, Y. / Wang, H. / Yoshida, K. / Mito, S. / Yuki, H. / Okamoto, K. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7ns0.cif.gz 7ns0.cif.gz | 308.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7ns0.ent.gz pdb7ns0.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  7ns0.json.gz 7ns0.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7ns0_validation.pdf.gz 7ns0_validation.pdf.gz | 1.4 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7ns0_full_validation.pdf.gz 7ns0_full_validation.pdf.gz | 1.4 MB | 表示 | |
| XML形式データ |  7ns0_validation.xml.gz 7ns0_validation.xml.gz | 45.7 KB | 表示 | |
| CIF形式データ |  7ns0_validation.cif.gz 7ns0_validation.cif.gz | 66.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ns/7ns0 https://data.pdbj.org/pub/pdb/validation_reports/ns/7ns0 ftp://data.pdbj.org/pub/pdb/validation_reports/ns/7ns0 ftp://data.pdbj.org/pub/pdb/validation_reports/ns/7ns0 | HTTPS FTP |
-関連構造データ
| 関連構造データ | 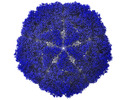 12554MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 | x 60
|
- 要素
要素
| #1: タンパク質 | 分子量: 43329.559 Da / 分子数: 3 / 由来タイプ: 天然 由来: (天然)  Chaetoceros tenuissimus DNA virus type-II (ウイルス) Chaetoceros tenuissimus DNA virus type-II (ウイルス)参照: UniProt: A0A0B6VL42 |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Chaetoceros tenuissimus DNA virus type-II / タイプ: VIRUS / 詳細: Capsid / Entity ID: all / 由来: NATURAL |
|---|---|
| 分子量 | 実験値: NO |
| 由来(天然) | 生物種:  Chaetoceros tenuissimus DNA virus type-II (ウイルス) Chaetoceros tenuissimus DNA virus type-II (ウイルス) |
| ウイルスについての詳細 | 中空か: NO / エンベロープを持つか: NO / 単離: SPECIES / タイプ: VIRION |
| 天然宿主 | 生物種: Chaetoceros tenuissimus |
| ウイルス殻 | 直径: 35 nm / 三角数 (T数): 3 |
| 緩衝液 | pH: 7.4 |
| 試料 | 濃度: 10 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3000 nm / 最小 デフォーカス(公称値): 1000 nm |
| 撮影 | 電子線照射量: 37 e/Å2 フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: I (正20面体型対称) | ||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 33507 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||
| 精密化 | 交差検証法: NONE 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2 | ||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 12.03 Å2 | ||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj