+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6rh3 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of E. coli RNA polymerase elongation complex bound to CTP substrate | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | TRANSCRIPTION / E. coli RNA polymerase / CTP / GreB / Elongation complex | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報submerged biofilm formation / cellular response to cell envelope stress / cytosolic DNA-directed RNA polymerase complex / regulation of DNA-templated transcription initiation / bacterial-type flagellum assembly / bacterial-type flagellum-dependent cell motility / nitrate assimilation / DNA-directed RNA polymerase complex / transcription elongation factor complex / regulation of DNA-templated transcription elongation ...submerged biofilm formation / cellular response to cell envelope stress / cytosolic DNA-directed RNA polymerase complex / regulation of DNA-templated transcription initiation / bacterial-type flagellum assembly / bacterial-type flagellum-dependent cell motility / nitrate assimilation / DNA-directed RNA polymerase complex / transcription elongation factor complex / regulation of DNA-templated transcription elongation / transcription antitermination / DNA-templated transcription initiation / cell motility / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / response to heat / intracellular iron ion homeostasis / protein dimerization activity / response to antibiotic / DNA-templated transcription / magnesium ion binding / DNA binding / zinc ion binding / membrane / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | ||||||
 データ登録者 データ登録者 | Abdelkareem, M. / Saint-Andre, C. / Takacs, M. / Papai, G. / Crucifix, C. / Guo, X. / Ortiz, J. / Weixlbaumer, A. | ||||||
| 資金援助 |  フランス, 1件 フランス, 1件
| ||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2019 ジャーナル: Mol Cell / 年: 2019タイトル: Structural Basis of Transcription: RNA Polymerase Backtracking and Its Reactivation. 著者: Mo'men Abdelkareem / Charlotte Saint-André / Maria Takacs / Gabor Papai / Corinne Crucifix / Xieyang Guo / Julio Ortiz / Albert Weixlbaumer /  要旨: Regulatory sequences or erroneous incorporations during DNA transcription cause RNA polymerase backtracking and inactivation in all kingdoms of life. Reactivation requires RNA transcript cleavage. ...Regulatory sequences or erroneous incorporations during DNA transcription cause RNA polymerase backtracking and inactivation in all kingdoms of life. Reactivation requires RNA transcript cleavage. Essential transcription factors (GreA and GreB, or TFIIS) accelerate this reaction. We report four cryo-EM reconstructions of Escherichia coli RNA polymerase representing the entire reaction pathway: (1) a backtracked complex; a backtracked complex with GreB (2) before and (3) after RNA cleavage; and (4) a reactivated, substrate-bound complex with GreB before RNA extension. Compared with eukaryotes, the backtracked RNA adopts a different conformation. RNA polymerase conformational changes cause distinct GreB states: a fully engaged GreB before cleavage; a disengaged GreB after cleavage; and a dislodged, loosely bound GreB removed from the active site to allow RNA extension. These reconstructions provide insight into the catalytic mechanism and dynamics of RNA cleavage and extension and suggest how GreB targets backtracked complexes without interfering with canonical transcription. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6rh3.cif.gz 6rh3.cif.gz | 602.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6rh3.ent.gz pdb6rh3.ent.gz | 476 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6rh3.json.gz 6rh3.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6rh3_validation.pdf.gz 6rh3_validation.pdf.gz | 1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6rh3_full_validation.pdf.gz 6rh3_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  6rh3_validation.xml.gz 6rh3_validation.xml.gz | 90.1 KB | 表示 | |
| CIF形式データ |  6rh3_validation.cif.gz 6rh3_validation.cif.gz | 140.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/rh/6rh3 https://data.pdbj.org/pub/pdb/validation_reports/rh/6rh3 ftp://data.pdbj.org/pub/pdb/validation_reports/rh/6rh3 ftp://data.pdbj.org/pub/pdb/validation_reports/rh/6rh3 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4882MC  4885C  4886C  4892C  4893C  6ri7C  6ri9C  6rinC  6ripC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-DNA鎖 , 2種, 2分子 NT
| #1: DNA鎖 | 分子量: 12064.742 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  |
|---|---|
| #2: DNA鎖 | 分子量: 11864.623 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  |
-DNA-directed RNA polymerase subunit ... , 4種, 5分子 ABCDE
| #3: タンパク質 | 分子量: 36558.680 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   #4: タンパク質 | | 分子量: 150820.875 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  遺伝子: rpoB, groN, nitB, rif, ron, stl, stv, tabD, b3987, JW3950 発現宿主:  #5: タンパク質 | | 分子量: 155366.781 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   #6: タンパク質 | | 分子量: 8321.375 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   |
|---|
-RNA鎖 , 1種, 1分子 R
| #7: RNA鎖 | 分子量: 4503.716 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  |
|---|
-非ポリマー , 3種, 4分子 
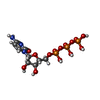



| #8: 化合物 | | #9: 化合物 | ChemComp-CTP / | #10: 化合物 | ChemComp-MG / | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 実験値: NO | ||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||
| 緩衝液 | pH: 8 | ||||||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: Cryo-EM structure of E. coli RNA polymerase elongation complex bound to CTP substrate | ||||||||||||||||||||||||
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 46 e/Å2 フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.12_2829: / 分類: 精密化 | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| |||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | |||||||||||||||
| 3次元再構成 | 解像度: 3.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 107124 / 対称性のタイプ: POINT | |||||||||||||||
| 原子モデル構築 | プロトコル: FLEXIBLE FIT / 空間: REAL | |||||||||||||||
| 原子モデル構築 | PDB-ID: 6ALH Accession code: 6ALH / Source name: PDB / タイプ: experimental model |
 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj




































































