+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 2y9k | ||||||
|---|---|---|---|---|---|---|---|
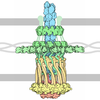
| タイトル | Three-dimensional model of Salmonella's needle complex at subnanometer resolution | ||||||
 要素 要素 | PROTEIN INVG | ||||||
 キーワード キーワード | PROTEIN TRANSPORT / TYPE III SECRETION SYSTEM / OUTER MEMBRANE RING / SECRETIN FAMILY / C15 FOLD | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報type III protein secretion system complex / type II protein secretion system complex / protein secretion by the type III secretion system / protein secretion / cell outer membrane / identical protein binding 類似検索 - 分子機能 | ||||||
| 生物種 |  SALMONELLA ENTERICA SUBSP. ENTERICA SEROVAR TYPHIMURIUM (サルモネラ菌) SALMONELLA ENTERICA SUBSP. ENTERICA SEROVAR TYPHIMURIUM (サルモネラ菌) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 8.3 Å | ||||||
 データ登録者 データ登録者 | Schraidt, O. / Marlovits, T.C. | ||||||
 引用 引用 |  ジャーナル: Science / 年: 2011 ジャーナル: Science / 年: 2011タイトル: Three-dimensional model of Salmonella's needle complex at subnanometer resolution. 著者: Oliver Schraidt / Thomas C Marlovits /  要旨: Type III secretion systems (T3SSs) are essential virulence factors used by many Gram-negative bacteria to inject proteins that make eukaryotic host cells accessible to invasion. The T3SS core ...Type III secretion systems (T3SSs) are essential virulence factors used by many Gram-negative bacteria to inject proteins that make eukaryotic host cells accessible to invasion. The T3SS core structure, the needle complex (NC), is a ~3.5 megadalton-sized, oligomeric, membrane-embedded complex. Analyzing cryo-electron microscopy images of top views of NCs or NC substructures from Salmonella typhimurium revealed a 24-fold symmetry for the inner rings and a 15-fold symmetry for the outer rings, giving an overall C3 symmetry. Local refinement and averaging showed the organization of the central core and allowed us to reconstruct a subnanometer composite structure of the NC, which together with confident docking of atomic structures reveal insights into its overall organization and structural requirements during assembly. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  2y9k.cif.gz 2y9k.cif.gz | 352.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb2y9k.ent.gz pdb2y9k.ent.gz | 282.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  2y9k.json.gz 2y9k.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  2y9k_validation.pdf.gz 2y9k_validation.pdf.gz | 766.2 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  2y9k_full_validation.pdf.gz 2y9k_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  2y9k_validation.xml.gz 2y9k_validation.xml.gz | 109.3 KB | 表示 | |
| CIF形式データ |  2y9k_validation.cif.gz 2y9k_validation.cif.gz | 134.9 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/y9/2y9k https://data.pdbj.org/pub/pdb/validation_reports/y9/2y9k ftp://data.pdbj.org/pub/pdb/validation_reports/y9/2y9k ftp://data.pdbj.org/pub/pdb/validation_reports/y9/2y9k | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 15616.915 Da / 分子数: 15 / 断片: N-TERMINAL DOMAIN, RESIDUES 34-170 / 由来タイプ: 天然 由来: (天然)  SALMONELLA ENTERICA SUBSP. ENTERICA SEROVAR TYPHIMURIUM (サルモネラ菌) SALMONELLA ENTERICA SUBSP. ENTERICA SEROVAR TYPHIMURIUM (サルモネラ菌)参照: UniProt: P35672 |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: NEEDLE COMPLEX / タイプ: COMPLEX |
|---|---|
| 緩衝液 | pH: 7.5 / 詳細: 10mM Tris-HCl 0.5M NaCl 0.1% LDAO |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | 詳細: CARBON |
| 急速凍結 | 凍結剤: ETHANE / 詳細: LIQUID ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI POLARA 300 詳細: ACUAL MAGNIFICATION AT CCD 112968, CAMERA PIXEL SIZE 15UM, 1.33 ANGSTROM PER PIXEL, DATA COLLECTED SEMI- AUTOMATICALLY USING POINT-2-POINT (DEVELOPED IN-HOUSE) |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 93000 X / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 1000 nm / Cs: 2 mm |
| 試料ホルダ | 傾斜角・最小: 0 ° |
| 撮影 | フィルム・検出器のモデル: GENERIC GATAN (4k x 4k) |
| 放射波長 | 相対比: 1 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | 詳細: EACH CCD FRAME | ||||||||||||
| 対称性 | 点対称性: C15 (15回回転対称) | ||||||||||||
| 3次元再構成 | 手法: PROJECTION MATCHING / 解像度: 8.3 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ピクセルサイズ(実測値): 1.33 Å 詳細: RESOLUTION 8.3 ANGSTROM (0.5 FSC), 6.7 ANGSTROM (HALF BIT) SUBMISSION BASED ON EXPERIMENTAL DATA FROM EMDB EMD-1871. (DEPOSITION ID: 7820). 対称性のタイプ: POINT | ||||||||||||
| 原子モデル構築 | プロトコル: RIGID BODY FIT / 空間: REAL / Target criteria: Cross-correlation coefficient / 詳細: METHOD--RIGID BODY FITTING | ||||||||||||
| 原子モデル構築 | PDB-ID: 3GR5 Accession code: 3GR5 / Source name: PDB / タイプ: experimental model | ||||||||||||
| 精密化 | 最高解像度: 8.3 Å | ||||||||||||
| 精密化ステップ | サイクル: LAST / 最高解像度: 8.3 Å
|
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj