+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Progesterone-bound DB3 Fab in complex with computationally designed DBPro1156_2 protein binder | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | progesterone / binder / de novo / Fab / anti-kappa / DE NOVO PROTEIN | |||||||||
| 生物種 | synthetic construct (人工物) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.3 Å | |||||||||
 データ登録者 データ登録者 | Pacesa M / Marchand A / Correia BE | |||||||||
| 資金援助 |  スイス, 1件 スイス, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2025 ジャーナル: Nature / 年: 2025タイトル: Targeting protein-ligand neosurfaces with a generalizable deep learning tool. 著者: Anthony Marchand / Stephen Buckley / Arne Schneuing / Martin Pacesa / Maddalena Elia / Pablo Gainza / Evgenia Elizarova / Rebecca M Neeser / Pao-Wan Lee / Luc Reymond / Yangyang Miao / Leo ...著者: Anthony Marchand / Stephen Buckley / Arne Schneuing / Martin Pacesa / Maddalena Elia / Pablo Gainza / Evgenia Elizarova / Rebecca M Neeser / Pao-Wan Lee / Luc Reymond / Yangyang Miao / Leo Scheller / Sandrine Georgeon / Joseph Schmidt / Philippe Schwaller / Sebastian J Maerkl / Michael Bronstein / Bruno E Correia /     要旨: Molecular recognition events between proteins drive biological processes in living systems. However, higher levels of mechanistic regulation have emerged, in which protein-protein interactions are ...Molecular recognition events between proteins drive biological processes in living systems. However, higher levels of mechanistic regulation have emerged, in which protein-protein interactions are conditioned to small molecules. Despite recent advances, computational tools for the design of new chemically induced protein interactions have remained a challenging task for the field. Here we present a computational strategy for the design of proteins that target neosurfaces, that is, surfaces arising from protein-ligand complexes. To develop this strategy, we leveraged a geometric deep learning approach based on learned molecular surface representations and experimentally validated binders against three drug-bound protein complexes: Bcl2-venetoclax, DB3-progesterone and PDF1-actinonin. All binders demonstrated high affinities and accurate specificities, as assessed by mutational and structural characterization. Remarkably, surface fingerprints previously trained only on proteins could be applied to neosurfaces induced by interactions with small molecules, providing a powerful demonstration of generalizability that is uncommon in other deep learning approaches. We anticipate that such designed chemically induced protein interactions will have the potential to expand the sensing repertoire and the assembly of new synthetic pathways in engineered cells for innovative drug-controlled cell-based therapies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_50522.map.gz emd_50522.map.gz | 88.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-50522-v30.xml emd-50522-v30.xml emd-50522.xml emd-50522.xml | 25 KB 25 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_50522_fsc.xml emd_50522_fsc.xml | 12 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_50522.png emd_50522.png | 108.7 KB | ||
| マスクデータ |  emd_50522_msk_1.map emd_50522_msk_1.map | 178 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-50522.cif.gz emd-50522.cif.gz | 7 KB | ||
| その他 |  emd_50522_half_map_1.map.gz emd_50522_half_map_1.map.gz emd_50522_half_map_2.map.gz emd_50522_half_map_2.map.gz | 165.3 MB 165.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-50522 http://ftp.pdbj.org/pub/emdb/structures/EMD-50522 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50522 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50522 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_50522.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_50522.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.658 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_50522_msk_1.map emd_50522_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_50522_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_50522_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Progesterone-bound DB3 Fab in complex with computationally design...
| 全体 | 名称: Progesterone-bound DB3 Fab in complex with computationally designed DBPro1156_2 protein binder |
|---|---|
| 要素 |
|
-超分子 #1: Progesterone-bound DB3 Fab in complex with computationally design...
| 超分子 | 名称: Progesterone-bound DB3 Fab in complex with computationally designed DBPro1156_2 protein binder タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#5 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 107.61566 KDa |
-分子 #1: De novo designed DBPro1156_2 binder
| 分子 | 名称: De novo designed DBPro1156_2 binder / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 8.087193 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: DEKAKTAETL IWQLFGKAMQ QSDPNEAEKL LKKAEELAKK ANDPRLEQVV RQHQVVVRFL VGGSHHHHHH |
-分子 #2: DB3 Fab Heavy chain
| 分子 | 名称: DB3 Fab Heavy chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 25.93093 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: ETGQIQLVQS GPELKKPGET VKISCKASGY AFTNYGVNWV KEAPGKELKW MGWINIYTGE PTYVDDFKGR FAFSLETSAS TAYLEINNL KNEDTATYFC TRGDYVNWYF DVWGAGTTVT VSSASTKGPS VFPLAPSSKS TSGGTAALGC LVKDYFPEPV T VSWNSGAL ...文字列: ETGQIQLVQS GPELKKPGET VKISCKASGY AFTNYGVNWV KEAPGKELKW MGWINIYTGE PTYVDDFKGR FAFSLETSAS TAYLEINNL KNEDTATYFC TRGDYVNWYF DVWGAGTTVT VSSASTKGPS VFPLAPSSKS TSGGTAALGC LVKDYFPEPV T VSWNSGAL TSGVHTFPAV LQSSGLYSLS SVVTVPSSSL GTQTYICNVN HKPSNTKVDK KVEPKSCDKT HTGTKHHHHH H |
-分子 #3: DB3 Fab Light Chain
| 分子 | 名称: DB3 Fab Light Chain / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 24.332191 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: ETGDVVMTQI PLSLPVSLGE QASISCRSSQ SLIHSNGNTY LHWYLQKPGQ SPKLLMYKVS NRFYGVPDRF SGSGSGTDFT LKISRVEAE DLGIYFCSQS SHVPPTFGGG TKLEIKRTVA APSVFIFPPS DEQLKSGTAS VVCLLNNFYP REAKVQWKVD N ALQSGNSQ ...文字列: ETGDVVMTQI PLSLPVSLGE QASISCRSSQ SLIHSNGNTY LHWYLQKPGQ SPKLLMYKVS NRFYGVPDRF SGSGSGTDFT LKISRVEAE DLGIYFCSQS SHVPPTFGGG TKLEIKRTVA APSVFIFPPS DEQLKSGTAS VVCLLNNFYP REAKVQWKVD N ALQSGNSQ ESVTEQDSKD STYSLSSTLT LSKADYEKHK VYACEVTHQG LSSPVTKSFN RGEC |
-分子 #4: Anti-kappa Fab Light Chain
| 分子 | 名称: Anti-kappa Fab Light Chain / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 24.11568 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: ETGSIVMTQT PKFLFVSAGD RVTITCKASQ SVSNDVEWYQ QKPGQSPKLM IYFASKRYNG VPDRFTGSGF GTEFTFTIST VQAEDLAVY FCQQDYSSPW TFGGGTKLEI KRADAAPTVS IFPPSSEQLT SGGASVVCFL NNFYPKDINV KWKIDGSERQ N GVLNSWTD ...文字列: ETGSIVMTQT PKFLFVSAGD RVTITCKASQ SVSNDVEWYQ QKPGQSPKLM IYFASKRYNG VPDRFTGSGF GTEFTFTIST VQAEDLAVY FCQQDYSSPW TFGGGTKLEI KRADAAPTVS IFPPSSEQLT SGGASVVCFL NNFYPKDINV KWKIDGSERQ N GVLNSWTD QDSKDSTYSM SSTLTLTKDE YERHNSYTCE ATHKTSTSPI VKSFNRGEC |
-分子 #5: Anti-kappa Fab Heavy Chain
| 分子 | 名称: Anti-kappa Fab Heavy Chain / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 25.346602 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: ETGEVKLLES GGGLVQPGRS LRLSCIASGF DFSGYWMTWV RQAPGKGLEW IGDINPDSST INSTPSLKDK VIISRDNAKN TLFLQMSKV RSEDTALYYC AQRGNYVPFP YWGQGTLVTV SAAKTTPPSV YPLAPGSAAQ TNSMVTLGCL VKGYFPEPVT V TWNSGSLS ...文字列: ETGEVKLLES GGGLVQPGRS LRLSCIASGF DFSGYWMTWV RQAPGKGLEW IGDINPDSST INSTPSLKDK VIISRDNAKN TLFLQMSKV RSEDTALYYC AQRGNYVPFP YWGQGTLVTV SAAKTTPPSV YPLAPGSAAQ TNSMVTLGCL VKGYFPEPVT V TWNSGSLS SGVHTFPAVL QSDLYTLSSS VTVPSSTWPS ETVTCNVAHP ASSTKVDKKI VPRDCGCKGT KHHHHHH |
-分子 #6: PROGESTERONE
| 分子 | 名称: PROGESTERONE / タイプ: ligand / ID: 6 / コピー数: 1 / 式: STR |
|---|---|
| 分子量 | 理論値: 314.462 Da |
| Chemical component information | 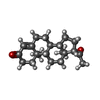 ChemComp-STR: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3.9 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: Quantifoil / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 283.15 K / 装置: FEI VITROBOT MARK IV |
| 詳細 | DB3 Fab and anti-Kappa Fab were pre-purified on SEC, while DBPro1156_2 de novo binder was added in 3-fold excess before grid freezing |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 温度 | 最低: 186.0 K / 最高: 192.0 K |
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー






 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)













































