[日本語] English
 万見
万見- EMDB-50222: Human DNA polymerase epsilon bound to DNA and PCNA (open conformation) -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human DNA polymerase epsilon bound to DNA and PCNA (open conformation) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | DNA / polymerase / epsilon / PCNA / leading strand / human / replication / replisome / proofreading | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報DNA replication initiation / epsilon DNA polymerase complex / positive regulation of deoxyribonuclease activity / dinucleotide insertion or deletion binding / PCNA-p21 complex / mitotic telomere maintenance via semi-conservative replication / purine-specific mismatch base pair DNA N-glycosylase activity / nuclear lamina / MutLalpha complex binding / positive regulation of DNA-directed DNA polymerase activity ...DNA replication initiation / epsilon DNA polymerase complex / positive regulation of deoxyribonuclease activity / dinucleotide insertion or deletion binding / PCNA-p21 complex / mitotic telomere maintenance via semi-conservative replication / purine-specific mismatch base pair DNA N-glycosylase activity / nuclear lamina / MutLalpha complex binding / positive regulation of DNA-directed DNA polymerase activity / Polymerase switching / Telomere C-strand (Lagging Strand) Synthesis / Processive synthesis on the lagging strand / PCNA complex / single-stranded DNA 3'-5' DNA exonuclease activity / Removal of the Flap Intermediate / Processive synthesis on the C-strand of the telomere / Mismatch repair (MMR) directed by MSH2:MSH3 (MutSbeta) / Polymerase switching on the C-strand of the telomere / Mismatch repair (MMR) directed by MSH2:MSH6 (MutSalpha) / Transcription of E2F targets under negative control by DREAM complex / Removal of the Flap Intermediate from the C-strand / replisome / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エンドデオキシリボヌクレアーゼ / response to L-glutamate / nucleotide-excision repair, DNA gap filling / DNA replication proofreading / histone acetyltransferase binding / DNA synthesis involved in DNA repair / DNA polymerase processivity factor activity / G1/S-Specific Transcription / response to dexamethasone / leading strand elongation / replication fork processing / nuclear replication fork / SUMOylation of DNA replication proteins / estrous cycle / Activation of the pre-replicative complex / PCNA-Dependent Long Patch Base Excision Repair / embryonic organ development / mismatch repair / translesion synthesis / cyclin-dependent protein kinase holoenzyme complex / response to cadmium ion / DNA polymerase binding / epithelial cell differentiation / positive regulation of DNA repair / Translesion synthesis by REV1 / Translesion synthesis by POLK / Translesion synthesis by POLI / Gap-filling DNA repair synthesis and ligation in GG-NER / base-excision repair, gap-filling / TP53 Regulates Transcription of Genes Involved in G2 Cell Cycle Arrest / positive regulation of DNA replication / replication fork / male germ cell nucleus / liver regeneration / nuclear estrogen receptor binding / Recognition of DNA damage by PCNA-containing replication complex / Termination of translesion DNA synthesis / Translesion Synthesis by POLH / HDR through Homologous Recombination (HRR) / Dual Incision in GG-NER / DNA-templated DNA replication / receptor tyrosine kinase binding / cellular response to hydrogen peroxide / Dual incision in TC-NER / G1/S transition of mitotic cell cycle / Gap-filling DNA repair synthesis and ligation in TC-NER / cellular response to UV / cellular response to xenobiotic stimulus / E3 ubiquitin ligases ubiquitinate target proteins / response to estradiol / heart development / mitotic cell cycle / 4 iron, 4 sulfur cluster binding / DNA replication / damaged DNA binding / chromosome, telomeric region / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity / nuclear body / nucleotide binding / centrosome / chromatin binding / chromatin / protein-containing complex binding / enzyme binding / negative regulation of transcription by RNA polymerase II / DNA binding / zinc ion binding / extracellular exosome / nucleoplasm / identical protein binding / nucleus / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / synthetic construct (人工物) Homo sapiens (ヒト) / synthetic construct (人工物) | |||||||||
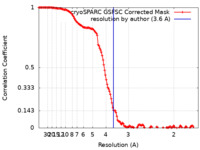
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | |||||||||
 データ登録者 データ登録者 | Roske JJ / Yeeles JTP | |||||||||
| 資金援助 |  英国, 1件 英国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat.Struct.Mol.Biol. / 年: 2024 ジャーナル: Nat.Struct.Mol.Biol. / 年: 2024タイトル: Structural basis for processive daughter-strand synthesis and proofreading by the human leading-strand DNA polymerase Pol epsilon. 著者: Roske JJ / Yeeles JTP | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_50222.map.gz emd_50222.map.gz | 223.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-50222-v30.xml emd-50222-v30.xml emd-50222.xml emd-50222.xml | 21.8 KB 21.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_50222_fsc.xml emd_50222_fsc.xml | 14.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_50222.png emd_50222.png | 131.6 KB | ||
| マスクデータ |  emd_50222_msk_1.map emd_50222_msk_1.map emd_50222_msk_2.map emd_50222_msk_2.map | 236.9 MB 236.9 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-50222.cif.gz emd-50222.cif.gz | 7 KB | ||
| その他 |  emd_50222_additional_1.map.gz emd_50222_additional_1.map.gz emd_50222_half_map_1.map.gz emd_50222_half_map_1.map.gz emd_50222_half_map_2.map.gz emd_50222_half_map_2.map.gz | 223.6 MB 219.8 MB 219.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-50222 http://ftp.pdbj.org/pub/emdb/structures/EMD-50222 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50222 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50222 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_50222_validation.pdf.gz emd_50222_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_50222_full_validation.pdf.gz emd_50222_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_50222_validation.xml.gz emd_50222_validation.xml.gz | 21.3 KB | 表示 | |
| CIF形式データ |  emd_50222_validation.cif.gz emd_50222_validation.cif.gz | 26.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50222 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50222 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50222 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50222 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9f6dMC  9f6eC  9f6fC  9f6iC  9f6jC  9f6kC  9f6lC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_50222.map.gz / 形式: CCP4 / 大きさ: 236.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_50222.map.gz / 形式: CCP4 / 大きさ: 236.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.84065 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_50222_msk_1.map emd_50222_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
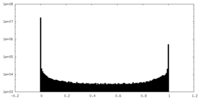
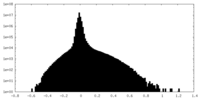
| 密度ヒストグラム |
-マスク #2
| ファイル |  emd_50222_msk_2.map emd_50222_msk_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
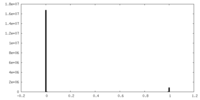
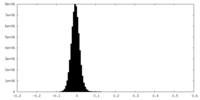
| 密度ヒストグラム |
-追加マップ: Map from focussed refinement with Mask around Polymerase...
| ファイル | emd_50222_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map from focussed refinement with Mask around Polymerase epsilon catalytic domain | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
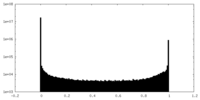
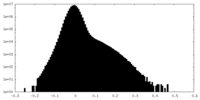
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_50222_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
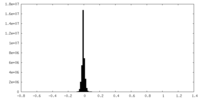
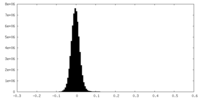
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_50222_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Quaternary Complex of human leading strand polymerase epsilon, Pr...
+超分子 #1: Quaternary Complex of human leading strand polymerase epsilon, Pr...
+超分子 #2: DNA polymerase epsilon catalytic subunit A
+超分子 #3: Proliferating cell nuclear antigen
+超分子 #4: DNA
+分子 #1: DNA polymerase epsilon catalytic subunit A
+分子 #2: Proliferating cell nuclear antigen
+分子 #3: DNA nascent strand
+分子 #4: DNA template strand
+分子 #5: IRON/SULFUR CLUSTER
+分子 #6: 2',3'-dideoxyadenosine triphosphate
+分子 #7: MAGNESIUM ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 40.08 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)


















































 Trichoplusia ni (イラクサキンウワバ)
Trichoplusia ni (イラクサキンウワバ)