+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4339 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Electron cryo-microscopy structure of the canonical TRPC4 ion channel | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報store-operated calcium channel activity / cation channel complex / inositol 1,4,5 trisphosphate binding / monoatomic cation transport / monoatomic cation channel activity / regulation of cytosolic calcium ion concentration / calcium ion transmembrane transport / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | |||||||||
 データ登録者 データ登録者 | Vinayagam D / Mager T / Apelbaum A / Bothe A / Merino F / Hofnagel O / Gatsogiannis C / Raunser S | |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2018 ジャーナル: Elife / 年: 2018タイトル: Electron cryo-microscopy structure of the canonical TRPC4 ion channel. 著者: Deivanayagabarathy Vinayagam / Thomas Mager / Amir Apelbaum / Arne Bothe / Felipe Merino / Oliver Hofnagel / Christos Gatsogiannis / Stefan Raunser /  要旨: Canonical transient receptor channels (TRPC) are non-selective cation channels. They are involved in receptor-operated Ca signaling and have been proposed to act as store-operated channels (SOC). ...Canonical transient receptor channels (TRPC) are non-selective cation channels. They are involved in receptor-operated Ca signaling and have been proposed to act as store-operated channels (SOC). Their malfunction is related to cardiomyopathies and their modulation by small molecules has been shown to be effective against renal cancer cells. The molecular mechanism underlying the complex activation and regulation is poorly understood. Here, we report the electron cryo-microscopy structure of zebrafish TRPC4 in its unliganded (apo), closed state at an overall resolution of 3.6 Å. The structure reveals the molecular architecture of the cation conducting pore, including the selectivity filter and lower gate. The cytoplasmic domain contains two key hubs that have been shown to interact with modulating proteins. Structural comparisons with other TRP channels give novel insights into the general architecture and domain organization of this superfamily of channels and help to understand their function and pharmacology. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4339.map.gz emd_4339.map.gz | 4.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4339-v30.xml emd-4339-v30.xml emd-4339.xml emd-4339.xml | 16.1 KB 16.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_4339.png emd_4339.png | 90.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4339 http://ftp.pdbj.org/pub/emdb/structures/EMD-4339 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4339 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4339 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_4339_validation.pdf.gz emd_4339_validation.pdf.gz | 238.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_4339_full_validation.pdf.gz emd_4339_full_validation.pdf.gz | 237.4 KB | 表示 | |
| XML形式データ |  emd_4339_validation.xml.gz emd_4339_validation.xml.gz | 5.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4339 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4339 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4339 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4339 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4339.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4339.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.09 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : TRPC4
| 全体 | 名称: TRPC4 |
|---|---|
| 要素 |
|
-超分子 #1: TRPC4
| 超分子 | 名称: TRPC4 / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1 / 詳細: Membrane protein |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 432 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換細胞: HEK293 GnTI- / 組換プラスミド: pEG BacMam Homo sapiens (ヒト) / 組換細胞: HEK293 GnTI- / 組換プラスミド: pEG BacMam |
-分子 #1: Transient receptor potential cation channel subfamily c member 4a
| 分子 | 名称: Transient receptor potential cation channel subfamily c member 4a タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 105.9345 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GSQLYFRRTD NSSYRDRIPL RIVRAESELS TQEKSYLSAV EKGDYASVKL ALEEAEIYFK ININCIDPLG RTALLIAIEN ENLEIIELL LSFNVYVGDA LLHAIRKEVV GAVELLLNHK KPSGEKQVPP ILLDKQFSDF TPDITPIILA AHTNNYEIIK M LVQKGVSV ...文字列: GSQLYFRRTD NSSYRDRIPL RIVRAESELS TQEKSYLSAV EKGDYASVKL ALEEAEIYFK ININCIDPLG RTALLIAIEN ENLEIIELL LSFNVYVGDA LLHAIRKEVV GAVELLLNHK KPSGEKQVPP ILLDKQFSDF TPDITPIILA AHTNNYEIIK M LVQKGVSV PQPHEVRCNC VECVSSSDVD SLRHSRSRLN IYKALASPSL IALSSEDPFL TAFQLSWELQ ELSKVENEFK AE YEELSHQ CKHFAKDLLD QTRSSRELEL ILNFRDDMNL LQDEANNELA RLKLAIKYRQ KEFVAQPNCQ QLLASRWYDE FPG WRRRHW AGKLITCVFI GLMFPLLSLC YLVAPKSRYG LFIRKPFIKF ICHTASYLTF LFLLLLASQH IVSNNPDRQG PKPT TVEWM ILPWVLGFIW TEIKQMWDGG FQDYIHDWWN LMDFVMNSLY LATISLKIVA YVKYSGCKPR DTWEMWHPTL VAEAV FAIA NIFSSLRLIS LFTANSHLGP LQISLGRMLL DILKFLFIYC LVLLAFANGL NQLYFYYENS EGMTCKGIRC ERQNNA FST LFETLQSLFW SIFGLISLYV TNVKADHKFT EFVGATMFGT YNVISLVVLL NMLIAMMNNS YQHIADHADI EWKFART KL WMSYFEEGGT LPPPFNIIPS PKSICYLITW IKVHVFKRRS KRTETFGTLG RRAAENVRLN HQYQEVLRNL VKRYVAAM I RDAKTEEGLT EENFKELKQD ISSFRYEVIG MMKGNRKSTR ANKSDTSASD VSHPEGSLQY SSALKQNSKL HLYDVTTAL QQQNSEEAKA SLGCLANGSA VVLTEPILKD KARSDFPKDF TDFGLFPKKQ NPNKIYSLAE EATESDPDIL DWGKEDKPLA GKVEQDVNE SKCLMEEDER VLEEQEMEHI ASSHEHLEVL FQ |
-分子 #2: CHOLESTEROL HEMISUCCINATE
| 分子 | 名称: CHOLESTEROL HEMISUCCINATE / タイプ: ligand / ID: 2 / コピー数: 4 / 式: Y01 |
|---|---|
| 分子量 | 理論値: 486.726 Da |
| Chemical component information |  ChemComp-Y01: |
-分子 #3: (2R)-3-(phosphonooxy)propane-1,2-diyl dihexanoate
| 分子 | 名称: (2R)-3-(phosphonooxy)propane-1,2-diyl dihexanoate / タイプ: ligand / ID: 3 / コピー数: 4 / 式: 44E |
|---|---|
| 分子量 | 理論値: 368.36 Da |
| Chemical component information | 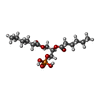 ChemComp-44E: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.25 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 構成要素 - 名称: PBS |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK III |
| 詳細 | The sample was monodisperse |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | 球面収差補正装置: CS corrected Microscope |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 撮影したグリッド数: 4 / 実像数: 3890 / 平均露光時間: 12.0 sec. / 平均電子線量: 70.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 最大 デフォーカス(補正後): 2.931 µm / 最小 デフォーカス(補正後): 0.844 µm / 照射モード: OTHER / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




















