+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the target ssDNA-bound SIR2-APAZ/Ago-gRNA quaternary complex | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | a protein / ANTIVIRAL PROTEIN | |||||||||
| 機能・相同性 | SIR2-like domain / SIR2-like domain / DHS-like NAD/FAD-binding domain superfamily / Ribonuclease H superfamily / nucleic acid binding / Ribonuclease H-like superfamily / Piwi domain protein / Sir2 superfamily protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) | |||||||||
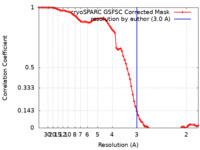
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.0 Å | |||||||||
 データ登録者 データ登録者 | Zhang H / Li Z / Yu GM / Li XZ / Wang XS | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Res / 年: 2023 ジャーナル: Cell Res / 年: 2023タイトル: Structural insights into mechanisms of Argonaute protein-associated NADase activation in bacterial immunity. 著者: Xiaoshen Wang / Xuzichao Li / Guimei Yu / Lingling Zhang / Chendi Zhang / Yong Wang / Fumeng Liao / Yanan Wen / Hang Yin / Xiang Liu / Yong Wei / Zhuang Li / Zengqin Deng / Heng Zhang /  要旨: Nicotinamide adenine dinucleotide (NAD) is a central metabolite in cellular processes. Depletion of NAD has been demonstrated to be a prevalent theme in both prokaryotic and eukaryotic immune ...Nicotinamide adenine dinucleotide (NAD) is a central metabolite in cellular processes. Depletion of NAD has been demonstrated to be a prevalent theme in both prokaryotic and eukaryotic immune responses. Short prokaryotic Argonaute proteins (Agos) are associated with NADase domain-containing proteins (TIR-APAZ or SIR2-APAZ) encoded in the same operon. They confer immunity against mobile genetic elements, such as bacteriophages and plasmids, by inducing NAD depletion upon recognition of target nucleic acids. However, the molecular mechanisms underlying the activation of such prokaryotic NADase/Ago immune systems remain unknown. Here, we report multiple cryo-EM structures of NADase/Ago complexes from two distinct systems (TIR-APAZ/Ago and SIR2-APAZ/Ago). Target DNA binding triggers tetramerization of the TIR-APAZ/Ago complex by a cooperative self-assembly mechanism, while the heterodimeric SIR2-APAZ/Ago complex does not assemble into higher-order oligomers upon target DNA binding. However, the NADase activities of these two systems are unleashed via a similar closed-to-open transition of the catalytic pocket, albeit by different mechanisms. Furthermore, a functionally conserved sensor loop is employed to inspect the guide RNA-target DNA base pairing and facilitate the conformational rearrangement of Ago proteins required for the activation of these two systems. Overall, our study reveals the mechanistic diversity and similarity of Ago protein-associated NADase systems in prokaryotic immune response. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_35592.map.gz emd_35592.map.gz | 49.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-35592-v30.xml emd-35592-v30.xml emd-35592.xml emd-35592.xml | 17.5 KB 17.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_35592_fsc.xml emd_35592_fsc.xml | 7.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_35592.png emd_35592.png | 53.6 KB | ||
| その他 |  emd_35592_half_map_1.map.gz emd_35592_half_map_1.map.gz emd_35592_half_map_2.map.gz emd_35592_half_map_2.map.gz | 48.9 MB 48.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-35592 http://ftp.pdbj.org/pub/emdb/structures/EMD-35592 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35592 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35592 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_35592_validation.pdf.gz emd_35592_validation.pdf.gz | 784.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_35592_full_validation.pdf.gz emd_35592_full_validation.pdf.gz | 784.5 KB | 表示 | |
| XML形式データ |  emd_35592_validation.xml.gz emd_35592_validation.xml.gz | 15.8 KB | 表示 | |
| CIF形式データ |  emd_35592_validation.cif.gz emd_35592_validation.cif.gz | 20.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35592 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35592 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35592 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35592 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_35592.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_35592.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.9066 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_35592_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_35592_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cryo-EM structure of the target ssDNA-bound SIR2-APAZ/Ago-gRNA qu...
| 全体 | 名称: Cryo-EM structure of the target ssDNA-bound SIR2-APAZ/Ago-gRNA quaternary complex |
|---|---|
| 要素 |
|
-超分子 #1: Cryo-EM structure of the target ssDNA-bound SIR2-APAZ/Ago-gRNA qu...
| 超分子 | 名称: Cryo-EM structure of the target ssDNA-bound SIR2-APAZ/Ago-gRNA quaternary complex タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|---|
| 由来(天然) | 生物種:  Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) |
-分子 #1: Sir2 superfamily protein
| 分子 | 名称: Sir2 superfamily protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) |
| 分子量 | 理論値: 66.645922 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MDVLTDNEFY QHYLQNSQHM MWFLGAGTSR SAGLPTASDI IWDLKHRYYC LHENQDYQKH DINNHAIKSK IQSYMDSKGF PLQWSPEEY SFYFELVFRD DYEAQRKYLL EALASRKVSL NIGHRVLAAL LEMNQTKVVF TTNFDDVIET AFSDISGKHL S VYHLEGSY ...文字列: MDVLTDNEFY QHYLQNSQHM MWFLGAGTSR SAGLPTASDI IWDLKHRYYC LHENQDYQKH DINNHAIKSK IQSYMDSKGF PLQWSPEEY SFYFELVFRD DYEAQRKYLL EALASRKVSL NIGHRVLAAL LEMNQTKVVF TTNFDDVIET AFSDISGKHL S VYHLEGSY AALSALNTEA FPIYAKIHGD FRYQKIKNLT PDLQTNDREI HKCFLAAAIR FGLVVSGYSG RDENVMTMLR AA IDQNNAF PHGLYWTVPS ISKSEPAVQD LITYAQGKGV RAYLVETGTF DEMLSKIWRQ VKDKPAAIDA KVRTARVCPV SIP LPGPGK SFPALRTNAL PVVTQSIRCG VVTLASPITF SELKERISQK SPKALLTYTE KVLFLGGEPE IRKIFSNDEI NSIG QYYID EIAQSVAAST FLKSFVEEAI LTALLREKPI LHRVRHRTHY AVIPNASAKD DRFLDLRKAV GFKGDLGYIT GNVTN AKEL SWAEAVSIRL EERGGKLWIM LKPEIWIKPL DRREEATDFI RSRRRYRFNQ CSYQILDAWI KILFGSIGGG GTVNIS CFP DAEFKAEFEI GTRTAFSLGV GYGR UniProtKB: Sir2 superfamily protein |
-分子 #2: Piwi domain protein
| 分子 | 名称: Piwi domain protein / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) |
| 分子量 | 理論値: 53.325566 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MADNLSQLAA HSTIPEPLLL FKDNRTDTHP LRGLSQYGPY SACFNLPGQV RLAYLAPTEH MRKLDAIVRE LQNPATPKEA TNYYVEYGG FEKVFKVPLV MPQEHLRCLA LDECHGVAAN GNGLALADKI VQSMSGLFRQ KHAFDVLLVY LPASWKKCFE Y DGFDLHDR ...文字列: MADNLSQLAA HSTIPEPLLL FKDNRTDTHP LRGLSQYGPY SACFNLPGQV RLAYLAPTEH MRKLDAIVRE LQNPATPKEA TNYYVEYGG FEKVFKVPLV MPQEHLRCLA LDECHGVAAN GNGLALADKI VQSMSGLFRQ KHAFDVLLVY LPASWKKCFE Y DGFDLHDR IKAKVAPLNL PIQIINDTAL TRQCRANVMW GVSVALYAKA GGIPWKLADW DKDEAYIGLS YAIKKNAEGQ EY TTCCSQV FDPDGTGFEF VAYDTREFIT DRKGNPYLSY QEMQSVLSKS LHLYQSSHNG RMPRKIFIHK TTHFTEDEIQ GAF DSFSSS TEIELVQIIQ STNWYGLKVD GKKGDKPVAP ASYPVDRGLY QPLTESECLL WTQGSVMGVN QQNPGQPVFK EAAL TPLPN PIMLRRFSGN GGWHATCSSI LALTKVDWNN NTLYKKLPVT LVYSQVFADV VKQTPEIVNE IYDYRFFM UniProtKB: Piwi domain protein |
-分子 #3: RNA (5'-R(P*AP*UP*AP*AP*UP*GP*GP*UP*UP*UP*CP*UP*UP*AP*GP*AP*CP*GP...
| 分子 | 名称: RNA (5'-R(P*AP*UP*AP*AP*UP*GP*GP*UP*UP*UP*CP*UP*UP*AP*GP*AP*CP*GP*UP*CP*GP*UP*UP*U)-3') タイプ: rna / ID: 3 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) |
| 分子量 | 理論値: 7.610471 KDa |
| 配列 | 文字列: AUAAUGGUUU CUUAGACGUC GUUU |
-分子 #4: DNA (5'-D(P*AP*AP*CP*GP*AP*CP*GP*TP*CP*TP*AP*AP*GP*AP*AP*AP*CP*CP...
| 分子 | 名称: DNA (5'-D(P*AP*AP*CP*GP*AP*CP*GP*TP*CP*TP*AP*AP*GP*AP*AP*AP*CP*CP*AP*TP*TP*AP*A)-3') タイプ: dna / ID: 4 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) Geobacter sulfurreducens (strain ATCC 51573 / DSM 12127 / PCA) (バクテリア) |
| 分子量 | 理論値: 7.050615 KDa |
| 配列 | 文字列: (DA)(DA)(DC)(DG)(DA)(DC)(DG)(DT)(DC)(DT) (DA)(DA)(DG)(DA)(DA)(DA)(DC)(DC)(DA)(DT) (DT)(DA)(DA) |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 1 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)