+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 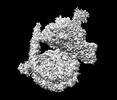 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Rpd3S bound to the nucleosome | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | HDAC / TRANSCRIPTION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Snt2C complex / negative regulation of reciprocal meiotic recombination / negative regulation of silent mating-type cassette heterochromatin formation / protein localization to nucleolar rDNA repeats / negative regulation of rDNA heterochromatin formation / Rpd3S complex / Rpd3L complex / Rpd3L-Expanded complex / rDNA chromatin condensation / nucleophagy ...Snt2C complex / negative regulation of reciprocal meiotic recombination / negative regulation of silent mating-type cassette heterochromatin formation / protein localization to nucleolar rDNA repeats / negative regulation of rDNA heterochromatin formation / Rpd3S complex / Rpd3L complex / Rpd3L-Expanded complex / rDNA chromatin condensation / nucleophagy / HDACs deacetylate histones / NuRD complex / histone deacetylase / SUMOylation of chromatin organization proteins / regulation of DNA-templated DNA replication initiation / negative regulation of transcription by RNA polymerase I / histone deacetylase activity / Sin3-type complex / NuA4 histone acetyltransferase complex / Estrogen-dependent gene expression / histone deacetylase complex / positive regulation of macroautophagy / nuclear periphery / transcription elongation by RNA polymerase II / double-strand break repair via nonhomologous end joining / structural constituent of chromatin / transcription corepressor activity / nucleosome / nucleosome assembly / response to oxidative stress / transcription coactivator activity / chromatin remodeling / cell cycle / protein heterodimerization activity / cell division / DNA repair / regulation of DNA-templated transcription / chromatin / regulation of transcription by RNA polymerase II / negative regulation of transcription by RNA polymerase II / positive regulation of transcription by RNA polymerase II / DNA binding / identical protein binding / nucleus / metal ion binding / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.72 Å | |||||||||
 データ登録者 データ登録者 | Zhang Y / Gang C | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Res / 年: 2023 ジャーナル: Cell Res / 年: 2023タイトル: Structural basis for nucleosome binding and catalysis by the yeast Rpd3S/HDAC holoenzyme. 著者: Yueyue Zhang / Mengxue Xu / Po Wang / Jiahui Zhou / Guangxian Wang / Shuailong Han / Gang Cai / Xuejuan Wang /  | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_35455.map.gz emd_35455.map.gz | 136.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-35455-v30.xml emd-35455-v30.xml emd-35455.xml emd-35455.xml | 26 KB 26 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_35455.png emd_35455.png | 85.8 KB | ||
| Filedesc metadata |  emd-35455.cif.gz emd-35455.cif.gz | 8.7 KB | ||
| その他 |  emd_35455_half_map_1.map.gz emd_35455_half_map_1.map.gz emd_35455_half_map_2.map.gz emd_35455_half_map_2.map.gz | 134.4 MB 134.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-35455 http://ftp.pdbj.org/pub/emdb/structures/EMD-35455 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35455 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35455 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_35455_validation.pdf.gz emd_35455_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_35455_full_validation.pdf.gz emd_35455_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_35455_validation.xml.gz emd_35455_validation.xml.gz | 14.3 KB | 表示 | |
| CIF形式データ |  emd_35455_validation.cif.gz emd_35455_validation.cif.gz | 17 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35455 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35455 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35455 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35455 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8ihtMC  8ihmC  8ihnC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_35455.map.gz / 形式: CCP4 / 大きさ: 144.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_35455.map.gz / 形式: CCP4 / 大きさ: 144.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.07 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_35455_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_35455_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Eaf3 CHD domain bound to the nucleosome
+超分子 #1: Eaf3 CHD domain bound to the nucleosome
+分子 #1: Histone H3
+分子 #2: Histone H4
+分子 #3: Histone H2A
+分子 #4: Histone H2B
+分子 #7: RCO1 isoform 1
+分子 #8: Chromatin modification-related protein EAF3
+分子 #9: Transcriptional regulatory protein SIN3
+分子 #10: Histone deacetylase RPD3
+分子 #5: DNA (164-MER)
+分子 #6: DNA (165-MER)
+分子 #11: ZINC ION
+分子 #12: CALCIUM ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.6 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 53.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD 最大 デフォーカス(公称値): 2.8000000000000003 µm 最小 デフォーカス(公称値): 1.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.72 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 107252 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー














 Z
Z Y
Y X
X