+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of heptameric RdrA ring in RNA-loading state | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Cryoelectron microscopy / adenosine triphosphatase / IMMUNE SYSTEM | |||||||||
| 機能・相同性 | P-loop containing nucleoside triphosphate hydrolase / Archaeal ATPase 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.76 Å | |||||||||
 データ登録者 データ登録者 | Gao Y | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2023 ジャーナル: Cell / 年: 2023タイトル: Molecular basis of RADAR anti-phage supramolecular assemblies. 著者: Yina Gao / Xiu Luo / Peipei Li / Zhaolong Li / Feng Ye / Songqing Liu / Pu Gao /  要旨: Adenosine-to-inosine RNA editing has been proposed to be involved in a bacterial anti-phage defense system called RADAR. RADAR contains an adenosine triphosphatase (RdrA) and an adenosine deaminase ...Adenosine-to-inosine RNA editing has been proposed to be involved in a bacterial anti-phage defense system called RADAR. RADAR contains an adenosine triphosphatase (RdrA) and an adenosine deaminase (RdrB). Here, we report cryo-EM structures of RdrA, RdrB, and currently identified RdrA-RdrB complexes in the presence or absence of RNA and ATP. RdrB assembles into a dodecameric cage with catalytic pockets facing outward, while RdrA adopts both autoinhibited tetradecameric and activation-competent heptameric rings. Structural and functional data suggest a model in which RNA is loaded through the bottom section of the RdrA ring and translocated along its inner channel, a process likely coupled with ATP-binding status. Intriguingly, up to twelve RdrA rings can dock one RdrB cage with precise alignments between deaminase catalytic pockets and RNA-translocation channels, indicative of enzymatic coupling of RNA translocation and deamination. Our data uncover an interesting mechanism of enzymatic coupling and anti-phage defense through supramolecular assemblies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_34965.map.gz emd_34965.map.gz | 116.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-34965-v30.xml emd-34965-v30.xml emd-34965.xml emd-34965.xml | 14.5 KB 14.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_34965.png emd_34965.png | 75.9 KB | ||
| その他 |  emd_34965_half_map_1.map.gz emd_34965_half_map_1.map.gz emd_34965_half_map_2.map.gz emd_34965_half_map_2.map.gz | 98.2 MB 98.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-34965 http://ftp.pdbj.org/pub/emdb/structures/EMD-34965 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34965 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34965 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_34965_validation.pdf.gz emd_34965_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_34965_full_validation.pdf.gz emd_34965_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_34965_validation.xml.gz emd_34965_validation.xml.gz | 13.6 KB | 表示 | |
| CIF形式データ |  emd_34965_validation.cif.gz emd_34965_validation.cif.gz | 15.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34965 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34965 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34965 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34965 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_34965.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_34965.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.06 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_34965_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
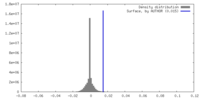
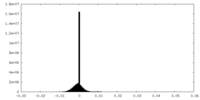
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_34965_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
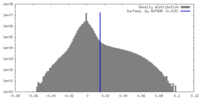
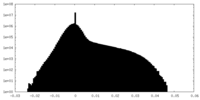
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : RdrA-RNA complex
| 全体 | 名称: RdrA-RNA complex |
|---|---|
| 要素 |
|
-超分子 #1: RdrA-RNA complex
| 超分子 | 名称: RdrA-RNA complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Archaeal ATPase
| 分子 | 名称: Archaeal ATPase / タイプ: protein_or_peptide / ID: 1 / コピー数: 7 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 107.132523 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MTDSVQTETT EGKIIINLFA PNLPGSTKED DLIQKSLRDQ LVESIRNSIA YPDTDKFAGL TRFIDESGRN VFFVDGTRGA GKTTFINSV VKSLNSDQDD VKVNIKCLPT IDPTKLPRHE PILVTVTARL NKMVSDKLKG YWASNDYRKQ KEQWQNHLAQ L QRGLHLLT ...文字列: MTDSVQTETT EGKIIINLFA PNLPGSTKED DLIQKSLRDQ LVESIRNSIA YPDTDKFAGL TRFIDESGRN VFFVDGTRGA GKTTFINSV VKSLNSDQDD VKVNIKCLPT IDPTKLPRHE PILVTVTARL NKMVSDKLKG YWASNDYRKQ KEQWQNHLAQ L QRGLHLLT DKEYKPEYFS DALKLDAQLD YSIGGQDLSE IFEELVKRAC EILDCKAILI TFDDIDTQFD AGWDVLESIR KF FNSRKLV VVATGDLRLY SQLIRGKQYE NYSKTLLEQE KESVRLAERG YMVEHLEQQY LLKLFPVQKR IQLKTMLQLV GEK GKAGKE EIKVKTEPGM QDIDAIDVRQ AIGDAVREGL NLREGSDADM YVNELLKQPV RLLMQVLQDF YTKKYHATSV KLDG KQSRN ERPNELSVPN LLRNALYGSM LSSIYRAGLN YEQHRFGMDS LCKDIFTYVK QDRDFNTGFY LRPQSESEAL RNCSI YLAS QVSENCQGSL SKFLQMLLVG CGSVSIFNQF VTELARAEND REKFEQLISE YVAYMSVGRI ESASHWANRC CAVVAN SPN DEKIGVFLGM VQLNRKSRQH MPGGYKKFNI DTENGLAKAA MASSLSTVAS NNLMDFCSVF NLIGAIADIS ACRCERS AI TNAFNKVIAQ TTCIVPPWSE AAVRAEMKGS SKSADNDAAV LDVDLDPKDD GVIDESQQDD ATEFSDAITK VEQWLKNV N EIEIGIRPSA LLIGKVWSRF YFNLNNVADQ HKTRLYRNAE HGRMASQSNA AKIMRFNVLA FLHAVLVEES LYHSVSDRE YIGEGLRLNP VTSVDEFEKK IKIIGEKLKA DNKTWKNTHP LFFLLISCPI LHPFIFPVGG INCSVKALNK ETSFNKLIDE IVGDKLLSD EEWDYLTKNN DQKTNTRQQI FQNTITSLNS STIVGASYDK DTPARKTKSP LLGDSEEK UniProtKB: Archaeal ATPase |
-分子 #2: RNA (5'-R(P*GP*UP*CP*CP*AP*GP*CP*GP*UP*CP*AP*UP*CP*GP*CP*UP*GP*GP...
| 分子 | 名称: RNA (5'-R(P*GP*UP*CP*CP*AP*GP*CP*GP*UP*CP*AP*UP*CP*GP*CP*UP*GP*GP*AP*C)-3') タイプ: rna / ID: 2 / コピー数: 3 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 6.374831 KDa |
| 配列 | 文字列: GUCCAGCGUC AUCGCUGGAC |
-分子 #3: ADENOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 3 / コピー数: 4 / 式: ATP |
|---|---|
| 分子量 | 理論値: 507.181 Da |
| Chemical component information |  ChemComp-ATP: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.5 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.76 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 158234 |
| 初期 角度割当 | タイプ: PROJECTION MATCHING |
| 最終 角度割当 | タイプ: PROJECTION MATCHING |
 ムービー
ムービー コントローラー
コントローラー


















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)