+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of cryptophyte photosystem I | |||||||||
 マップデータ マップデータ | Cryo-EM structure of cryptophyte photosystem I | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Cryptophyte / Photosystem I / evolution / PHOTOSYNTHESIS | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報thylakoid membrane / photosystem I reaction center / photosystem I / photosystem I / plastid / chlorophyll binding / photosynthetic electron transport in photosystem I / chloroplast thylakoid membrane / photosynthesis / 4 iron, 4 sulfur cluster binding ...thylakoid membrane / photosystem I reaction center / photosystem I / photosystem I / plastid / chlorophyll binding / photosynthetic electron transport in photosystem I / chloroplast thylakoid membrane / photosynthesis / 4 iron, 4 sulfur cluster binding / electron transfer activity / magnesium ion binding / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Chroomonas placoidea (真核生物) Chroomonas placoidea (真核生物) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.71 Å | |||||||||
 データ登録者 データ登録者 | Zhao LS / Zhang YZ / Liu LN / Li K | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Plant Cell / 年: 2023 ジャーナル: Plant Cell / 年: 2023タイトル: Structural basis and evolution of the photosystem I-light-harvesting supercomplex of cryptophyte algae. 著者: Long-Sheng Zhao / Peng Wang / Kang Li / Quan-Bao Zhang / Fei-Yu He / Chun-Yang Li / Hai-Nan Su / Xiu-Lan Chen / Lu-Ning Liu / Yu-Zhong Zhang /   要旨: Cryptophyte plastids originated from a red algal ancestor through secondary endosymbiosis. Cryptophyte photosystem I (PSI) associates with transmembrane alloxanthin-chlorophyll a/c proteins (ACPIs) ...Cryptophyte plastids originated from a red algal ancestor through secondary endosymbiosis. Cryptophyte photosystem I (PSI) associates with transmembrane alloxanthin-chlorophyll a/c proteins (ACPIs) as light-harvesting complexes (LHCs). Here, we report the structure of the photosynthetic PSI-ACPI supercomplex from the cryptophyte Chroomonas placoidea at 2.7-Å resolution obtained by crygenic electron microscopy. Cryptophyte PSI-ACPI represents a unique PSI-LHCI intermediate in the evolution from red algal to diatom PSI-LHCI. The PSI-ACPI supercomplex is composed of a monomeric PSI core containing 14 subunits, 12 of which originated in red algae, 1 diatom PsaR homolog, and an additional peptide. The PSI core is surrounded by 14 ACPI subunits that form 2 antenna layers: an inner layer with 11 ACPIs surrounding the PSI core and an outer layer containing 3 ACPIs. A pigment-binding subunit that is not present in any other previously characterized PSI-LHCI complexes, ACPI-S, mediates the association and energy transfer between the outer and inner ACPIs. The extensive pigment network of PSI-ACPI ensures efficient light harvesting, energy transfer, and dissipation. Overall, the PSI-LHCI structure identified in this study provides a framework for delineating the mechanisms of energy transfer in cryptophyte PSI-LHCI and for understanding the evolution of photosynthesis in the red lineage, which occurred via secondary endosymbiosis. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_33683.map.gz emd_33683.map.gz | 181.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-33683-v30.xml emd-33683-v30.xml emd-33683.xml emd-33683.xml | 43.6 KB 43.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_33683.png emd_33683.png | 207 KB | ||
| その他 |  emd_33683_half_map_1.map.gz emd_33683_half_map_1.map.gz emd_33683_half_map_2.map.gz emd_33683_half_map_2.map.gz | 186.4 MB 186.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-33683 http://ftp.pdbj.org/pub/emdb/structures/EMD-33683 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33683 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33683 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_33683_validation.pdf.gz emd_33683_validation.pdf.gz | 916 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_33683_full_validation.pdf.gz emd_33683_full_validation.pdf.gz | 915.5 KB | 表示 | |
| XML形式データ |  emd_33683_validation.xml.gz emd_33683_validation.xml.gz | 16 KB | 表示 | |
| CIF形式データ |  emd_33683_validation.cif.gz emd_33683_validation.cif.gz | 19 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33683 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33683 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33683 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33683 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7y8aMC  7y7bC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_33683.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_33683.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM structure of cryptophyte photosystem I | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.06 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: Cryo-EM structure of cryptophyte photosystem I
| ファイル | emd_33683_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM structure of cryptophyte photosystem I | ||||||||||||
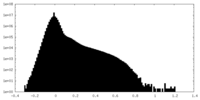
| 投影像・断面図 |
| ||||||||||||
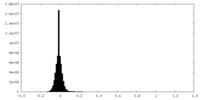
| 密度ヒストグラム |
-ハーフマップ: Cryo-EM structure of cryptophyte photosystem I
| ファイル | emd_33683_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM structure of cryptophyte photosystem I | ||||||||||||
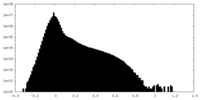
| 投影像・断面図 |
| ||||||||||||
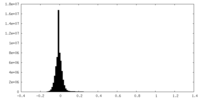
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : photosystem I of cryptophyte
+超分子 #1: photosystem I of cryptophyte
+分子 #1: ACPI-1
+分子 #2: ACPI-2
+分子 #3: ACPI-3
+分子 #4: ACPI-4
+分子 #5: ACPI-5
+分子 #6: ACPI-6
+分子 #7: ACPI-7
+分子 #8: ACPI-8
+分子 #9: ACPI-12
+分子 #10: Photosystem I P700 chlorophyll a apoprotein A1
+分子 #11: Photosystem I P700 chlorophyll a apoprotein A2
+分子 #12: Photosystem I iron-sulfur center
+分子 #13: Photosystem I reaction center subunit II
+分子 #14: Photosystem I reaction center subunit IV
+分子 #15: Photosystem I reaction center subunit III
+分子 #16: Photosystem I reaction center subunit VIII
+分子 #17: Photosystem I reaction center subunit IX
+分子 #18: Photosystem I reaction center subunit PsaK
+分子 #19: Photosystem I reaction center subunit XI
+分子 #20: Photosystem I reaction center subunit XII
+分子 #21: PsaO
+分子 #22: PsaR
+分子 #23: Unk1
+分子 #24: ACPI-S
+分子 #25: ACPI-13
+分子 #26: ACPI-14
+分子 #27: CHLOROPHYLL A
+分子 #28: Chlorophyll c2
+分子 #29: (1~{R})-3,5,5-trimethyl-4-[(3~{E},5~{E},7~{E},9~{E},11~{E},13~{E}...
+分子 #30: (1~{R})-3,5,5-trimethyl-4-[(3~{E},5~{E},7~{E},9~{E},11~{E},13~{E}...
+分子 #31: (1~{R})-3,5,5-trimethyl-4-[(3~{E},5~{E},7~{E},9~{E},11~{E},13~{E}...
+分子 #32: 1,2-DISTEAROYL-MONOGALACTOSYL-DIGLYCERIDE
+分子 #33: 1,2-DIPALMITOYL-PHOSPHATIDYL-GLYCEROLE
+分子 #34: 1,2-DI-O-ACYL-3-O-[6-DEOXY-6-SULFO-ALPHA-D-GLUCOPYRANOSYL]-SN-GLYCEROL
+分子 #35: (6'R,11cis,11'cis,13cis,15cis)-4',5'-didehydro-5',6'-dihydro-beta...
+分子 #36: DODECYL-ALPHA-D-MALTOSIDE
+分子 #37: IRON/SULFUR CLUSTER
+分子 #38: PHYLLOQUINONE
+分子 #39: DIGALACTOSYL DIACYL GLYCEROL (DGDG)
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 6.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.71 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 118810 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー













 Z
Z Y
Y X
X