+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of type III-E CRISPR gRAMP-crRNA complex bound to non-self RNA target | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Nuclease / STRUCTURAL PROTEIN-RNA COMPLEX | |||||||||
| 機能・相同性 | : / CRISPR type III-associated protein / RAMP superfamily / defense response to virus / RAMP superfamily protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.54 Å | |||||||||
 データ登録者 データ登録者 | Zhang JT / Cui N / Huang HD / Jia N | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2022 ジャーナル: Nat Commun / 年: 2022タイトル: Structural basis for the non-self RNA-activated protease activity of the type III-E CRISPR nuclease-protease Craspase. 著者: Ning Cui / Jun-Tao Zhang / Zhuolin Li / Xiao-Yu Liu / Chongyuan Wang / Hongda Huang / Ning Jia /  要旨: The RNA-targeting type III-E CRISPR-gRAMP effector interacts with a caspase-like protease TPR-CHAT to form the CRISPR-guided caspase complex (Craspase), but their functional mechanism is unknown. ...The RNA-targeting type III-E CRISPR-gRAMP effector interacts with a caspase-like protease TPR-CHAT to form the CRISPR-guided caspase complex (Craspase), but their functional mechanism is unknown. Here, we report cryo-EM structures of the type III-E gRAMP and gRAMP-TPR-CHAT complexes, before and after either self or non-self RNA target binding, and elucidate the mechanisms underlying RNA-targeting and non-self RNA-induced protease activation. The associated TPR-CHAT adopted a distinct conformation upon self versus non-self RNA target binding, with nucleotides at positions -1 and -2 of the CRISPR-derived RNA (crRNA) serving as a sensor. Only binding of the non-self RNA target activated the TPR-CHAT protease, leading to cleavage of Csx30 protein. Furthermore, TPR-CHAT structurally resembled eukaryotic separase, but with a distinct mechanism for protease regulation. Our findings should facilitate the development of gRAMP-based RNA manipulation tools, and advance our understanding of the virus-host discrimination process governed by a nuclease-protease Craspase during type III-E CRISPR-Cas immunity. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_33677.map.gz emd_33677.map.gz | 59.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-33677-v30.xml emd-33677-v30.xml emd-33677.xml emd-33677.xml | 18 KB 18 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_33677.png emd_33677.png | 75.3 KB | ||
| マスクデータ |  emd_33677_msk_1.map emd_33677_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-33677.cif.gz emd-33677.cif.gz | 6.6 KB | ||
| その他 |  emd_33677_half_map_1.map.gz emd_33677_half_map_1.map.gz emd_33677_half_map_2.map.gz emd_33677_half_map_2.map.gz | 59.4 MB 59.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-33677 http://ftp.pdbj.org/pub/emdb/structures/EMD-33677 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33677 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33677 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_33677.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_33677.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||
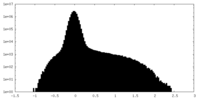
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_33677_msk_1.map emd_33677_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
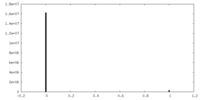
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_33677_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
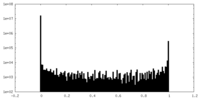
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_33677_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
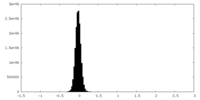
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Type III-E CRISPR gRAMP-crRNA binary complex
| 全体 | 名称: Type III-E CRISPR gRAMP-crRNA binary complex |
|---|---|
| 要素 |
|
-超分子 #1: Type III-E CRISPR gRAMP-crRNA binary complex
| 超分子 | 名称: Type III-E CRISPR gRAMP-crRNA binary complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
-超分子 #2: gRAMP
| 超分子 | 名称: gRAMP / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
-超分子 #3: crRNA
| 超分子 | 名称: crRNA / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|
-超分子 #4: Non-self RNA target
| 超分子 | 名称: Non-self RNA target / タイプ: complex / ID: 4 / 親要素: 1 / 含まれる分子: #3 |
|---|
-分子 #1: RAMP superfamily protein
| 分子 | 名称: RAMP superfamily protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
| 分子量 | 理論値: 198.652688 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MHHHHHHKSN DMNITVELTF FEPYRLVEWF DWDARKKSHS AMRGQAFAQW TWKGKGRTAG KSFITGTLVR SAVIKAVEEL LSLNNGKWE GVPCCNGSFQ TDESKGKKPS FLRKRHTLQW QANNKNICDK EEACPFCILL GRFDNAGKVH ERNKDYDIHF S NFDLDHKQ ...文字列: MHHHHHHKSN DMNITVELTF FEPYRLVEWF DWDARKKSHS AMRGQAFAQW TWKGKGRTAG KSFITGTLVR SAVIKAVEEL LSLNNGKWE GVPCCNGSFQ TDESKGKKPS FLRKRHTLQW QANNKNICDK EEACPFCILL GRFDNAGKVH ERNKDYDIHF S NFDLDHKQ EKNDLRLVDI ASGRILNRVD FDTGKAKDYF RTWEADYETY GTYTGRITLR NEHAKKLLLA SLGFVDKLCG AL CRIEVIK KSESPLPSDT KEQSYTKDDT VEVLSEDHND ELRKQAEVIV EAFKQNDKLE KIRILADAIR TLRLHGEGVI EKD ELPDGK EERDKGHHLW DIKVQGTALR TKLKELWQSN KDIGWRKFTE MLGSNLYLIY KKETGGVSTR FRILGDTEYY SKAH DSEGS DLFIPVTPPE GIETKEWIIV GRLKAATPFY FGVQQPSDSI PGKEKKSEDS LVINEHTSFN ILLDKENRYR IPRSA LRGA LRRDLRTAFG SGCNVSLGGQ ILCNCKVCIE MRRITLKDSV SDFSEPPEIR YRIAKNPGTA TVEDGSLFDI EVGPEG LTF PFVLRYRGHK FPEQLSSVIR YWEENDGKNG MAWLGGLDST GKGRFALKDI KIFEWDLNQK INEYIKERGM RGKEKEL LE MGESSLPDGL IPYKFFEERE CLFPYKENLK PQWSEVQYTI EVGSPLLTAD TISALTEPGN RDAIAYKKRV YNDGNNAI E PEPRFAVKSE THRGIFRTAV GRRTGDLGKE DHEDCTCDMC IIFGNEHESS KIRFEDLELI NGNEFEKLEK HIDHVAIDR FTGGALDKAK FDTYPLAGSP KKPLKLKGRF WIKKGFSGDH KLLITTALSD IRDGLYPLGS KGGVGYGWVA GISIDDNVPD DFKEMINKT EMPLPEEVEE SNNGPINNDY VHPGHQSPKQ DHKNKNIYYP HYFLDSGSKV YREKDIITHE EFTEELLSGK I NCKLETLT PLIIPDTSDE NGLKLQGNKP GHKNYKFFNI NGELMIPGSE LRGMLRTHFE ALTKSCFAIF GEDSTLSWRM NA DEKDYKI DSNSIRKMES QRNPKYRIPD ELQKELRNSG NGLFNRLYTS ERRFWSDVSN KFENSIDYKR EILRCAGRPK NYK GGIIRQ RKDSLMAEEL KVHRLPLYDN FDIPDSAYKA NDHCRKSATC STSRGCRERF TCGIKVRDKN RVFLNAANNN RQYL NNIKK SNHDLYLQYL KGEKKIRFNS KVITGSERSP IDVIAELNER GRQTGFIKLS GLNNSNKSQG NTGTTFNSGW DRFEL NILL DDLETRPSKS DYPRPRLLFT KDQYEYNITK RCERVFEIDK GNKTGYPVDD QIKKNYEDIL DSYDGIKDQE VAERFD TFT RGSKLKVGDL VYFHIDGDNK IDSLIPVRIS RKCASKTLGG KLDKALHPCT GLSDGLCPGC HLFGTTDYKG RVKFGFA KY ENGPEWLITR GNNPERSLTL GVLESPRPAF SIPDDESEIP GRKFYLHHNG WRIIRQKQLE IRETVQPERN VTTEVMDK G NVFSFDVRFE NLREWELGLL LQSLDPGKNI AHKLGKGKPY GFGSVKIKID SLHTFKINSN NDKIKRVPQS DIREYINKG YQKLIEWSGN NSIQKGNVLP QWHVIPHIDK LYKLLWVPFL NDSKLEPDVR YPVLNEESKG YIEGSDYTYK KLGDKDNLPY KTRVKGLTT PWSPWNPFQV IAEHEEQEVN VTGSRPSVTD KIERDGKMV UniProtKB: RAMP superfamily protein |
-分子 #2: crRNA
| 分子 | 名称: crRNA / タイプ: rna / ID: 2 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
| 分子量 | 理論値: 35.43209 KDa |
| 配列 | 文字列: GUUAUGAAAC AAGAGAAGGA CUUAAUGUCA CGGUACCCAA UUUUCUGCCC CGGACUCCAC GGCUGUUACU AGAGGUUAUG AAACAAGAG AAGGACUUAA UGUCACGGUA C |
-分子 #3: Non-self RNA target
| 分子 | 名称: Non-self RNA target / タイプ: rna / ID: 3 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
| 分子量 | 理論値: 18.097797 KDa |
| 配列 | 文字列: CUCUAGUAAC AGCCGUGGAG UCCGGGGCAG AAAAUUGGCA UGGCACUGUA AUUCAG |
-分子 #4: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 4 / コピー数: 4 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 1 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.5 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: INSILICO MODEL |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.54 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 444936 |
| 初期 角度割当 | タイプ: RANDOM ASSIGNMENT |
| 最終 角度割当 | タイプ: RANDOM ASSIGNMENT |
 ムービー
ムービー コントローラー
コントローラー















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)