+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the nucleosome containing Komagataella pastoris histones | ||||||||||||||||||||||||
 マップデータ マップデータ | Cryo-EM map of the nucleosome containing Komagataella pastoris histones | ||||||||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||||||||
 キーワード キーワード | Chromatin / Nucleosome / Komagataella pastoris / Histone H2A / Histone H2B / Histone H3 / Histone H4 / DNA / Epigenetic / Gene regulation / cryo-EM / GENE REGULATION-DNA complex | ||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報structural constituent of chromatin / nucleosome / protein heterodimerization activity / DNA repair / DNA binding / nucleus 類似検索 - 分子機能 | ||||||||||||||||||||||||
| 生物種 |  Komagataella pastoris (菌類) / synthetic construct (人工物) Komagataella pastoris (菌類) / synthetic construct (人工物) | ||||||||||||||||||||||||
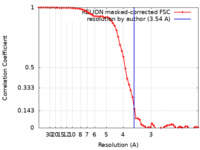
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.54 Å | ||||||||||||||||||||||||
 データ登録者 データ登録者 | Fukushima Y / Hatazawa S / Hirai S / Kujirai T / Takizawa Y / Kurumizaka H | ||||||||||||||||||||||||
| 資金援助 |  日本, 7件 日本, 7件
| ||||||||||||||||||||||||
 引用 引用 |  ジャーナル: J Biochem / 年: 2022 ジャーナル: J Biochem / 年: 2022タイトル: Structural and biochemical analyses of the nucleosome containing Komagataella pastoris histones. 著者: Yutaro Fukushima / Suguru Hatazawa / Seiya Hirai / Tomoya Kujirai / Haruhiko Ehara / Shun-Ichi Sekine / Yoshimasa Takizawa / Hitoshi Kurumizaka /  要旨: Komagataella pastoris is a methylotrophic yeast that is commonly used as a host cell for protein production. In the present study, we reconstituted the nucleosome with K. pastoris histones and ...Komagataella pastoris is a methylotrophic yeast that is commonly used as a host cell for protein production. In the present study, we reconstituted the nucleosome with K. pastoris histones and determined the structure of the nucleosome core particle by cryogenic electron microscopy. In the K. pastoris nucleosome, the histones form an octamer and the DNA is left-handedly wrapped around it. Micrococcal nuclease assays revealed that the DNA ends of the K. pastoris nucleosome are somewhat more accessible, as compared with those of the human nucleosome. In vitro transcription assays demonstrated that the K. pastoris nucleosome is transcribed by the K. pastoris RNA polymerase II (RNAPII) more efficiently than the human nucleosome, while the RNAPII pausing positions of the K. pastoris nucleosome are the same as those of the human nucleosome. These results suggested that the DNA end flexibility may enhance the transcription efficiency in the nucleosome but minimally affect the nucleosomal pausing positions of RNAPII. | ||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32591.map.gz emd_32591.map.gz | 2.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32591-v30.xml emd-32591-v30.xml emd-32591.xml emd-32591.xml | 18.4 KB 18.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_32591_fsc.xml emd_32591_fsc.xml | 6.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_32591.png emd_32591.png | 124.2 KB | ||
| Filedesc metadata |  emd-32591.cif.gz emd-32591.cif.gz | 5.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32591 http://ftp.pdbj.org/pub/emdb/structures/EMD-32591 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32591 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32591 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7wlrMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32591.map.gz / 形式: CCP4 / 大きさ: 22.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32591.map.gz / 形式: CCP4 / 大きさ: 22.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM map of the nucleosome containing Komagataella pastoris histones | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.06 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : K. pastoris nucleosome
| 全体 | 名称: K. pastoris nucleosome |
|---|---|
| 要素 |
|
-超分子 #1: K. pastoris nucleosome
| 超分子 | 名称: K. pastoris nucleosome / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|---|
| 由来(天然) | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
-超分子 #2: Histone
| 超分子 | 名称: Histone / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#4 |
|---|
-超分子 #3: DNA
| 超分子 | 名称: DNA / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #1-#2 |
|---|
-分子 #1: Histone H3
| 分子 | 名称: Histone H3 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
| 分子量 | 理論値: 11.601565 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: KPHRYKPGTV ALREIRRFQK STELLIRKLP FQRLVREIAQ DFKTDLRFQS SAIGALQESV EAYLVSLFED TNLCAIHAKR VTIQKKDIL LARRLRGERS UniProtKB: Histone H3 |
-分子 #2: Histone H4
| 分子 | 名称: Histone H4 / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
| 分子量 | 理論値: 10.030811 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: KRHRKILRDN IQGITKPAIR RLARRGGVKR ISALIYEEVR AVLKTFLENV IRDAVTYTEH AKRKTVTSLD VVYALKRQGR TLYGFGG UniProtKB: Histone H4 |
-分子 #3: Histone H2A
| 分子 | 名称: Histone H2A / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
| 分子量 | 理論値: 11.810682 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: KASTSRSSKA GLTFPVGRVH RLLRRGNYAQ RIGSGAPVYL TAVLEYLAAE ILELAGNAAR DNKKSRIIPR HLQLAIRNDE ELNKLLGHV TIAQGGVLPN IQSELLPKK UniProtKB: Histone H2A |
-分子 #4: Histone H2B
| 分子 | 名称: Histone H2B / タイプ: protein_or_peptide / ID: 4 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
| 分子量 | 理論値: 11.018554 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: RSKVRKESYA SYIYKVLKQT HPDTGISQKA MSIMNSFVND IFERIASEAS KLASYNKKST ISAREIQTAV RLILPGELSK HAVSEGTRA VTKYTSSTQA UniProtKB: Histone H2B |
-分子 #5: DNA (145-MER)
| 分子 | 名称: DNA (145-MER) / タイプ: dna / ID: 5 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 44.520383 KDa |
| 配列 | 文字列: (DA)(DT)(DC)(DA)(DG)(DA)(DA)(DT)(DC)(DC) (DC)(DG)(DG)(DT)(DG)(DC)(DC)(DG)(DA)(DG) (DG)(DC)(DC)(DG)(DC)(DT)(DC)(DA)(DA) (DT)(DT)(DG)(DG)(DT)(DC)(DG)(DT)(DA)(DG) (DA) (DC)(DA)(DG)(DC)(DT) ...文字列: (DA)(DT)(DC)(DA)(DG)(DA)(DA)(DT)(DC)(DC) (DC)(DG)(DG)(DT)(DG)(DC)(DC)(DG)(DA)(DG) (DG)(DC)(DC)(DG)(DC)(DT)(DC)(DA)(DA) (DT)(DT)(DG)(DG)(DT)(DC)(DG)(DT)(DA)(DG) (DA) (DC)(DA)(DG)(DC)(DT)(DC)(DT)(DA) (DG)(DC)(DA)(DC)(DC)(DG)(DC)(DT)(DT)(DA) (DA)(DA) (DC)(DG)(DC)(DA)(DC)(DG)(DT) (DA)(DC)(DG)(DC)(DG)(DC)(DT)(DG)(DT)(DC) (DC)(DC)(DC) (DC)(DG)(DC)(DG)(DT)(DT) (DT)(DT)(DA)(DA)(DC)(DC)(DG)(DC)(DC)(DA) (DA)(DG)(DG)(DG) (DG)(DA)(DT)(DT)(DA) (DC)(DT)(DC)(DC)(DC)(DT)(DA)(DG)(DT)(DC) (DT)(DC)(DC)(DA)(DG) (DG)(DC)(DA)(DC) (DG)(DT)(DG)(DT)(DC)(DA)(DG)(DA)(DT)(DA) (DT)(DA)(DT)(DA)(DC)(DA) (DT)(DC)(DG) (DA)(DT) |
-分子 #6: DNA (145-MER)
| 分子 | 名称: DNA (145-MER) / タイプ: dna / ID: 6 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 44.99166 KDa |
| 配列 | 文字列: (DA)(DT)(DC)(DG)(DA)(DT)(DG)(DT)(DA)(DT) (DA)(DT)(DA)(DT)(DC)(DT)(DG)(DA)(DC)(DA) (DC)(DG)(DT)(DG)(DC)(DC)(DT)(DG)(DG) (DA)(DG)(DA)(DC)(DT)(DA)(DG)(DG)(DG)(DA) (DG) (DT)(DA)(DA)(DT)(DC) ...文字列: (DA)(DT)(DC)(DG)(DA)(DT)(DG)(DT)(DA)(DT) (DA)(DT)(DA)(DT)(DC)(DT)(DG)(DA)(DC)(DA) (DC)(DG)(DT)(DG)(DC)(DC)(DT)(DG)(DG) (DA)(DG)(DA)(DC)(DT)(DA)(DG)(DG)(DG)(DA) (DG) (DT)(DA)(DA)(DT)(DC)(DC)(DC)(DC) (DT)(DT)(DG)(DG)(DC)(DG)(DG)(DT)(DT)(DA) (DA)(DA) (DA)(DC)(DG)(DC)(DG)(DG)(DG) (DG)(DG)(DA)(DC)(DA)(DG)(DC)(DG)(DC)(DG) (DT)(DA)(DC) (DG)(DT)(DG)(DC)(DG)(DT) (DT)(DT)(DA)(DA)(DG)(DC)(DG)(DG)(DT)(DG) (DC)(DT)(DA)(DG) (DA)(DG)(DC)(DT)(DG) (DT)(DC)(DT)(DA)(DC)(DG)(DA)(DC)(DC)(DA) (DA)(DT)(DT)(DG)(DA) (DG)(DC)(DG)(DG) (DC)(DC)(DT)(DC)(DG)(DG)(DC)(DA)(DC)(DC) (DG)(DG)(DG)(DA)(DT)(DT) (DC)(DT)(DG) (DA)(DT) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.3 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 57.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.25 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)