+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The structure of formyl peptide receptor 1 in complex with Gi and peptide agonist fMLF | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報N-formyl peptide receptor activity / complement receptor activity / scavenger receptor binding / RAGE receptor binding / complement receptor mediated signaling pathway / Formyl peptide receptors bind formyl peptides and many other ligands / azurophil granule membrane / Interleukin-10 signaling / ficolin-1-rich granule membrane / Adenylate cyclase inhibitory pathway ...N-formyl peptide receptor activity / complement receptor activity / scavenger receptor binding / RAGE receptor binding / complement receptor mediated signaling pathway / Formyl peptide receptors bind formyl peptides and many other ligands / azurophil granule membrane / Interleukin-10 signaling / ficolin-1-rich granule membrane / Adenylate cyclase inhibitory pathway / positive regulation of protein localization to cell cortex / regulation of cAMP-mediated signaling / nitric oxide mediated signal transduction / D2 dopamine receptor binding / G protein-coupled serotonin receptor binding / regulation of mitotic spindle organization / cellular response to forskolin / adenylate cyclase-inhibiting G protein-coupled receptor signaling pathway / secretory granule membrane / Regulation of insulin secretion / G protein-coupled receptor binding / G protein-coupled receptor activity / G-protein beta/gamma-subunit complex binding / Olfactory Signaling Pathway / Activation of the phototransduction cascade / adenylate cyclase-modulating G protein-coupled receptor signaling pathway / G beta:gamma signalling through PLC beta / Presynaptic function of Kainate receptors / Thromboxane signalling through TP receptor / G-protein activation / G protein-coupled acetylcholine receptor signaling pathway / Activation of G protein gated Potassium channels / Inhibition of voltage gated Ca2+ channels via Gbeta/gamma subunits / Prostacyclin signalling through prostacyclin receptor / Glucagon signaling in metabolic regulation / G beta:gamma signalling through CDC42 / response to peptide hormone / ADP signalling through P2Y purinoceptor 12 / G beta:gamma signalling through BTK / Synthesis, secretion, and inactivation of Glucagon-like Peptide-1 (GLP-1) / Sensory perception of sweet, bitter, and umami (glutamate) taste / photoreceptor disc membrane / Adrenaline,noradrenaline inhibits insulin secretion / Glucagon-type ligand receptors / Vasopressin regulates renal water homeostasis via Aquaporins / G alpha (z) signalling events / cellular response to catecholamine stimulus / Glucagon-like Peptide-1 (GLP1) regulates insulin secretion / ADORA2B mediated anti-inflammatory cytokines production / sensory perception of taste / ADP signalling through P2Y purinoceptor 1 / adenylate cyclase-activating dopamine receptor signaling pathway / G beta:gamma signalling through PI3Kgamma / cellular response to prostaglandin E stimulus / Cooperation of PDCL (PhLP1) and TRiC/CCT in G-protein beta folding / GPER1 signaling / GDP binding / chemotaxis / G-protein beta-subunit binding / Inactivation, recovery and regulation of the phototransduction cascade / heterotrimeric G-protein complex / G alpha (12/13) signalling events / extracellular vesicle / signaling receptor complex adaptor activity / Thrombin signalling through proteinase activated receptors (PARs) / GTPase binding / retina development in camera-type eye / phospholipase C-activating G protein-coupled receptor signaling pathway / Ca2+ pathway / cell cortex / midbody / positive regulation of cytosolic calcium ion concentration / G alpha (i) signalling events / fibroblast proliferation / G alpha (s) signalling events / G alpha (q) signalling events / cell population proliferation / cell cycle / Ras protein signal transduction / Extra-nuclear estrogen signaling / inflammatory response / G protein-coupled receptor signaling pathway / cell division / lysosomal membrane / GTPase activity / centrosome / synapse / Neutrophil degranulation / protein-containing complex binding / GTP binding / nucleolus / magnesium ion binding / signal transduction / extracellular exosome / nucleoplasm / membrane / plasma membrane / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.9 Å | |||||||||
 データ登録者 データ登録者 | Wang XK / Chen G / Liao QW / Du Y / Hu HL / Ye DQ | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2022 ジャーナル: Nat Commun / 年: 2022タイトル: Structural basis for recognition of N-formyl peptides as pathogen-associated molecular patterns. 著者: Geng Chen / Xiankun Wang / Qiwen Liao / Yunjun Ge / Haizhan Jiao / Qiang Chen / Yezhou Liu / Wenping Lyu / Lizhe Zhu / Gydo C P van Zundert / Michael J Robertson / Georgios Skiniotis / Yang ...著者: Geng Chen / Xiankun Wang / Qiwen Liao / Yunjun Ge / Haizhan Jiao / Qiang Chen / Yezhou Liu / Wenping Lyu / Lizhe Zhu / Gydo C P van Zundert / Michael J Robertson / Georgios Skiniotis / Yang Du / Hongli Hu / Richard D Ye /   要旨: The formyl peptide receptor 1 (FPR1) is primarily responsible for detection of short peptides bearing N-formylated methionine (fMet) that are characteristic of protein synthesis in bacteria and ...The formyl peptide receptor 1 (FPR1) is primarily responsible for detection of short peptides bearing N-formylated methionine (fMet) that are characteristic of protein synthesis in bacteria and mitochondria. As a result, FPR1 is critical to phagocyte migration and activation in bacterial infection, tissue injury and inflammation. How FPR1 distinguishes between formyl peptides and non-formyl peptides remains elusive. Here we report cryo-EM structures of human FPR1-Gi protein complex bound to S. aureus-derived peptide fMet-Ile-Phe-Leu (fMIFL) and E. coli-derived peptide fMet-Leu-Phe (fMLF). Both structures of FPR1 adopt an active conformation and exhibit a binding pocket containing the R201XXXR205 (RGIIR) motif for formyl group interaction and receptor activation. This motif works together with D106 for hydrogen bond formation with the N-formyl group and with fMet, a model supported by MD simulation and functional assays of mutant receptors with key residues for recognition substituted by alanine. The cryo-EM model of agonist-bound FPR1 provides a structural basis for recognition of bacteria-derived chemotactic peptides with potential applications in developing FPR1-targeting agents. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_31323.map.gz emd_31323.map.gz | 59.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-31323-v30.xml emd-31323-v30.xml emd-31323.xml emd-31323.xml | 23.5 KB 23.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_31323.png emd_31323.png | 33 KB | ||
| その他 |  emd_31323_half_map_1.map.gz emd_31323_half_map_1.map.gz emd_31323_half_map_2.map.gz emd_31323_half_map_2.map.gz | 59.5 MB 59.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-31323 http://ftp.pdbj.org/pub/emdb/structures/EMD-31323 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-31323 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-31323 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_31323_validation.pdf.gz emd_31323_validation.pdf.gz | 873.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_31323_full_validation.pdf.gz emd_31323_full_validation.pdf.gz | 873 KB | 表示 | |
| XML形式データ |  emd_31323_validation.xml.gz emd_31323_validation.xml.gz | 12.4 KB | 表示 | |
| CIF形式データ |  emd_31323_validation.cif.gz emd_31323_validation.cif.gz | 14.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-31323 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-31323 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-31323 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-31323 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7euoMC  7vfxC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_31323.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_31323.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.85 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_31323_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
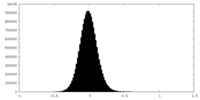
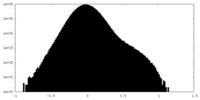
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_31323_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
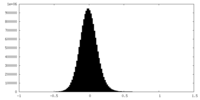
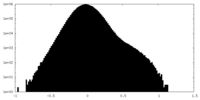
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Complex of FPR1 with Gi and peptdie agonist fMLF
+超分子 #1: Complex of FPR1 with Gi and peptdie agonist fMLF
+超分子 #2: FPR1 with Gi
+超分子 #3: scFv16
+超分子 #4: peptdie agonist fMLF
+分子 #1: fMet-Leu-Phe receptor
+分子 #2: Guanine nucleotide-binding protein G(i) subunit alpha-1
+分子 #3: Guanine nucleotide-binding protein G(I)/G(S)/G(T) subunit beta-1
+分子 #4: Guanine nucleotide-binding protein G(I)/G(S)/G(O) subunit gamma-2
+分子 #5: scFv16
+分子 #6: Peptide Agonist fMLF
+分子 #7: CHOLESTEROL
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 6 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | 材質: NICKEL/TITANIUM / メッシュ: 300 / 前処理 - タイプ: PLASMA CLEANING / 前処理 - 時間: 60 sec. |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 55.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 倍率(公称値): 105000 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: EMDB MAP EMDB ID: |
|---|---|
| 最終 再構成 | アルゴリズム: BACK PROJECTION / 解像度のタイプ: BY AUTHOR / 解像度: 2.9 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC / 使用した粒子像数: 392103 |
| 初期 角度割当 | タイプ: RANDOM ASSIGNMENT / ソフトウェア - 名称: RELION |
| 最終 角度割当 | タイプ: OTHER / ソフトウェア - 名称: cryoSPARC |
 ムービー
ムービー コントローラー
コントローラー




































 Z
Z Y
Y X
X