+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CRYO-EM STRUCTURE OF IMPORTIN ALPHA1/BETA HETERODIMER | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Importins / TRANSPORT PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RNA import into nucleus / Inhibition of nitric oxide production / mitotic chromosome movement towards spindle pole / Sensing of DNA Double Strand Breaks / endoplasmic reticulum tubular network / regulation of DNA recombination / establishment of mitotic spindle localization / astral microtubule organization / entry of viral genome into host nucleus through nuclear pore complex via importin / positive regulation of viral life cycle ...RNA import into nucleus / Inhibition of nitric oxide production / mitotic chromosome movement towards spindle pole / Sensing of DNA Double Strand Breaks / endoplasmic reticulum tubular network / regulation of DNA recombination / establishment of mitotic spindle localization / astral microtubule organization / entry of viral genome into host nucleus through nuclear pore complex via importin / positive regulation of viral life cycle / Transport of Ribonucleoproteins into the Host Nucleus / Regulation of cholesterol biosynthesis by SREBP (SREBF) / importin-alpha family protein binding / Initiation of Nuclear Envelope (NE) Reformation / ribosomal protein import into nucleus / NS1 Mediated Effects on Host Pathways / NLS-dependent protein nuclear import complex / Apoptosis induced DNA fragmentation / Nuclear import of Rev protein / Postmitotic nuclear pore complex (NPC) reformation / CREB1 phosphorylation through the activation of CaMKII/CaMKK/CaMKIV cascasde / nuclear import signal receptor activity / CaMK IV-mediated phosphorylation of CREB / nuclear localization sequence binding / mitotic metaphase chromosome alignment / DNA metabolic process / NLS-bearing protein import into nucleus / mitotic spindle assembly / positive regulation of type I interferon production / nuclear pore / Assembly of the ORC complex at the origin of replication / Hsp90 protein binding / ISG15 antiviral mechanism / small GTPase binding / histone deacetylase binding / cytoplasmic stress granule / specific granule lumen / protein import into nucleus / SARS-CoV-1 activates/modulates innate immune responses / host cell / Interferon alpha/beta signaling / nuclear envelope / nuclear membrane / Estrogen-dependent gene expression / ficolin-1-rich granule lumen / protein domain specific binding / Golgi membrane / Neutrophil degranulation / endoplasmic reticulum membrane / SARS-CoV-2 activates/modulates innate and adaptive immune responses / enzyme binding / RNA binding / zinc ion binding / extracellular exosome / extracellular region / nucleoplasm / membrane / nucleus / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.95 Å | |||||||||
 データ登録者 データ登録者 | Ko Y / Cingolani G | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: CRYO-EM STRUCTURE OF IMPORTIN ALPHA1/BETA HETERODIMER 著者: Ko Y / Cingolani G | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_29936.map.gz emd_29936.map.gz | 16.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-29936-v30.xml emd-29936-v30.xml emd-29936.xml emd-29936.xml | 14 KB 14 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_29936.png emd_29936.png | 104 KB | ||
| Filedesc metadata |  emd-29936.cif.gz emd-29936.cif.gz | 5.5 KB | ||
| その他 |  emd_29936_half_map_1.map.gz emd_29936_half_map_1.map.gz emd_29936_half_map_2.map.gz emd_29936_half_map_2.map.gz | 31.9 MB 31.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-29936 http://ftp.pdbj.org/pub/emdb/structures/EMD-29936 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29936 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29936 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_29936_validation.pdf.gz emd_29936_validation.pdf.gz | 686.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_29936_full_validation.pdf.gz emd_29936_full_validation.pdf.gz | 685.9 KB | 表示 | |
| XML形式データ |  emd_29936_validation.xml.gz emd_29936_validation.xml.gz | 10.9 KB | 表示 | |
| CIF形式データ |  emd_29936_validation.cif.gz emd_29936_validation.cif.gz | 12.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29936 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29936 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29936 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29936 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8gcnMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_29936.map.gz / 形式: CCP4 / 大きさ: 34.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_29936.map.gz / 形式: CCP4 / 大きさ: 34.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.872 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_29936_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
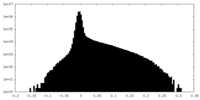
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_29936_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
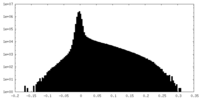
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Importin Alpha1/Beta Heterodimer
| 全体 | 名称: Importin Alpha1/Beta Heterodimer |
|---|---|
| 要素 |
|
-超分子 #1: Importin Alpha1/Beta Heterodimer
| 超分子 | 名称: Importin Alpha1/Beta Heterodimer / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Importin subunit beta-1
| 分子 | 名称: Importin subunit beta-1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 97.257812 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MELITILEKT VSPDRLELEA AQKFLERAAV ENLPTFLVEL SRVLANPGNS QVARVAAGLQ IKNSLTSKDP DIKAQYQQRW LAIDANARR EVKNYVLQTL GTETYRPSSA SQCVAGIACA EIPVNQWPEL IPQLVANVTN PNSTEHMKES TLEAIGYICQ D IDPEQLQD ...文字列: MELITILEKT VSPDRLELEA AQKFLERAAV ENLPTFLVEL SRVLANPGNS QVARVAAGLQ IKNSLTSKDP DIKAQYQQRW LAIDANARR EVKNYVLQTL GTETYRPSSA SQCVAGIACA EIPVNQWPEL IPQLVANVTN PNSTEHMKES TLEAIGYICQ D IDPEQLQD KSNEILTAII QGMRKEEPSN NVKLAATNAL LNSLEFTKAN FDKESERHFI MQVVCEATQC PDTRVRVAAL QN LVKIMSL YYQYMETYMG PALFAITIEA MKSDIDEVAL QGIEFWSNVC DEEMDLAIEA SEAAEQGRPP EHTSKFYAKG ALQ YLVPIL TQTLTKQDEN DDDDDWNPCK AAGVCLMLLA TCCEDDIVPH VLPFIKEHIK NPDWRYRDAA VMAFGCILEG PEPS QLKPL VIQAMPTLIE LMKDPSVVVR DTAAWTVGRI CELLPEAAIN DVYLAPLLQC LIEGLSAEPR VASNVCWAFS SLAEA AYEA ADVADDQEEP ATYCLSSSFE LIVQKLLETT DRPDGHQNNL RSSAYESLME IVKNSAKDCY PAVQKTTLVI MERLQQ VLQ MESHIQSTSD RIQFNDLQSL LCATLQNVLR KVQHQDALQI SDVVMASLLR MFQSTAGSGG VQEDALMAVS TLVEVLG GE FLKYMEAFKP FLGIGLKNYA EYQVCLAAVG LVGDLCRALQ SNIIPFCDEV MQLLLENLGN ENVHRSVKPQ ILSVFGDI A LAIGGEFKKY LEVVLNTLQQ ASQAQVDKSD YDMVDYLNEL RESCLEAYTG IVQGLKGDQE NVHPDVMLVQ PRVEFILSF IDHIAGDEDH TDGVVACAAG LIGDLCTAFG KDVLKLVEAR PMIHELLTEG RRSKTNKAKT LATWATKELR KLKNQA UniProtKB: Importin subunit beta-1 |
-分子 #2: Importin subunit alpha-1
| 分子 | 名称: Importin subunit alpha-1 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 5.296262 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: AARLHRFKNK GKDSTEMRRR RIEVNVELRK AKKDDQMLKR RNV UniProtKB: Importin subunit alpha-1 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.95 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 1009142 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー














 Z
Z Y
Y X
X