+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of 3DVA component 0 of Escherichia coli que-PEC (paused elongation complex) RNA Polymerase plus preQ1 ligand | |||||||||||||||
 マップデータ マップデータ | ||||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | RNA Polymerase / Riboswitch / Transcription / preQ1 | |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報DNA-directed RNA polymerase complex / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / protein dimerization activity / DNA-templated transcription / magnesium ion binding / DNA binding / zinc ion binding / cytoplasm 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |  | |||||||||||||||
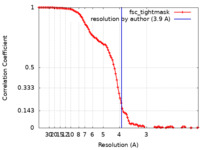
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.9 Å | |||||||||||||||
 データ登録者 データ登録者 | Porta JC / Chauvier A / Deb I / Ellinger E / Frank AT / Meze K / Ohi MD / Walter NG | |||||||||||||||
| 資金援助 |  米国, 4件 米国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2023 ジャーナル: Nat Struct Mol Biol / 年: 2023タイトル: Structural basis for control of bacterial RNA polymerase pausing by a riboswitch and its ligand. 著者: Adrien Chauvier / Jason C Porta / Indrajit Deb / Emily Ellinger / Katarina Meze / Aaron T Frank / Melanie D Ohi / Nils G Walter /   要旨: Folding of nascent transcripts can be modulated by the RNA polymerase (RNAP) that carries out their transcription, and vice versa. A pause of RNAP during transcription of a preQ riboswitch (termed ...Folding of nascent transcripts can be modulated by the RNA polymerase (RNAP) that carries out their transcription, and vice versa. A pause of RNAP during transcription of a preQ riboswitch (termed que-PEC) is stabilized by a previously characterized template consensus sequence and the ligand-free conformation of the nascent RNA. Ligand binding to the riboswitch induces RNAP pause release and downstream transcription termination; however, the mechanism by which riboswitch folding modulates pausing is unclear. Here, we report single-particle cryo-electron microscopy reconstructions of que-PEC in ligand-free and ligand-bound states. In the absence of preQ, the RNA transcript is in an unexpected hyper-translocated state, preventing downstream nucleotide incorporation. Strikingly, on ligand binding, the riboswitch rotates around its helical axis, expanding the surrounding RNAP exit channel and repositioning the transcript for elongation. Our study reveals the tight coupling by which nascent RNA structures and their ligands can functionally regulate the macromolecular transcription machinery. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
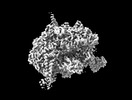
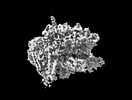
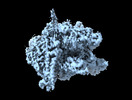
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_29812.map.gz emd_29812.map.gz | 93.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-29812-v30.xml emd-29812-v30.xml emd-29812.xml emd-29812.xml | 29.2 KB 29.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_29812_fsc.xml emd_29812_fsc.xml | 10.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_29812.png emd_29812.png | 57.3 KB | ||
| Filedesc metadata |  emd-29812.cif.gz emd-29812.cif.gz | 9 KB | ||
| その他 |  emd_29812_half_map_1.map.gz emd_29812_half_map_1.map.gz emd_29812_half_map_2.map.gz emd_29812_half_map_2.map.gz | 94 MB 94 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-29812 http://ftp.pdbj.org/pub/emdb/structures/EMD-29812 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29812 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29812 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_29812_validation.pdf.gz emd_29812_validation.pdf.gz | 1021.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_29812_full_validation.pdf.gz emd_29812_full_validation.pdf.gz | 1021.4 KB | 表示 | |
| XML形式データ |  emd_29812_validation.xml.gz emd_29812_validation.xml.gz | 16.1 KB | 表示 | |
| CIF形式データ |  emd_29812_validation.cif.gz emd_29812_validation.cif.gz | 21.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29812 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29812 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29812 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29812 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8g7eMC  8f3cC  8g00C  8g1sC  8g2wC  8g4wC  8g8zC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_29812.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_29812.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_29812_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
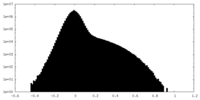
| 投影像・断面図 |
| ||||||||||||
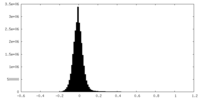
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_29812_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
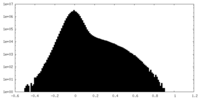
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Cryo-EM structure of 3DVA component 0 of Escherichia coli que-PEC...
+超分子 #1: Cryo-EM structure of 3DVA component 0 of Escherichia coli que-PEC...
+分子 #1: DNA (39-mer)
+分子 #2: DNA (31-MER)
+分子 #3: DNA-directed RNA polymerase subunit alpha
+分子 #4: DNA-directed RNA polymerase subunit omega
+分子 #6: DNA-directed RNA polymerase subunit beta
+分子 #7: DNA-directed RNA polymerase subunit beta'
+分子 #5: RNA (47-MER)
+分子 #8: 7-DEAZA-7-AMINOMETHYL-GUANINE
+分子 #9: MAGNESIUM ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5.00 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||
| グリッド | モデル: C-flat-1.2/1.3 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: AIR | ||||||||||||
| 凍結 | 凍結剤: ETHANE 詳細: VITRIFICATION WAS CARRIED OUT IN A CHAMBER WITH THE TEMPERATURE SET TO 4 DEGREES CELSIUS.. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) デジタル化 - サイズ - 横: 1 pixel / デジタル化 - サイズ - 縦: 1 pixel / 平均電子線量: 62.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.5 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー









 Z
Z Y
Y X
X