+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of 3DVA component 2 of Escherichia coli que-PEC (paused elongation complex) RNA Polymerase minus preQ1 ligand | |||||||||||||||
 マップデータ マップデータ | ||||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | RNA Polymerase / Riboswitch / Transcription / preQ1 | |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RNA polymerase complex / submerged biofilm formation / cellular response to cell envelope stress / cytosolic DNA-directed RNA polymerase complex / regulation of DNA-templated transcription initiation / bacterial-type flagellum assembly / bacterial-type flagellum-dependent cell motility / nitrate assimilation / DNA-directed RNA polymerase complex / transcription elongation factor complex ...RNA polymerase complex / submerged biofilm formation / cellular response to cell envelope stress / cytosolic DNA-directed RNA polymerase complex / regulation of DNA-templated transcription initiation / bacterial-type flagellum assembly / bacterial-type flagellum-dependent cell motility / nitrate assimilation / DNA-directed RNA polymerase complex / transcription elongation factor complex / regulation of DNA-templated transcription elongation / transcription antitermination / DNA-templated transcription initiation / cell motility / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / response to heat / protein-containing complex assembly / intracellular iron ion homeostasis / protein dimerization activity / DNA-templated transcription / magnesium ion binding / DNA binding / zinc ion binding / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |  | |||||||||||||||
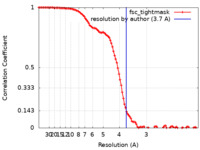
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.7 Å | |||||||||||||||
 データ登録者 データ登録者 | Porta JC / Chauvier A / Deb I / Ellinger E / Frank AT / Meze K / Ohi MD / Walter NG | |||||||||||||||
| 資金援助 |  米国, 4件 米国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2023 ジャーナル: Nat Struct Mol Biol / 年: 2023タイトル: Structural basis for control of bacterial RNA polymerase pausing by a riboswitch and its ligand. 著者: Adrien Chauvier / Jason C Porta / Indrajit Deb / Emily Ellinger / Katarina Meze / Aaron T Frank / Melanie D Ohi / Nils G Walter /   要旨: Folding of nascent transcripts can be modulated by the RNA polymerase (RNAP) that carries out their transcription, and vice versa. A pause of RNAP during transcription of a preQ riboswitch (termed ...Folding of nascent transcripts can be modulated by the RNA polymerase (RNAP) that carries out their transcription, and vice versa. A pause of RNAP during transcription of a preQ riboswitch (termed que-PEC) is stabilized by a previously characterized template consensus sequence and the ligand-free conformation of the nascent RNA. Ligand binding to the riboswitch induces RNAP pause release and downstream transcription termination; however, the mechanism by which riboswitch folding modulates pausing is unclear. Here, we report single-particle cryo-electron microscopy reconstructions of que-PEC in ligand-free and ligand-bound states. In the absence of preQ, the RNA transcript is in an unexpected hyper-translocated state, preventing downstream nucleotide incorporation. Strikingly, on ligand binding, the riboswitch rotates around its helical axis, expanding the surrounding RNAP exit channel and repositioning the transcript for elongation. Our study reveals the tight coupling by which nascent RNA structures and their ligands can functionally regulate the macromolecular transcription machinery. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
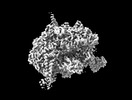
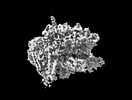
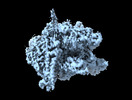
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_29683.map.gz emd_29683.map.gz | 97.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-29683-v30.xml emd-29683-v30.xml emd-29683.xml emd-29683.xml | 28.9 KB 28.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_29683_fsc.xml emd_29683_fsc.xml | 10.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_29683.png emd_29683.png | 55.3 KB | ||
| Filedesc metadata |  emd-29683.cif.gz emd-29683.cif.gz | 8.9 KB | ||
| その他 |  emd_29683_half_map_1.map.gz emd_29683_half_map_1.map.gz emd_29683_half_map_2.map.gz emd_29683_half_map_2.map.gz | 95.5 MB 95.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-29683 http://ftp.pdbj.org/pub/emdb/structures/EMD-29683 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29683 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29683 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_29683_validation.pdf.gz emd_29683_validation.pdf.gz | 1.3 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_29683_full_validation.pdf.gz emd_29683_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  emd_29683_validation.xml.gz emd_29683_validation.xml.gz | 16.1 KB | 表示 | |
| CIF形式データ |  emd_29683_validation.cif.gz emd_29683_validation.cif.gz | 21.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29683 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29683 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29683 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29683 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8g2wMC  8f3cC  8g00C  8g1sC  8g4wC  8g7eC  8g8zC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_29683.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_29683.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_29683_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
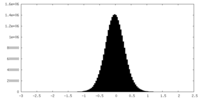
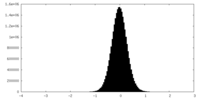
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_29683_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
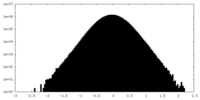
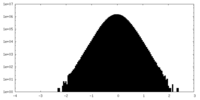
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cryo-EM structure of 3DVA component 2 of Escherichia coli que-PEC...
| 全体 | 名称: Cryo-EM structure of 3DVA component 2 of Escherichia coli que-PEC (paused elongation complex) RNA Polymerase minus preQ1 ligand |
|---|---|
| 要素 |
|
-超分子 #1: Cryo-EM structure of 3DVA component 2 of Escherichia coli que-PEC...
| 超分子 | 名称: Cryo-EM structure of 3DVA component 2 of Escherichia coli que-PEC (paused elongation complex) RNA Polymerase minus preQ1 ligand タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#7 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 420 KDa |
-分子 #1: DNA (39-MER)
| 分子 | 名称: DNA (39-MER) / タイプ: dna / ID: 1 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 12.063754 KDa |
| 配列 | 文字列: (DG)(DG)(DT)(DC)(DA)(DG)(DT)(DA)(DC)(DG) (DT)(DC)(DC)(DA)(DT)(DT)(DA)(DG)(DC)(DT) (DC)(DT)(DT)(DC)(DG)(DG)(DA)(DA)(DG) (DA)(DG)(DA)(DT)(DT)(DC)(DA)(DG)(DA)(DG) |
-分子 #2: DNA (31-MER)
| 分子 | 名称: DNA (31-MER) / タイプ: dna / ID: 2 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 9.486079 KDa |
| 配列 | 文字列: (DC)(DT)(DC)(DT)(DG)(DA)(DA)(DT)(DC)(DT) (DC)(DT)(DT)(DC)(DC)(DT)(DC)(DG)(DT)(DG) (DT)(DG)(DG)(DT)(DC)(DA)(DG)(DG)(DA) (DC)(DG) |
-分子 #3: DNA-directed RNA polymerase subunit alpha
| 分子 | 名称: DNA-directed RNA polymerase subunit alpha / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO / EC番号: DNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 25.971531 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MQGSVTEFLK PRLVDIEQVS STHAKVTLEP LERGFGHTLG NALRRILLSS MPGCAVTEVE IDGVLHEYST KEGVQEDILE ILLNLKGLA VRVQGKDEVI LTLNKSGIGP VTAADITHDG DVEIVKPQHV ICHLTDENAS ISMRIKVQRG RGYVPASTRI H SEEDERPI ...文字列: MQGSVTEFLK PRLVDIEQVS STHAKVTLEP LERGFGHTLG NALRRILLSS MPGCAVTEVE IDGVLHEYST KEGVQEDILE ILLNLKGLA VRVQGKDEVI LTLNKSGIGP VTAADITHDG DVEIVKPQHV ICHLTDENAS ISMRIKVQRG RGYVPASTRI H SEEDERPI GRLLVDACYS PVERIAYNVE AARVEQRTDL DKLVIEMETN GTIDPEEAIR RAATILAEQL EAFVDLE UniProtKB: DNA-directed RNA polymerase subunit alpha |
-分子 #4: DNA-directed RNA polymerase subunit beta
| 分子 | 名称: DNA-directed RNA polymerase subunit beta / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 150.560562 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: VYSYTEKKRI RKDFGKRPQV LDVPYLLSIQ LDSFQKFIEQ DPEGQYGLEA AFRSVFPIQS YSGNSELQYV SYRLGEPVFD VQECQIRGV TYSAPLRVKL RLVIYEREAP EGTVKDIKEQ EVYMGEIPLM TDNGTFVING TERVIVSQLH RSPGVFFDSD K GKTHSSGK ...文字列: VYSYTEKKRI RKDFGKRPQV LDVPYLLSIQ LDSFQKFIEQ DPEGQYGLEA AFRSVFPIQS YSGNSELQYV SYRLGEPVFD VQECQIRGV TYSAPLRVKL RLVIYEREAP EGTVKDIKEQ EVYMGEIPLM TDNGTFVING TERVIVSQLH RSPGVFFDSD K GKTHSSGK VLYNARIIPY RGSWLDFEFD PKDNLFVRID RRRKLPATII LRALNYTTEQ ILDLFFEKVI FEIRDNKLQM EL VPERLRG ETASFDIEAN GKVYVEKGRR ITARHIRQLE KDDVKLIEVP VEYIAGKVVA KDYIDESTGE LICAANMELS LDL LAKLSQ SGHKRIETLF TNDLDHGPYI SETLRVDPTN DRLSALVEIY RMMRPGEPPT REAAESLFEN LFFSEDRYDL SAVG RMKFN RSLLREEIEG SGILSKDDII DVMKKLIDIR NGKGEVDDID HLGNRRIRSV GEMAENQFRV GLVRVERAVK ERLSL GDLD TLMPQDMINA KPISAAVKEF FGSSQLSQFM DQNNPLSEIT HKRRISALGP GGLTRERAGF EVRDVHPTHY GRVCPI ETP EGPNIGLINS LSVYAQTNEY GFLETPYRKV TDGVVTDEIH YLSAIEEGNY VIAQANSNLD EEGHFVEDLV TCRSKGE SS LFSRDQVDYM DVSTQQVVSV GASLIPFLEH DDANRALMGA NMQRQAVPTL RADKPLVGTG MERAVAVDSG VTAVAKRG G VVQYVDASRI VIKVNEDEMY PGEAGIDIYN LTKYTRSNQN TCINQMPCVS LGEPVERGDV LADGPSTDLG ELALGQNMR VAFMPWNGYN FEDSILVSER VVQEDRFTTI HIQELACVSR DTKLGPEEIT ADIPNVGEAA LSKLDESGIV YIGAEVTGGD ILVGKVTPK GETQLTPEEK LLRAIFGEKA SDVKDSSLRV PNGVSGTVID VQVFTRDGVE KDKRALEIEE MQLKQAKKDL S EELQILEA GLFSRIRAVL VAGGVEAEKL DKLPRDRWLE LGLTDEEKQN QLEQLAEQYD ELKHEFEKKL EAKRRKITQG DD LAPGVLK IVKVYLAVKR RIQPGDKMAG RHGNKGVISK INPIEDMPYD ENGTPVDIVL NPLGVPSRMN IGQILETHLG MAA KGIGDK INAMLKQQQE VAKLREFIQR AYDLGADVRQ KVDLSTFSDE EVMRLAENLR KGMPIATPVF DGAKEAEIKE LLKL GDLPT SGQIRLYDGR TGEQFERPVT VGYMYMLKLN HLVDDKMHAR STGSYSLVTQ QPLGGKAQFG GQRFGEMEVW ALEAY GAAY TLQEMLTVKS DDVNGRTKMY KNIVDGNHQM EPGMPESFNV LLKEIRSLGI NIELED UniProtKB: DNA-directed RNA polymerase subunit beta |
-分子 #5: DNA-directed RNA polymerase subunit beta'
| 分子 | 名称: DNA-directed RNA polymerase subunit beta' / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 150.436344 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: EFDAIKIALA SPDMIRSWSF GEVKKPETIN YRTFKPERDG LFCARIFGPV KDYECLCGKY KRLKHRGVIC EKCGVEVTQT KVRRERMGH IELASPTAHI WFLKSLPSRI GLLLDMPLRD IERVLYFESY VVIEGGMTNL ERQQILTEEQ YLDALEEFGD E FDAKMGAE ...文字列: EFDAIKIALA SPDMIRSWSF GEVKKPETIN YRTFKPERDG LFCARIFGPV KDYECLCGKY KRLKHRGVIC EKCGVEVTQT KVRRERMGH IELASPTAHI WFLKSLPSRI GLLLDMPLRD IERVLYFESY VVIEGGMTNL ERQQILTEEQ YLDALEEFGD E FDAKMGAE AIQALLKSMD LEQECEQLRE ELNETNSETK RKKLTKRIKL LEAFVQSGNK PEWMILTVLP VLPPDLRPLV PL DGGRFAT SDLNDLYRRV INRNNRLKRL LDLAAPDIIV RNEKRMLQEA VDALLDNGRR GRAITGSNKR PLKSLADMIK GKQ GRFRQN LLGKRVDYSG RSVITVGPYL RLHQCGLPKK MALELFKPFI YGKLELRGLA TTIKAAKKMV EREEAVVWDI LDEV IREHP VLLNRAPTLH RLGIQAFEPV LIEGKAIQLH PLVCAAYNAD FDGDQMAVHV PLTLEAQLEA RALMMSTNNI LSPAN GEPI IVPSQDVVLG LYYMTRDCVN AKGEGMVLTG PKEAERLYRS GLASLHARVK VRITEYEKDA NGELVAKTSL KDTTVG RAI LWMIVPKGLP YSIVNQALGK KAISKMLNTC YRILGLKPTV IFADQIMYTG FAYAARSGAS VGIDDMVIPE KKHEIIS EA EAEVAEIQEQ FQSGLVTAGE RYNKVIDIWA AANDRVSKAM MDNLQTETVI NRDGQEEKQV SFNSIYMMAD SGARGSAA Q IRQLAGMRGL MAKPDGSIIE TPITANFREG LNVLQYFIST HGARKGLADT ALKTANSGYL TRRLVDVAQD LVVTEDDCG THEGIMMTPV IEGGDVKEPL RDRVLGRVTA EDVLKPGTAD ILVPRNTLLH EQWCDLLEEN SVDAVKVRSV VSCDTDFGVC AHCYGRDLA RGHIINKGEA IGVIAAQSIG EPGTQLTMRT FHIGGAASRA AAESSIQVKN KGSIKLSNVK SVVNSSGKLV I TSRNTELK LIDEFGRTKE SYKVPYGAVL AKGDGEQVAG GETVANWDPH TMPVITEVSG FVRFTDMIDG QTITRQTDEL TG LSSLVVL DSAERTAGGK DLRPALKIVD AQGNDVLIPG TDMPAQYFLP GKAIVQLEDG VQISSGDTLA RIPQESGGTK DIT GGLPRV ADLFEARRPK EPAILAEISG IVSFGKETKG KRRLVITPVD GSDPYEEMIP KWRQLNVFEG ERVERGDVIS DGPE APHDI LRLRGVHAVT RYIVNEVQDV YRLQGVKIND KHIEVIVRQM LRKATIVNAG SSDFLEGEQV EYSRVKIANR ELEAN GKVG ATYSRDLLGI TKASLATESF ISAASFQETT RVLTEAAVAG KRDELRGLKE NVIVGRLIPA GTGYAYHQDR MRRR UniProtKB: DNA-directed RNA polymerase subunit beta' |
-分子 #6: DNA-directed RNA polymerase subunit omega
| 分子 | 名称: DNA-directed RNA polymerase subunit omega / タイプ: protein_or_peptide / ID: 6 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 8.963044 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: ARVTVQDAVE KIGNRFDLVL VAARRARQMQ VGGKDPLVPE ENDKTTVIAL REIEEGLINN QILDVRERQE QQEQEAAEL UniProtKB: DNA-directed RNA polymerase subunit omega |
-分子 #7: RNA (47-MER)
| 分子 | 名称: RNA (47-MER) / タイプ: rna / ID: 7 / コピー数: 1 / EC番号: DNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 15.059079 KDa |
| 配列 | 文字列: GCAGAGGUUC UAGCUACACC CUCUAUAAAA AACUAAGGAC CACACGA |
-分子 #8: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 8 / コピー数: 1 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5.00 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||
| グリッド | モデル: C-flat-1.2/1.3 / 材質: GOLD / メッシュ: 400 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: AIR | ||||||||||||
| 凍結 | 凍結剤: ETHANE 詳細: VITRIFICATION WAS CARRIED OUT IN A CHAMBER WITH THE TEMPERATURE SET TO 4 DEGREES CELSIUS.. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) デジタル化 - サイズ - 横: 1 pixel / デジタル化 - サイズ - 縦: 1 pixel / 平均電子線量: 62.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.5 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT 当てはまり具合の基準: Cross-correlation coefficient |
| 得られたモデル |  PDB-8g2w: |
 ムービー
ムービー コントローラー
コントローラー









 Z
Z Y
Y X
X