登録情報 データベース : EMDB / ID : EMD-26830タイトル CryoEM Structure of E. coli Transcription-Coupled Ribonucleotide Excision Repair (TC-RER) complex 複合体 : Elongation Complex(EC)-RNaseH2 complexDNA : DNA (29-MER)DNA : DNA (29-MER)RNA : RNA (18-MER)タンパク質・ペプチド : DNA-directed RNA polymerase subunit alphaタンパク質・ペプチド : DNA-directed RNA polymerase subunit betaタンパク質・ペプチド : DNA-directed RNA polymerase subunit beta'タンパク質・ペプチド : DNA-directed RNA polymerase subunit omegaタンパク質・ペプチド : Ribonuclease HIIリガンド : MAGNESIUM IONリガンド : ZINC ION / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
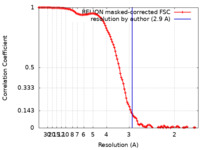
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Escherichia coli (大腸菌)手法 / / 解像度 : 2.9 Å Hao ZT / Grower M / Bharati B / Proshkin S / Epshtein V / Svetlov V / Nudler E / Shamovsky I 資金援助 Organization Grant number 国 National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) GM126891 Howard Hughes Medical Institute (HHMI)
ジャーナル : Cell / 年 : 2023タイトル : RNA polymerase drives ribonucleotide excision DNA repair in E. coli.著者 : Zhitai Hao / Manjunath Gowder / Sergey Proshkin / Binod K Bharati / Vitaly Epshtein / Vladimir Svetlov / Ilya Shamovsky / Evgeny Nudler / 要旨 : Ribonuclease HII (RNaseHII) is the principal enzyme that removes misincorporated ribonucleoside monophosphates (rNMPs) from genomic DNA. Here, we present structural, biochemical, and genetic evidence ... Ribonuclease HII (RNaseHII) is the principal enzyme that removes misincorporated ribonucleoside monophosphates (rNMPs) from genomic DNA. Here, we present structural, biochemical, and genetic evidence demonstrating that ribonucleotide excision repair (RER) is directly coupled to transcription. Affinity pull-downs and mass-spectrometry-assisted mapping of in cellulo inter-protein cross-linking reveal the majority of RNaseHII molecules interacting with RNA polymerase (RNAP) in E. coli. Cryoelectron microscopy structures of RNaseHII bound to RNAP during elongation, with and without the target rNMP substrate, show specific protein-protein interactions that define the transcription-coupled RER (TC-RER) complex in engaged and unengaged states. The weakening of RNAP-RNaseHII interactions compromises RER in vivo. The structure-functional data support a model where RNaseHII scans DNA in one dimension in search for rNMPs while "riding" the RNAP. We further demonstrate that TC-RER accounts for a significant fraction of repair events, thereby establishing RNAP as a surveillance "vehicle" for detecting the most frequently occurring replication errors. 履歴 登録 2022年5月3日 - ヘッダ(付随情報) 公開 2023年5月31日 - マップ公開 2023年5月31日 - 更新 2024年6月12日 - 現状 2024年6月12日 処理サイト : RCSB / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報
 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 米国, 2件
米国, 2件  引用
引用 ジャーナル: Cell / 年: 2023
ジャーナル: Cell / 年: 2023

 構造の表示
構造の表示 ダウンロードとリンク
ダウンロードとリンク emd_26830.map.gz
emd_26830.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-26830-v30.xml
emd-26830-v30.xml emd-26830.xml
emd-26830.xml EMDBヘッダ
EMDBヘッダ emd_26830_fsc.xml
emd_26830_fsc.xml FSCデータファイル
FSCデータファイル emd_26830.png
emd_26830.png emd_26830_msk_1.map
emd_26830_msk_1.map マスクマップ
マスクマップ emd-26830.cif.gz
emd-26830.cif.gz emd_26830_half_map_1.map.gz
emd_26830_half_map_1.map.gz emd_26830_half_map_2.map.gz
emd_26830_half_map_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-26830
http://ftp.pdbj.org/pub/emdb/structures/EMD-26830 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26830
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26830 emd_26830_validation.pdf.gz
emd_26830_validation.pdf.gz EMDB検証レポート
EMDB検証レポート emd_26830_full_validation.pdf.gz
emd_26830_full_validation.pdf.gz emd_26830_validation.xml.gz
emd_26830_validation.xml.gz emd_26830_validation.cif.gz
emd_26830_validation.cif.gz https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26830
https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26830 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26830
ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26830

 F&H 検索
F&H 検索 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_26830.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_26830.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) emd_26830_msk_1.map
emd_26830_msk_1.map 試料の構成要素
試料の構成要素 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 ムービー
ムービー コントローラー
コントローラー







 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)