+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
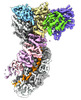
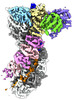
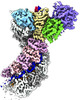
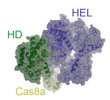
| タイトル | Cascade complex from type I-A CRISPR-Cas system | ||||||||||||
 マップデータ マップデータ | |||||||||||||
 試料 試料 |
| ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||||||||
| 生物種 |  Geobacter sulfurreducens (バクテリア) / Geobacter sulfurreducens (バクテリア) /   Pyrococcus furiosus DSM 3638 (古細菌) / Pyrococcus furiosus DSM 3638 (古細菌) /  | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | ||||||||||||
 データ登録者 データ登録者 | Hu C / Ni D / Nam KH / Majumdar S / McLean J / Stahlberg H / Terns M / Ke A | ||||||||||||
| 資金援助 |  米国, 米国,  スイス, 3件 スイス, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2022 ジャーナル: Mol Cell / 年: 2022タイトル: Allosteric control of type I-A CRISPR-Cas3 complexes and establishment as effective nucleic acid detection and human genome editing tools. 著者: Chunyi Hu / Dongchun Ni / Ki Hyun Nam / Sonali Majumdar / Justin McLean / Henning Stahlberg / Michael P Terns / Ailong Ke /    要旨: Type I CRISPR-Cas systems typically rely on a two-step process to degrade DNA. First, an RNA-guided complex named Cascade identifies the complementary DNA target. The helicase-nuclease fusion enzyme ...Type I CRISPR-Cas systems typically rely on a two-step process to degrade DNA. First, an RNA-guided complex named Cascade identifies the complementary DNA target. The helicase-nuclease fusion enzyme Cas3 is then recruited in trans for processive DNA degradation. Contrary to this model, here, we show that type I-A Cascade and Cas3 function as an integral effector complex. We provide four cryoelectron microscopy (cryo-EM) snapshots of the Pyrococcus furiosus (Pfu) type I-A effector complex in different stages of DNA recognition and degradation. The HD nuclease of Cas3 is autoinhibited inside the effector complex. It is only allosterically activated upon full R-loop formation, when the entire targeted region has been validated by the RNA guide. The mechanistic insights inspired us to convert Pfu Cascade-Cas3 into a high-sensitivity, low-background, and temperature-activated nucleic acid detection tool. Moreover, Pfu CRISPR-Cas3 shows robust bi-directional deletion-editing activity in human cells, which could find usage in allele-specific inactivation of disease-causing mutations. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_26081.map.gz emd_26081.map.gz | 204.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-26081-v30.xml emd-26081-v30.xml emd-26081.xml emd-26081.xml | 19.5 KB 19.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_26081.png emd_26081.png | 125.8 KB | ||
| その他 |  emd_26081_additional_1.map.gz emd_26081_additional_1.map.gz | 203.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-26081 http://ftp.pdbj.org/pub/emdb/structures/EMD-26081 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26081 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26081 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_26081.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_26081.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.99297 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: #1
| ファイル | emd_26081_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
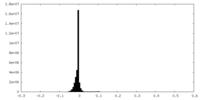
| 投影像・断面図 |
| ||||||||||||
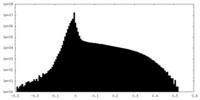
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cascade complex from Pyrococcus furiosus type I-A CRISPR/Cas system
| 全体 | 名称: Cascade complex from Pyrococcus furiosus type I-A CRISPR/Cas system |
|---|---|
| 要素 |
|
-超分子 #1: Cascade complex from Pyrococcus furiosus type I-A CRISPR/Cas system
| 超分子 | 名称: Cascade complex from Pyrococcus furiosus type I-A CRISPR/Cas system タイプ: complex / キメラ: Yes / ID: 1 / 親要素: 0 / 含まれる分子: all / 詳細: Cascade alone |
|---|---|
| 由来(天然) | 生物種:  Geobacter sulfurreducens (バクテリア) Geobacter sulfurreducens (バクテリア) |
| 分子量 | 実験値: 350 KDa |
-分子 #1: Cas8a
| 分子 | 名称: Cas8a / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 |
| 分子量 | 理論値: 38.800719 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: FNEFKTPQID PIFDLYVAYG YVVSLIRGGA KEATLIPHGA SYLIQTDVSN EEFRHGLVDA LSSMLSLHIA LARHSPREGG KLVSDADFS AGANINNVYW DSVPRNLEKL MKDLEKKRSV KGTATIPITL MPSAGKYMLK HFGVQGGNPI KVDLLNYALA W VGFHYYTP ...文字列: FNEFKTPQID PIFDLYVAYG YVVSLIRGGA KEATLIPHGA SYLIQTDVSN EEFRHGLVDA LSSMLSLHIA LARHSPREGG KLVSDADFS AGANINNVYW DSVPRNLEKL MKDLEKKRSV KGTATIPITL MPSAGKYMLK HFGVQGGNPI KVDLLNYALA W VGFHYYTP YIKYAKGDTT WIHIYQIAPV EEVDMISILS LKDLKMHLPH YYESNLDFLI NRRLALLYHL LHSEALELFT EK EFVIHSY TLERSGNNQA IRSFEEEEIG KLMDFLWKLK RRDFYHAIKF IDDLLKKATE GALALIDAIM NERLEGFYTA LKL GKKAGV VSSREIVAAL EDIIC |
-分子 #2: Cas11a
| 分子 | 名称: Cas11a / タイプ: protein_or_peptide / ID: 2 / コピー数: 5 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 |
| 分子量 | 理論値: 12.208933 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: GGWIRNIGRY LSYLVDDTFE EYAYDVVDGI AKARTQEELL EGVYKALRLA PKLKKKAESK GCPPPRIPSP EDIEALEEKV EQLSNPKDL RKLAVSLALW AFASWNNCP |
-分子 #3: Cas7a
| 分子 | 名称: Cas7a / タイプ: protein_or_peptide / ID: 3 / コピー数: 7 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 |
| 分子量 | 理論値: 36.989148 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MYVRISGRIR LNAHSLNAQG GGGTNYIEIT KTKVTVRTEN GWTVVEVPAI TGNMLKHWHF VGFVDYFKTT PYGVNLTERA LRYNGTRFG QGETTATKAN GATVQLNDEA TIIKELADAD VHGFLAPKTG RRRVSLVKAS FILPTEDFIK EVEGERLITA I KHNRVDVD ...文字列: MYVRISGRIR LNAHSLNAQG GGGTNYIEIT KTKVTVRTEN GWTVVEVPAI TGNMLKHWHF VGFVDYFKTT PYGVNLTERA LRYNGTRFG QGETTATKAN GATVQLNDEA TIIKELADAD VHGFLAPKTG RRRVSLVKAS FILPTEDFIK EVEGERLITA I KHNRVDVD EKGAIGSSKE GTAQMLFSRE YATGLYGFSI VLDLGLVGIP QGLPVKFEEN QPRPNIVIDP NERKARIESA LK ALIPMLS GYIGANLARS FPVFKVEELV AIASEGPIPA LVHGFYEDYI EANRSIIKNA RALGFNIEVF TYNVDLGEDI EAT KVSSVE ELVANLVKMV |
-分子 #4: Cas5a
| 分子 | 名称: Cas5a / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 Pyrococcus furiosus DSM 3638 (古細菌) / 株: ATCC 43587 / DSM 3638 / JCM 8422 / Vc1 |
| 分子量 | 理論値: 29.147219 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MDILLVCLRF PFFSVAKRSY QVRTSFLLPP PSALKGALAK GLILLKPEKY ASSSLDEAAL KAIKEIESKL VDIKAVSVAP LSPLIRNAF LLKRLRNLES GSNAEKSDAM RREYTFTREL LVAYIFKNLT QEEKNLYLKA AMLIDVIGDT ESLATPVWAS F VKPEDKKA ...文字列: MDILLVCLRF PFFSVAKRSY QVRTSFLLPP PSALKGALAK GLILLKPEKY ASSSLDEAAL KAIKEIESKL VDIKAVSVAP LSPLIRNAF LLKRLRNLES GSNAEKSDAM RREYTFTREL LVAYIFKNLT QEEKNLYLKA AMLIDVIGDT ESLATPVWAS F VKPEDKKA PLAFSAPYTE IYSLLSSKIQ AKGKIRMYIE KMRVSPEYSK TKGPQEEIFY LPIEERRYKR IVYYARIYPP EV EKALTVD GEVLGIWIP |
-分子 #5: crRNA (45-MER)
| 分子 | 名称: crRNA (45-MER) / タイプ: rna / ID: 5 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 14.373537 KDa |
| 配列 | 文字列: AUUGAAAGAG UGCUUCCCCA AACCCUUAAC UGGUUGUAAC AGUUG |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 / 構成要素 - 濃度: 150.0 mM / 構成要素 - 式: NaCl / 構成要素 - 名称: sodium chloride |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 前処理 - タイプ: PLASMA CLEANING |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV / 詳細: 6 seconds. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS TALOS |
|---|---|
| 特殊光学系 | 位相板: VOLTA PHASE PLATE |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 実像数: 800 / 平均露光時間: 2.5 sec. / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 最小 デフォーカス(補正後): 1.0 µm / 照射モード: FLOOD BEAM / 撮影モード: DIFFRACTION / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.5 µm |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | プロトコル: OTHER |
|---|---|
| 得られたモデル |  PDB-7tr6: |
 ムービー
ムービー コントローラー
コントローラー








 Z
Z Y
Y X
X