+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of EC+EC (leading EC-focused) | |||||||||
 マップデータ マップデータ | Leading EC_map_with_sharpening by postprocesssed in Relion | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報: / : / maintenance of transcriptional fidelity during transcription elongation by RNA polymerase II / RNA polymerase III activity / positive regulation of nuclear-transcribed mRNA poly(A) tail shortening / RNA polymerase II activity / positive regulation of translational initiation / RNA polymerase I complex / RNA polymerase III complex / transcription-coupled nucleotide-excision repair ...: / : / maintenance of transcriptional fidelity during transcription elongation by RNA polymerase II / RNA polymerase III activity / positive regulation of nuclear-transcribed mRNA poly(A) tail shortening / RNA polymerase II activity / positive regulation of translational initiation / RNA polymerase I complex / RNA polymerase III complex / transcription-coupled nucleotide-excision repair / tRNA transcription by RNA polymerase III / RNA polymerase II, core complex / RNA polymerase I activity / translation initiation factor binding / transcription initiation at RNA polymerase II promoter / P-body / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / single-stranded DNA binding / nucleic acid binding / single-stranded RNA binding / protein dimerization activity / nucleotide binding / DNA-templated transcription / nucleolus / DNA binding / zinc ion binding / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.54 Å | |||||||||
 データ登録者 データ登録者 | Yang C / Murakami K | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2022 ジャーナル: Mol Cell / 年: 2022タイトル: Structural visualization of de novo transcription initiation by Saccharomyces cerevisiae RNA polymerase II. 著者: Chun Yang / Rina Fujiwara / Hee Jong Kim / Pratik Basnet / Yunye Zhu / Jose J Gorbea Colón / Stefan Steimle / Benjamin A Garcia / Craig D Kaplan / Kenji Murakami /  要旨: Previous structural studies of the initiation-elongation transition of RNA polymerase II (pol II) transcription have relied on the use of synthetic oligonucleotides, often artificially discontinuous ...Previous structural studies of the initiation-elongation transition of RNA polymerase II (pol II) transcription have relied on the use of synthetic oligonucleotides, often artificially discontinuous to capture pol II in the initiating state. Here, we report multiple structures of initiation complexes converted de novo from a 33-subunit yeast pre-initiation complex (PIC) through catalytic activities and subsequently stalled at different template positions. We determine that PICs in the initially transcribing complex (ITC) can synthesize a transcript of ∼26 nucleotides before transitioning to an elongation complex (EC) as determined by the loss of general transcription factors (GTFs). Unexpectedly, transition to an EC was greatly accelerated when an ITC encountered a downstream EC stalled at promoter proximal regions and resulted in a collided head-to-end dimeric EC complex. Our structural analysis reveals a dynamic state of TFIIH, the largest of GTFs, in PIC/ITC with distinct functional consequences at multiple steps on the pathway to elongation. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23888.map.gz emd_23888.map.gz | 9.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23888-v30.xml emd-23888-v30.xml emd-23888.xml emd-23888.xml | 34.2 KB 34.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_23888_fsc.xml emd_23888_fsc.xml | 7.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_23888.png emd_23888.png | 67.9 KB | ||
| マスクデータ |  emd_23888_msk_1.map emd_23888_msk_1.map | 40.6 MB |  マスクマップ マスクマップ | |
| その他 |  emd_23888_additional_1.map.gz emd_23888_additional_1.map.gz emd_23888_half_map_1.map.gz emd_23888_half_map_1.map.gz emd_23888_half_map_2.map.gz emd_23888_half_map_2.map.gz | 31.2 MB 31.3 MB 31.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23888 http://ftp.pdbj.org/pub/emdb/structures/EMD-23888 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23888 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23888 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_23888_validation.pdf.gz emd_23888_validation.pdf.gz | 871.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_23888_full_validation.pdf.gz emd_23888_full_validation.pdf.gz | 871.4 KB | 表示 | |
| XML形式データ |  emd_23888_validation.xml.gz emd_23888_validation.xml.gz | 13.5 KB | 表示 | |
| CIF形式データ |  emd_23888_validation.cif.gz emd_23888_validation.cif.gz | 19 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23888 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23888 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23888 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23888 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7mkaMC  7meiC  7mk9C  7ml0C  7ml1C  7ml2C  7ml3C  7ml4C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23888.map.gz / 形式: CCP4 / 大きさ: 40.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23888.map.gz / 形式: CCP4 / 大きさ: 40.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Leading EC_map_with_sharpening by postprocesssed in Relion | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.08 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_23888_msk_1.map emd_23888_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
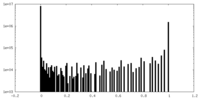
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Leading EC map without sharpening
| ファイル | emd_23888_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Leading EC_map_without_sharpening | ||||||||||||
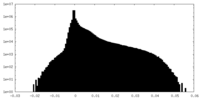
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: EC+EC (leading EC-focused) half map 1
| ファイル | emd_23888_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EC+EC (leading EC-focused) half map 1 | ||||||||||||
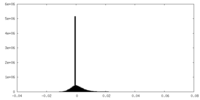
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: EC+EC (leading EC-focused) half map 2
| ファイル | emd_23888_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EC+EC (leading EC-focused) half map 2 | ||||||||||||
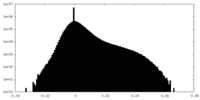
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : The leading EC of complex EC+EC
+超分子 #1: The leading EC of complex EC+EC
+分子 #1: DNA (40-MER)
+分子 #2: DNA (40-MER)
+分子 #3: DNA-directed RNA polymerase subunit
+分子 #4: DNA-directed RNA polymerase subunit beta
+分子 #5: DNA-directed RNA polymerase II subunit RPB3
+分子 #6: DNA-directed RNA polymerase II subunit RPB4
+分子 #7: DNA-directed RNA polymerases I, II, and III subunit RPABC1
+分子 #8: DNA-directed RNA polymerases I,II,and III subunit RPABC2
+分子 #9: DNA-directed RNA polymerase II subunit RPB7
+分子 #10: DNA-directed RNA polymerases I, II, and III subunit RPABC3
+分子 #11: DNA-directed RNA polymerase II subunit RPB9
+分子 #12: DNA-directed RNA polymerases II subunit RPABC5
+分子 #13: DNA-directed RNA polymerase II subunit RPB11
+分子 #14: DNA-directed RNA polymerases II subunit RPABC4
+分子 #15: RNA (5'-R(P*AP*AP*CP*UP*AP*GP*UP*UP*AP*AP*GP*AP*GP*GP*UP*U)-3')
+分子 #16: ZINC ION
+分子 #17: MAGNESIUM ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.0 mg/mL |
|---|---|
| 緩衝液 | pH: 7.6 / 詳細: 20 mM HEPES PH 7.6 50 mM KoAc 5 mM DTT 2 mM MgoAc |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER |
| 凍結 | 凍結剤: ETHANE / 装置: LEICA EM CPC |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 1.25 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.75 µm / 最小 デフォーカス(公称値): 0.75 µm / 倍率(公称値): 81000 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

















 Z
Z Y
Y X
X