+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-23264 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM map of PDX1.2/PDX1.3 co-expression complex (Arabidopsis thaliana) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報response to non-ionic osmotic stress / response to lipid hydroperoxide / chlorophyll metabolic process / pyridoxal 5'-phosphate synthase (glutamine hydrolysing) / pyridoxal 5'-phosphate synthase (glutamine hydrolysing) activity / pyridoxal phosphate biosynthetic process / hyperosmotic salinity response / amino acid metabolic process / response to UV-B / endomembrane system ...response to non-ionic osmotic stress / response to lipid hydroperoxide / chlorophyll metabolic process / pyridoxal 5'-phosphate synthase (glutamine hydrolysing) / pyridoxal 5'-phosphate synthase (glutamine hydrolysing) activity / pyridoxal phosphate biosynthetic process / hyperosmotic salinity response / amino acid metabolic process / response to UV-B / endomembrane system / response to salt stress / response to oxidative stress / protein heterodimerization activity / protein homodimerization activity / plasma membrane / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
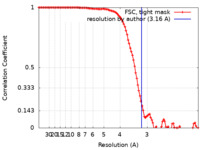
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.16 Å | |||||||||
 データ登録者 データ登録者 | Novikova IV / Evans JE | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: ACS Chem Biol / 年: 2021 ジャーナル: ACS Chem Biol / 年: 2021タイトル: Tunable Heteroassembly of a Plant Pseudoenzyme-Enzyme Complex. 著者: Irina V Novikova / Mowei Zhou / Chen Du / Marcelina Parra / Doo Nam Kim / Zachary L VanAernum / Jared B Shaw / Hanjo Hellmann / Vicki H Wysocki / James E Evans /  要旨: Pseudoenzymes have emerged as key regulatory elements in all kingdoms of life despite being catalytically nonactive. Yet many factors defining why one protein is active while its homologue is ...Pseudoenzymes have emerged as key regulatory elements in all kingdoms of life despite being catalytically nonactive. Yet many factors defining why one protein is active while its homologue is inactive remain uncertain. For pseudoenzyme-enzyme pairs, the similarity of both subunits can often hinder conventional characterization approaches. In plants, a pseudoenzyme, PDX1.2, positively regulates vitamin B production by association with its active catalytic homologues such as PDX1.3 through an unknown assembly mechanism. Here we used an integrative experimental approach to learn that such pseudoenzyme-enzyme pair associations result in heterocomplexes of variable stoichiometry, which are unexpectedly tunable. We also present the atomic structure of the PDX1.2 pseudoenzyme as well as the population averaged PDX1.2-PDX1.3 pseudoenzyme-enzyme pair. Finally, we dissected hetero-dodecamers of each stoichiometry to understand the arrangement of monomers in the heterocomplexes and identified symmetry-imposed preferences in PDX1.2-PDX1.3 interactions. Our results provide a new model of pseudoenzyme-enzyme interactions and their native heterogeneity. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23264.map.gz emd_23264.map.gz | 51.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23264-v30.xml emd-23264-v30.xml emd-23264.xml emd-23264.xml | 11.2 KB 11.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_23264_fsc.xml emd_23264_fsc.xml | 11.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_23264.png emd_23264.png | 82.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23264 http://ftp.pdbj.org/pub/emdb/structures/EMD-23264 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23264 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23264 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_23264_validation.pdf.gz emd_23264_validation.pdf.gz | 361.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_23264_full_validation.pdf.gz emd_23264_full_validation.pdf.gz | 361.5 KB | 表示 | |
| XML形式データ |  emd_23264_validation.xml.gz emd_23264_validation.xml.gz | 12 KB | 表示 | |
| CIF形式データ |  emd_23264_validation.cif.gz emd_23264_validation.cif.gz | 15.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23264 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23264 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23264 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23264 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23264.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23264.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.012 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : PDX1.2/PDX1.3 heterododecamer
| 全体 | 名称: PDX1.2/PDX1.3 heterododecamer |
|---|---|
| 要素 |
|
-超分子 #1: PDX1.2/PDX1.3 heterododecamer
| 超分子 | 名称: PDX1.2/PDX1.3 heterododecamer / タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  |
| 分子量 | 実験値: 445 KDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.2 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 / 詳細: 50 mM Tris, 150 mM NaCl, 4 mM. DTT |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR / 詳細: at 15 mA |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 85 % / チャンバー内温度: 298 K / 装置: LEICA EM GP |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 100.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー