+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-22290 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of a mitochondrial calcium uniporter holocomplex (MICU1, MICU2, MCU, EMRE) in low Ca2+ | |||||||||
 マップデータ マップデータ | main map. Sharpened | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | ion channel / calcium channel / mitochondrial calcium uniporter / MCU / EMRE / mitochondria / TRANSPORT PROTEIN-CALCIUM BINDING PROTEIN complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報mitochondrial crista junction / positive regulation of cristae formation / negative regulation of mitochondrial calcium ion concentration / regulation of cellular hyperosmotic salinity response / uniporter activity / Processing of SMDT1 / mitochondrial calcium ion transmembrane transport / uniplex complex / Mitochondrial calcium ion transport / positive regulation of mitochondrial calcium ion concentration ...mitochondrial crista junction / positive regulation of cristae formation / negative regulation of mitochondrial calcium ion concentration / regulation of cellular hyperosmotic salinity response / uniporter activity / Processing of SMDT1 / mitochondrial calcium ion transmembrane transport / uniplex complex / Mitochondrial calcium ion transport / positive regulation of mitochondrial calcium ion concentration / mitochondrial calcium ion homeostasis / calcium ion sensor activity / calcium import into the mitochondrion / cellular response to calcium ion starvation / calcium ion import / calcium channel inhibitor activity / calcium channel complex / Mitochondrial protein degradation / cellular response to calcium ion / mitochondrial membrane / protein homooligomerization / calcium channel activity / mitochondrial intermembrane space / defense response / mitochondrial inner membrane / protein heterodimerization activity / calcium ion binding / mitochondrion / identical protein binding / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.3 Å | |||||||||
 データ登録者 データ登録者 | Long SB / Wang C | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2020 ジャーナル: Elife / 年: 2020タイトル: Structures reveal gatekeeping of the mitochondrial Ca uniporter by MICU1-MICU2. 著者: Chongyuan Wang / Agata Jacewicz / Bryce D Delgado / Rozbeh Baradaran / Stephen Barstow Long /  要旨: The mitochondrial calcium uniporter is a Ca-gated ion channel complex that controls mitochondrial Ca entry and regulates cell metabolism. MCU and EMRE form the channel while Ca-dependent regulation ...The mitochondrial calcium uniporter is a Ca-gated ion channel complex that controls mitochondrial Ca entry and regulates cell metabolism. MCU and EMRE form the channel while Ca-dependent regulation is conferred by MICU1 and MICU2 through an enigmatic process. We present a cryo-EM structure of an MCU-EMRE-MICU1-MICU2 holocomplex comprising MCU and EMRE subunits from the beetle Tribolium castaneum in complex with a human MICU1-MICU2 heterodimer at 3.3 Å resolution. With analogy to how neuronal channels are blocked by protein toxins, a uniporter interaction domain on MICU1 binds to a channel receptor site comprising MCU and EMRE subunits to inhibit ion flow under resting Ca conditions. A Ca-bound structure of MICU1-MICU2 at 3.1 Å resolution indicates how Ca-dependent changes enable dynamic response to cytosolic Ca signals. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_22290.map.gz emd_22290.map.gz | 74.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-22290-v30.xml emd-22290-v30.xml emd-22290.xml emd-22290.xml | 24 KB 24 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_22290.png emd_22290.png | 65.7 KB | ||
| Filedesc metadata |  emd-22290.cif.gz emd-22290.cif.gz | 6.9 KB | ||
| その他 |  emd_22290_additional_1.map.gz emd_22290_additional_1.map.gz emd_22290_additional_2.map.gz emd_22290_additional_2.map.gz | 3 MB 2.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-22290 http://ftp.pdbj.org/pub/emdb/structures/EMD-22290 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22290 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22290 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_22290_validation.pdf.gz emd_22290_validation.pdf.gz | 480 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_22290_full_validation.pdf.gz emd_22290_full_validation.pdf.gz | 479.6 KB | 表示 | |
| XML形式データ |  emd_22290_validation.xml.gz emd_22290_validation.xml.gz | 6.2 KB | 表示 | |
| CIF形式データ |  emd_22290_validation.cif.gz emd_22290_validation.cif.gz | 7.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22290 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22290 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22290 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22290 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_22290.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_22290.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | main map. Sharpened | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.064 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: sharpened map calculated from the first 6 frames.
| ファイル | emd_22290_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
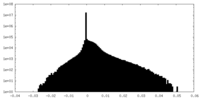
| 注釈 | sharpened map calculated from the first 6 frames. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: unsharpened map
| ファイル | emd_22290_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
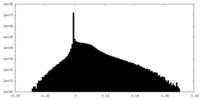
| 注釈 | unsharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Mitochondrial Calcium Uniporter holocomplex
| 全体 | 名称: Mitochondrial Calcium Uniporter holocomplex |
|---|---|
| 要素 |
|
-超分子 #1: Mitochondrial Calcium Uniporter holocomplex
| 超分子 | 名称: Mitochondrial Calcium Uniporter holocomplex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|
-超分子 #2: EMRE
| 超分子 | 名称: EMRE / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #3: MCU
| 超分子 | 名称: MCU / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #4: MICU1-MICU2 heterodimer
| 超分子 | 名称: MICU1-MICU2 heterodimer / タイプ: complex / ID: 4 / 親要素: 1 / 含まれる分子: #3-#4 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Protein EMRE homolog, mitochondrial-like Protein
| 分子 | 名称: Protein EMRE homolog, mitochondrial-like Protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 7.37219 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GPTAAALETA VYSKSGGLLP EPHRTSFGII RLILTVVPGL LIGAAISKNI ANFLEENDLF VPSDDDDDDD UniProtKB: Essential MCU regulator, mitochondrial |
-分子 #2: Calcium uniporter protein
| 分子 | 名称: Calcium uniporter protein / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 23.6341 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GPTAAALERL TTEEVQGLSD VKTLVNQLYE ALNVREHQLQ KEVELTTQLE TLQQELLPLE EKKLELEQVA NRRSNWMAWA GLGLMSVQF GILARLTWWE YSWDIMEPVT YFVTYGTAMA AYAYFVLTRE EYILNDVRDR QQLLLLHKKA KKTGFDVNQY N VLKDQIAK ...文字列: GPTAAALERL TTEEVQGLSD VKTLVNQLYE ALNVREHQLQ KEVELTTQLE TLQQELLPLE EKKLELEQVA NRRSNWMAWA GLGLMSVQF GILARLTWWE YSWDIMEPVT YFVTYGTAMA AYAYFVLTRE EYILNDVRDR QQLLLLHKKA KKTGFDVNQY N VLKDQIAK LELDLKRLRD PLKLRLPPKA AAKEEGGWSH PQFEK UniProtKB: Calcium uniporter protein, mitochondrial |
-分子 #3: Calcium uptake protein 1, mitochondrial
| 分子 | 名称: Calcium uptake protein 1, mitochondrial / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 45.422883 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GPTAAALEPH PEEKKKKRSG FRDRKVMEYE NRIRAYSTPD KIFRYFATLK VISEPGEAEV FMTPEDFVRS ITPNEKQPEH LGLDQYIIK RFDGKKISQE REKFADEGSI FYTLGECGLI SFSDYIFLTT VLSTPQRNFE IAFKMFDLNG DGEVDMEEFE Q VQSIIRSQ ...文字列: GPTAAALEPH PEEKKKKRSG FRDRKVMEYE NRIRAYSTPD KIFRYFATLK VISEPGEAEV FMTPEDFVRS ITPNEKQPEH LGLDQYIIK RFDGKKISQE REKFADEGSI FYTLGECGLI SFSDYIFLTT VLSTPQRNFE IAFKMFDLNG DGEVDMEEFE Q VQSIIRSQ TSMGMRHRDR PTTGNTLKSG LCSALTTYFF GADLKGKLTI KNFLEFQRKL QHDVLKLEFE RHDPVDGRIT ER QFGGMLL AYSGVQSKKL TAMQRQLKKH FKEGKGLTFQ EVENFFTFLK NINDVDTALS FYHMAGASLD KVTMQQVART VAK VELSDH VCDVVFALFD CDGNGELSNK EFVSIMKQRL MRGLEKPKDM GFTRLMQAMW KCAQETAWDF ALPKQSNW UniProtKB: Calcium uptake protein 1, mitochondrial |
-分子 #4: Calcium uptake protein 2, mitochondrial
| 分子 | 名称: Calcium uptake protein 2, mitochondrial / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 44.980609 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: HHSRVSVAAR DGSFTVSAQK NVEHGIIYIG KPSLRKQRFM QFSSLEHEGE YYMTPRDFLF SVMFEQMERK TSVKKLTKKD IEDTLSGIQ TAGCGSTFFR DLGDKGLISY TEYLFLLTIL TKPHSGFHVA FKMLDTDGNE MIEKREFFKL QKIISKQDDL M TVKTNETG ...文字列: HHSRVSVAAR DGSFTVSAQK NVEHGIIYIG KPSLRKQRFM QFSSLEHEGE YYMTPRDFLF SVMFEQMERK TSVKKLTKKD IEDTLSGIQ TAGCGSTFFR DLGDKGLISY TEYLFLLTIL TKPHSGFHVA FKMLDTDGNE MIEKREFFKL QKIISKQDDL M TVKTNETG YQEAIVKEPE INTTLQMRFF GKRGQRKLHY KEFRRFMENL QTEIQEMEFL QFSKGLSFMR KEDFAEWLLF FT NTENKDI YWKNVREKLS AGESISLDEF KSFCHFTTHL EDFAIAMQMF SLAHRPVRLA EFKRAVKVAT GQELSNNILD TVF KIFDLD GDECLSHEEF LGVLKNRMHR GLWVPQHQSI QEYWKCVKKE SIKGVKEVWK QAGKGLF UniProtKB: Calcium uptake protein 2, mitochondrial |
-分子 #5: CALCIUM ION
| 分子 | 名称: CALCIUM ION / タイプ: ligand / ID: 5 / コピー数: 1 / 式: CA |
|---|---|
| 分子量 | 理論値: 40.078 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.0 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV / 詳細: 2 second blot, blot force of 0. | ||||||||||||
| 詳細 | Monodisperse sample |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 検出モード: SUPER-RESOLUTION / デジタル化 - 画像ごとのフレーム数: 1-40 / 撮影したグリッド数: 5 / 実像数: 21115 / 平均露光時間: 4.0 sec. / 平均電子線量: 71.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): -3.0 µm / 最小 デフォーカス(公称値): -1.0 µm / 倍率(公称値): 22500 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 124 / 当てはまり具合の基準: Correlation coefficient |
|---|---|
| 得られたモデル |  PDB-6xqn: |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)