+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of the plant helper NLR NRC2 in its resting state | |||||||||
 マップデータ マップデータ | Please use contour for 0.0034 for atom inclusion. This covers all the main chain atoms in the model | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | NLR protein / Helper NLRl / plant immunity / R-protein / IMMUNE SYSTEM | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.9 Å | |||||||||
 データ登録者 データ登録者 | Selvaraj M / Kamoun S / Contreras MP | |||||||||
| 資金援助 |  英国, 1件 英国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Biorxiv / 年: 2023 ジャーナル: Biorxiv / 年: 2023タイトル: Activation of plant immunity through conversion of a helper NLR homodimer into a resistosome 著者: Selvaraj M / Kamoun S / Contreras MP | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
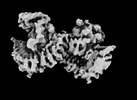
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_19121.map.gz emd_19121.map.gz | 8.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-19121-v30.xml emd-19121-v30.xml emd-19121.xml emd-19121.xml | 19.4 KB 19.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
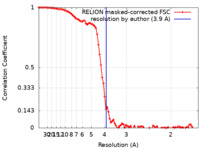
| FSC (解像度算出) |  emd_19121_fsc.xml emd_19121_fsc.xml | 9.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_19121.png emd_19121.png | 57.1 KB | ||
| マスクデータ |  emd_19121_msk_1.map emd_19121_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-19121.cif.gz emd-19121.cif.gz | 7 KB | ||
| その他 |  emd_19121_half_map_1.map.gz emd_19121_half_map_1.map.gz emd_19121_half_map_2.map.gz emd_19121_half_map_2.map.gz | 48.5 MB 48.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-19121 http://ftp.pdbj.org/pub/emdb/structures/EMD-19121 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19121 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19121 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8rfhMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_19121.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_19121.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Please use contour for 0.0034 for atom inclusion. This covers all the main chain atoms in the model | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.828 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_19121_msk_1.map emd_19121_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_19121_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_19121_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : NRC2 heler NLR dimer with ADP
| 全体 | 名称: NRC2 heler NLR dimer with ADP |
|---|---|
| 要素 |
|
-超分子 #1: NRC2 heler NLR dimer with ADP
| 超分子 | 名称: NRC2 heler NLR dimer with ADP / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 詳細: This is helper NLR protein NRC2 in inactive state with ADP nucleotide bound state |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 100 KDa |
-分子 #1: NRC2a
| 分子 | 名称: NRC2a / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 107.522398 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MANVAVEFLV QNLMQLLRDN AELIVGVKDS AESLLQDLND FNAFLKQTAK SRTENDVHKE LVKKIKTVVN SAEDAIDKFV IEAKLHKDK GVGRFVDVKH YKRVYDVAGE IKTIRDKVKE IRLNNALDLQ ALQDEDQSAK GVQERKPPVV EEDDVVGFEE E ADKVINRL ...文字列: MANVAVEFLV QNLMQLLRDN AELIVGVKDS AESLLQDLND FNAFLKQTAK SRTENDVHKE LVKKIKTVVN SAEDAIDKFV IEAKLHKDK GVGRFVDVKH YKRVYDVAGE IKTIRDKVKE IRLNNALDLQ ALQDEDQSAK GVQERKPPVV EEDDVVGFEE E ADKVINRL LGGSSGLEVV PVVGMPGLGK TTLANKIYKH PDIGYQFFTR IWVYVSQSYR RRELFLNIIS KFTRNTKQYH DM CEEDLAD EIEDFLGKGG KYLIVLDDVW SPDAWERIRI AFPNNNKSNR ILLTTRDSKV AKQCKQCIGI PHDLKFLTED ESW ILLEKK VFHKDKCPPE LELSGKSIAK KCNGLPLAIV VIAGALIGKG KTSREWKQVD ESVGEHLINK DQPENCNKLV QLSY DRLSY DLKACFLYCG AFPGGFEIPA WKLIRLWIAE GFIQYKGHLS LECKAEDNLN DLINRNLVMV MQRTSDGQIK TCRLH DMLH EFCRQEAMKE ENLFQEIKLG AEQYFPGKRE LATYRRLCIH SSVLEFISTK PSGEHVRSFL SFSLKKIEMP SVDIPT IPK GFPLLRVFDV ESINFSRFSK EFFQLYHLRY IAFSSDTIKI IPKHIGELWN IQTLIINTQQ RSLDIQANIW NMERLRH LH TNSSAKLPVP VTPRSSKVPL VNQSLQTLST IAPESCTEEV FARTPNLKKL GIRGKIAVLL EPNKSLLKNV KKLESLEN L KLINDSSQTG KGLRLPPSYI FPTKLRKLSL VDTWLEWNDM SILGQMEHLE VLKLKENGFM GECWESVGGF CSLLVLWIE RTDLVSWKAS ADHFPRLKHL VLICCDKLKE IPIGLADIRS FQVMELQNST KTAAISARGI RDKKDKQTQE GTNNNGFKLS IFPPDLGSG SGRGSHHHHH HDYDIPTTAS ENLYFQGELD YKDHDGDYKD HDIDYKDDDD K UniProtKB: NRC2a |
-分子 #2: ADENOSINE-5'-DIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-DIPHOSPHATE / タイプ: ligand / ID: 2 / コピー数: 2 / 式: ADP |
|---|---|
| 分子量 | 理論値: 427.201 Da |
| Chemical component information |  ChemComp-ADP: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.2 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||
| グリッド | モデル: C-flat / 材質: COPPER / 支持フィルム - 材質: GRAPHENE / 支持フィルム - トポロジー: CONTINUOUS / 前処理 - タイプ: GLOW DISCHARGE / 詳細: The grids were negatively glow discharged | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV 詳細: The C-flat grids were coated with grphene oxide, in house and the sample was applied two times inside the vitrobot chamber. | ||||||||||||
| 詳細 | the particles are NRC2 purified from plant after over expression. This was suspended in buffer and cryogrids were made on graphene oxide backing |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 6000 / 平均露光時間: 2.6 sec. / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.7 µm / 最小 デフォーカス(公称値): 1.5 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | Chain - Residue range: 1-880 / Chain - Source name: AlphaFold / Chain - Initial model type: in silico model / 詳細: This is the full length sequence of NRC |
|---|---|
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 温度因子: 100 / 当てはまり具合の基準: CC |
| 得られたモデル |  PDB-8rfh: |
 ムービー
ムービー コントローラー
コントローラー




 Z
Z Y
Y X
X