+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-11698 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Helical structure of PspA | |||||||||
 マップデータ マップデータ | sharpened map from phenix.auto_sharpen | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | PspA / IM30 / Vipp1 / ESCRT-III / helical reconstruction / Cryo-EM / membrane remodeling / LIPID BINDING PROTEIN | |||||||||
| 機能・相同性 | PspA/IM30 / PspA/IM30 family / Chloroplast membrane-associated 30 kD protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  | |||||||||
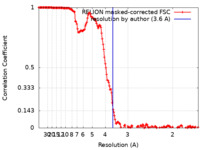
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | |||||||||
 データ登録者 データ登録者 | Junglas B / Huber ST | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2021 ジャーナル: Cell / 年: 2021タイトル: PspA adopts an ESCRT-III-like fold and remodels bacterial membranes. 著者: Benedikt Junglas / Stefan T Huber / Thomas Heidler / Lukas Schlösser / Daniel Mann / Raoul Hennig / Mairi Clarke / Nadja Hellmann / Dirk Schneider / Carsten Sachse /  要旨: PspA is the main effector of the phage shock protein (Psp) system and preserves the bacterial inner membrane integrity and function. Here, we present the 3.6 Å resolution cryoelectron microscopy ...PspA is the main effector of the phage shock protein (Psp) system and preserves the bacterial inner membrane integrity and function. Here, we present the 3.6 Å resolution cryoelectron microscopy (cryo-EM) structure of PspA assembled in helical rods. PspA monomers adopt a canonical ESCRT-III fold in an extended open conformation. PspA rods are capable of enclosing lipids and generating positive membrane curvature. Using cryo-EM, we visualized how PspA remodels membrane vesicles into μm-sized structures and how it mediates the formation of internalized vesicular structures. Hotspots of these activities are zones derived from PspA assemblies, serving as lipid transfer platforms and linking previously separated lipid structures. These membrane fusion and fission activities are in line with the described functional properties of bacterial PspA/IM30/LiaH proteins. Our structural and functional analyses reveal that bacterial PspA belongs to the evolutionary ancestry of ESCRT-III proteins involved in membrane remodeling. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_11698.map.gz emd_11698.map.gz | 202.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-11698-v30.xml emd-11698-v30.xml emd-11698.xml emd-11698.xml | 18.7 KB 18.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_11698_fsc.xml emd_11698_fsc.xml | 16 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_11698.png emd_11698.png | 178.7 KB | ||
| マスクデータ |  emd_11698_msk_1.map emd_11698_msk_1.map | 347.6 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-11698.cif.gz emd-11698.cif.gz | 5.9 KB | ||
| その他 |  emd_11698_additional_1.map.gz emd_11698_additional_1.map.gz emd_11698_half_map_1.map.gz emd_11698_half_map_1.map.gz emd_11698_half_map_2.map.gz emd_11698_half_map_2.map.gz | 325.1 MB 277.7 MB 277.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-11698 http://ftp.pdbj.org/pub/emdb/structures/EMD-11698 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11698 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11698 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_11698.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_11698.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sharpened map from phenix.auto_sharpen | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8389 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_11698_msk_1.map emd_11698_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Guinier sharpened filtered map from Relion Refine3D
| ファイル | emd_11698_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Guinier sharpened filtered map from Relion Refine3D | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: unfiltered unsharpened half map from Relion Refine3D
| ファイル | emd_11698_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | unfiltered unsharpened half map from Relion Refine3D | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: unfiltered unsharpened half map from Relion Refine3D
| ファイル | emd_11698_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | unfiltered unsharpened half map from Relion Refine3D | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Helical filament assembly of PspA
| 全体 | 名称: Helical filament assembly of PspA |
|---|---|
| 要素 |
|
-超分子 #1: Helical filament assembly of PspA
| 超分子 | 名称: Helical filament assembly of PspA / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 25 KDa |
-分子 #1: Chloroplast membrane-associated 30 kD protein
| 分子 | 名称: Chloroplast membrane-associated 30 kD protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: PCC 6803 / Kazusa |
| 分子量 | 理論値: 28.260816 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGHHHHHHHH HSSGHIDDDD KHMELFNRVG RVLKSQLTHW QQQQEAPEDL LERLLGEMEL ELIELRRALA QTIATFKSTE RQRDAQQLI AQRWYEKAQA ALDRGNEQLA REALGQRQSY QSHTEALGKS LGEQRALVEQ VRGQLQKLER KYLELKSQKN L YLARLKSA ...文字列: MGHHHHHHHH HSSGHIDDDD KHMELFNRVG RVLKSQLTHW QQQQEAPEDL LERLLGEMEL ELIELRRALA QTIATFKSTE RQRDAQQLI AQRWYEKAQA ALDRGNEQLA REALGQRQSY QSHTEALGKS LGEQRALVEQ VRGQLQKLER KYLELKSQKN L YLARLKSA IAAQKIEEIA GNLDNASASS LFERIETKIL ELEAERELLN PPPSPLDKKF EQWEEQQAVE ATLAAMKARR SL PPPSS UniProtKB: Chloroplast membrane-associated 30 kD protein |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 濃度 | 7.9 mg/mL |
|---|---|
| 緩衝液 | pH: 7.6 / 構成要素 - 濃度: 10.0 mM / 構成要素 - 式: NaH2PO4 / 構成要素 - 名称: Sodium Phosphate |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 前処理 - タイプ: GLOW DISCHARGE / 詳細: Pelco easiGlow |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 283.15 K / 装置: FEI VITROBOT MARK IV / 詳細: Quantifoil R1.2/1.3 Cu200 grids. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS TALOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm 最大 デフォーカス(公称値): 2.3000000000000003 µm 最小 デフォーカス(公称値): 0.2 µm / 倍率(公称値): 100000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL |
|---|---|
| 得られたモデル |  PDB-7abk: |
 ムービー
ムービー コントローラー
コントローラー










 X (Sec.)
X (Sec.) Y (Row.)
Y (Row.) Z (Col.)
Z (Col.)