+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4260 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Volta phase plate data collection facilitates image processing and cryo-EM structure determination | |||||||||
 マップデータ マップデータ | human 80S ribosome reconstructed from close to focus VPP data, postprocessed map. | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
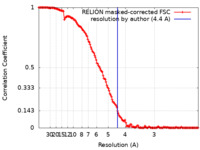
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.4 Å | |||||||||
 データ登録者 データ登録者 | von Loeffelholz O / Klaholz BP / Natchiar SK | |||||||||
 引用 引用 |  ジャーナル: J Struct Biol / 年: 2018 ジャーナル: J Struct Biol / 年: 2018タイトル: Volta phase plate data collection facilitates image processing and cryo-EM structure determination. 著者: Ottilie von Loeffelholz / Gabor Papai / Radostin Danev / Alexander G Myasnikov / S Kundhavai Natchiar / Isabelle Hazemann / Jean-François Ménétret / Bruno P Klaholz /   要旨: A current bottleneck in structure determination of macromolecular complexes by cryo electron microscopy (cryo-EM) is the large amount of data needed to obtain high-resolution 3D reconstructions, ...A current bottleneck in structure determination of macromolecular complexes by cryo electron microscopy (cryo-EM) is the large amount of data needed to obtain high-resolution 3D reconstructions, including through sorting into different conformations and compositions with advanced image processing. Additionally, it may be difficult to visualize small ligands that bind in sub-stoichiometric levels. Volta phase plates (VPP) introduce a phase shift in the contrast transfer and drastically increase the contrast of the recorded low-dose cryo-EM images while preserving high frequency information. Here we present a comparative study to address the behavior of different data sets during image processing and quantify important parameters during structure refinement. The automated data collection was done from the same human ribosome sample either as a conventional defocus range dataset or with a Volta phase plate close to focus (cfVPP) or with a small defocus (dfVPP). The analysis of image processing parameters shows that dfVPP data behave more robustly during cryo-EM structure refinement because particle alignments, Euler angle assignments and 2D & 3D classifications behave more stably and converge faster. In particular, less particle images are required to reach the same resolution in the 3D reconstructions. Finally, we find that defocus range data collection is also applicable to VPP. This study shows that data processing and cryo-EM map interpretation, including atomic model refinement, are facilitated significantly by performing VPP cryo-EM, which will have an important impact on structural biology. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4260.map.gz emd_4260.map.gz | 264.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4260-v30.xml emd-4260-v30.xml emd-4260.xml emd-4260.xml | 9.2 KB 9.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4260_fsc.xml emd_4260_fsc.xml | 14.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4260.png emd_4260.png | 182.7 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4260 http://ftp.pdbj.org/pub/emdb/structures/EMD-4260 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4260 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4260 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_4260_validation.pdf.gz emd_4260_validation.pdf.gz | 357.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_4260_full_validation.pdf.gz emd_4260_full_validation.pdf.gz | 356.9 KB | 表示 | |
| XML形式データ |  emd_4260_validation.xml.gz emd_4260_validation.xml.gz | 14.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4260 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4260 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4260 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4260 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4261C  4262C C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10154 (タイトル: Volta phase plate data collection facilitates image processing and cryo-EM structure determination EMPIAR-10154 (タイトル: Volta phase plate data collection facilitates image processing and cryo-EM structure determinationData size: 89.4 Data #1: Unaligned multi-frame micrographs of human ribosome, collected with VPP close to focus (cfVPP) [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4260.map.gz / 形式: CCP4 / 大きさ: 282.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4260.map.gz / 形式: CCP4 / 大きさ: 282.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | human 80S ribosome reconstructed from close to focus VPP data, postprocessed map. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.09 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : ribosome
| 全体 | 名称: ribosome |
|---|---|
| 要素 |
|
-超分子 #1: ribosome
| 超分子 | 名称: ribosome / タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) / 株: HeLa Homo sapiens (ヒト) / 株: HeLa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.6 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN |
|---|---|
| 特殊光学系 | 位相板: VOLTA PHASE PLATE 球面収差補正装置: CS corrector used, opening up to 13 mrad at 26 mrad tilt エネルギーフィルター - 名称: GIF Quantum LS |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / デジタル化 - サイズ - 横: 7420 pixel / デジタル化 - サイズ - 縦: 7676 pixel / デジタル化 - サンプリング間隔: 5.0 µm / デジタル化 - 画像ごとのフレーム数: 1-29 / 撮影したグリッド数: 1 / 実像数: 433 / 平均露光時間: 4.5 sec. / 平均電子線量: 1.03 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 45871 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 0.01 mm / 最大 デフォーカス(公称値): 0.05 µm / 最小 デフォーカス(公称値): 0.05 µm / 倍率(公称値): 45871 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
 ムービー
ムービー コントローラー
コントローラー