+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | AP2 bound to MSP2N2 nanodisc with Tgn38 cargo peptide; composite map | |||||||||
 マップデータ マップデータ | chimeric map from three focused refinements | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Clathrin-mediated endocytosis / peripheral membrane protein / ENDOCYTOSIS | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Post-translational protein phosphorylation / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / Retrograde transport at the Trans-Golgi-Network / Formation of annular gap junctions / Gap junction degradation / LDL clearance / WNT5A-dependent internalization of FZD2, FZD5 and ROR2 / WNT5A-dependent internalization of FZD4 / Trafficking of GluR2-containing AMPA receptors / Retrograde neurotrophin signalling ...Post-translational protein phosphorylation / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / Retrograde transport at the Trans-Golgi-Network / Formation of annular gap junctions / Gap junction degradation / LDL clearance / WNT5A-dependent internalization of FZD2, FZD5 and ROR2 / WNT5A-dependent internalization of FZD4 / Trafficking of GluR2-containing AMPA receptors / Retrograde neurotrophin signalling / clathrin adaptor complex / clathrin coat / extrinsic component of presynaptic endocytic zone membrane / VLDLR internalisation and degradation / Golgi to endosome transport / Golgi Associated Vesicle Biogenesis / cardiac septum development / Recycling pathway of L1 / AP-2 adaptor complex / regulation of vesicle size / postsynaptic neurotransmitter receptor internalization / Cargo recognition for clathrin-mediated endocytosis / clathrin coat assembly / Cargo recognition for clathrin-mediated endocytosis / positive regulation of synaptic vesicle endocytosis / Clathrin-mediated endocytosis / clathrin adaptor activity / Clathrin-mediated endocytosis / vesicle budding from membrane / membrane coat / clathrin-dependent endocytosis / trans-Golgi network transport vesicle / MHC class II antigen presentation / coronary vasculature development / neurotransmitter receptor internalization / positive regulation of protein localization to membrane / signal sequence binding / aorta development / negative regulation of protein localization to plasma membrane / regulation of hematopoietic stem cell differentiation / ventricular septum development / low-density lipoprotein particle receptor binding / clathrin binding / positive regulation of endocytosis / positive regulation of receptor internalization / synaptic vesicle endocytosis / protein serine/threonine kinase binding / vesicle-mediated transport / Neutrophil degranulation / phosphatidylinositol binding / secretory granule / kidney development / intracellular protein transport / trans-Golgi network / cytoplasmic side of plasma membrane / kinase binding / disordered domain specific binding / synaptic vesicle / heart development / cytoplasmic vesicle / postsynapse / protein-containing complex assembly / transmembrane transporter binding / endosome / protein domain specific binding / intracellular membrane-bounded organelle / glutamatergic synapse / lipid binding / synapse / protein-containing complex binding / protein kinase binding / Golgi apparatus / mitochondrion / membrane / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.3 Å | |||||||||
 データ登録者 データ登録者 | Baker RW / Cannon KS / Reta S | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: J Struct Biol / 年: 2023 ジャーナル: J Struct Biol / 年: 2023タイトル: Lipid nanodiscs as a template for high-resolution cryo-EM structures of peripheral membrane proteins. 著者: Kevin S Cannon / Reta D Sarsam / Tanita Tedamrongwanish / Kevin Zhang / Richard W Baker /  要旨: Peripheral membrane proteins are ubiquitous throughout cell biology and are required for a variety of cellular processes such as signal transduction, membrane trafficking, and autophagy. Transient ...Peripheral membrane proteins are ubiquitous throughout cell biology and are required for a variety of cellular processes such as signal transduction, membrane trafficking, and autophagy. Transient binding to the membrane has a profound impact on protein function, serving to induce conformational changes and alter biochemical and biophysical parameters by increasing the local concentration of factors and restricting diffusion to two dimensions. Despite the centrality of the membrane in serving as a template for cell biology, there are few reported high-resolution structures of peripheral membrane proteins bound to the membrane. We analyzed the utility of lipid nanodiscs to serve as a template for cryo-EM analysis of peripheral membrane proteins. We tested a variety of nanodiscs and we report a 3.3 Å structure of the AP2 clathrin adaptor complex bound to a 17-nm nanodisc, with sufficient resolution to visualize a bound lipid head group. Our data demonstrate that lipid nanodiscs are amenable to high-resolution structure determination of peripheral membrane proteins and provide a framework for extending this analysis to other systems. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_40973.map.gz emd_40973.map.gz | 202.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-40973-v30.xml emd-40973-v30.xml emd-40973.xml emd-40973.xml | 24.8 KB 24.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_40973.png emd_40973.png | 113.3 KB | ||
| Filedesc metadata |  emd-40973.cif.gz emd-40973.cif.gz | 7.6 KB | ||
| その他 |  emd_40973_half_map_1.map.gz emd_40973_half_map_1.map.gz emd_40973_half_map_2.map.gz emd_40973_half_map_2.map.gz | 202.2 MB 202.2 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-40973 http://ftp.pdbj.org/pub/emdb/structures/EMD-40973 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40973 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40973 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_40973_validation.pdf.gz emd_40973_validation.pdf.gz | 861.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_40973_full_validation.pdf.gz emd_40973_full_validation.pdf.gz | 861 KB | 表示 | |
| XML形式データ |  emd_40973_validation.xml.gz emd_40973_validation.xml.gz | 15.9 KB | 表示 | |
| CIF形式データ |  emd_40973_validation.cif.gz emd_40973_validation.cif.gz | 18.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40973 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40973 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40973 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40973 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8t1oMC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_40973.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_40973.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | chimeric map from three focused refinements | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.88 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: Half map 1 of composite map
| ファイル | emd_40973_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 of composite map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 2 of composite map
| ファイル | emd_40973_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 of composite map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : AP2 bound to MSP2N2 nanodisc with Tgn38 cargo peptide
| 全体 | 名称: AP2 bound to MSP2N2 nanodisc with Tgn38 cargo peptide |
|---|---|
| 要素 |
|
-超分子 #1: AP2 bound to MSP2N2 nanodisc with Tgn38 cargo peptide
| 超分子 | 名称: AP2 bound to MSP2N2 nanodisc with Tgn38 cargo peptide タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#5 詳細: Nanodiscs were assembled with a lipid mixture containing 75 mol% DOPC, 15 mol% DOPS, 10 mol% PIP2. Complex was formed by co-elution via gel filtration chromatography. |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 200 KDa |
-分子 #1: AP-2 complex subunit alpha-2
| 分子 | 名称: AP-2 complex subunit alpha-2 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 70.57332 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MPAVSKGDGM RGLAVFISDI RNCKSKEAEI KRINKELANI RSKFKGDKAL DGYSKKKYVC KLLFIFLLGH DIDFGHMEAV NLLSSNRYT EKQIGYLFIS VLVNSNSELI RLINNAIKND LASRNPTFMG LALHCIANVG SREMAEAFAG EIPKILVAGD T MDSVKQSA ...文字列: MPAVSKGDGM RGLAVFISDI RNCKSKEAEI KRINKELANI RSKFKGDKAL DGYSKKKYVC KLLFIFLLGH DIDFGHMEAV NLLSSNRYT EKQIGYLFIS VLVNSNSELI RLINNAIKND LASRNPTFMG LALHCIANVG SREMAEAFAG EIPKILVAGD T MDSVKQSA ALCLLRLYRT SPDLVPMGDW TSRVVHLLND QHLGVVTAAT SLITTLAQKN PEEFKTSVSL AVSRLSRIVT SA STDLQDY TYYFVPAPWL SVKLLRLLQC YPPPEDPAVR GRLTECLETI LNKAQEPPKS KKVQHSNAKN AVLFEAISLI IHH DSEPNL LVRACNQLGQ FLQHRETNLR YLALESMCTL ASSEFSHEAV KTHIETVINA LKTERDVSVR QRAVDLLYAM CDRS NAQQI VAEMLSYLET ADYSIREEIV LKVAILAEKY AVDYTWYVDT ILNLIRIAGD YVSEEVWYRV IQIVINRDDV QGYAA KTVF EALQAPACHE NLVKVGGYIL GEFGNLIAGD PRSSPLIQFN LLHSKFHLCS VPTRALLLST YIKFVNLFPE VKATIQ DVL RSDSQLKNAD VELQQRAVEY LRLSTVASTD ILATVLEEMP PFPERESSIL AKLKKKKGGS GLEVLFQ UniProtKB: AP-2 complex subunit alpha-2 |
-分子 #2: AP-2 complex subunit beta
| 分子 | 名称: AP-2 complex subunit beta / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 66.953195 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MTDSKYFTTN KKGEIFELKA ELNNEKKEKR KEAVKKVIAA MTVGKDVSSL FPDVVNCMQT DNLELKKLVY LYLMNYAKSQ PDMAIMAVN SFVKDCEDPN PLIRALAVRT MGCIRVDKIT EYLCEPLRKC LKDEDPYVRK TAAVCVAKLH DINAQMVEDQ G FLDSLRDL ...文字列: MTDSKYFTTN KKGEIFELKA ELNNEKKEKR KEAVKKVIAA MTVGKDVSSL FPDVVNCMQT DNLELKKLVY LYLMNYAKSQ PDMAIMAVN SFVKDCEDPN PLIRALAVRT MGCIRVDKIT EYLCEPLRKC LKDEDPYVRK TAAVCVAKLH DINAQMVEDQ G FLDSLRDL IADSNPMVVA NAVAALSEIS ESHPNSNLLD LNPQNINKLL TALNECTEWG QIFILDCLSN YNPKDDREAQ SI CERVTPR LSHANSAVVL SAVKVLMKFL ELLPKDSDYY NMLLKKLAPP LVTLLSGEPE VQYVALRNIN LIVQKRPEIL KQE IKVFFV KYNDPIYVKL EKLDIMIRLA SQANIAQVLA ELKEYATEVD VDFVRKAVRA IGRCAIKVEQ SAERCVSTLL DLIQ TKVNY VVQEAIVVIR DIFRKYPNKY ESIIATLCEN LDSLDEPDAR AAMIWIVGEY AERIDNADEL LESFLEGFHD ESTQV QLTL LTAIVKLFLK KPSETQELVQ QVLSLATQDS DNPDLRDRGY IYWRLLSTDP VTAKEVVLSE KPLISEETDL IEPTLL DEL ICHIGSLASV YHKPPNAFVE GSHGIHRK UniProtKB: AP-2 complex subunit beta |
-分子 #3: AP-2 complex subunit mu
| 分子 | 名称: AP-2 complex subunit mu / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 49.726641 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MIGGLFIYNH KGEVLISRVY RDDIGRNAVD AFRVNVIHAR QQVRSPVTNI ARTSFFHVKR SNIWLAAVTK QNVNAAMVFE FLYKMCDVM AAYFGKISEE NIKNNFVLIY ELLDEILDFG YPQNSETGAL KTFITQQGIK SQHQTKEEQS QITSQVTGQI G WRREGIKY ...文字列: MIGGLFIYNH KGEVLISRVY RDDIGRNAVD AFRVNVIHAR QQVRSPVTNI ARTSFFHVKR SNIWLAAVTK QNVNAAMVFE FLYKMCDVM AAYFGKISEE NIKNNFVLIY ELLDEILDFG YPQNSETGAL KTFITQQGIK SQHQTKEEQS QITSQVTGQI G WRREGIKY RRNELFLDVL ESVNLLMSPQ GQVLSAHVSG RVVMKSYLSG MPECKFGMND KIVIEKQGKG TADETSKSGK QS IAIDDCT FHQCVRLSKF DSERSISFIP PDGEFELMRY RTTKDIILPF RVIPLVREVG RTKLEVKVVI KSNFKPSLLA QKI EVRIPT PLNTSGVQVI CMKGKAKYKA SENAIVWKIK RMAGMKESQI SAEIELLPTN DKKKWARPPI SMNFEVPFAP SGLK VRYLK VFEPKLNYSD HDVIKWVRYI GRSGIYETRC UniProtKB: AP-2 complex subunit mu |
-分子 #4: AP-2 complex subunit sigma
| 分子 | 名称: AP-2 complex subunit sigma / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 17.038688 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MIRFILIQNR AGKTRLAKWY MQFDDDEKQK LIEEVHAVVT VRDAKHTNFV EFRNFKIIYR RYAGLYFCIC VDVNDNNLAY LEAIHNFVE VLNEYFHNVC ELDLVFNFYK VYTVVDEMFL AGEIRETSQT KVLKQLLMLQ SLE UniProtKB: AP-2 complex subunit sigma |
-分子 #5: Trans-Golgi network integral membrane protein TGN38
| 分子 | 名称: Trans-Golgi network integral membrane protein TGN38 / タイプ: protein_or_peptide / ID: 5 詳細: Synthesized cargo peptide with an N-terminal oleic acid modification コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 1.723009 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: KVTRRPKASD YQRL UniProtKB: Trans-Golgi network integral membrane protein TGN38 |
-分子 #6: [(2R)-2-octanoyloxy-3-[oxidanyl-[(1R,2R,3S,4R,5R,6S)-2,3,6-tris(o...
| 分子 | 名称: [(2R)-2-octanoyloxy-3-[oxidanyl-[(1R,2R,3S,4R,5R,6S)-2,3,6-tris(oxidanyl)-4,5-diphosphonooxy-cyclohexyl]oxy-phosphoryl]oxy-propyl] octanoate タイプ: ligand / ID: 6 / コピー数: 1 / 式: PIO |
|---|---|
| 分子量 | 理論値: 746.566 Da |
| Chemical component information | 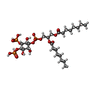 ChemComp-PIO: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 詳細: 20 mM HEPES pH 7.4, 100 mM NaCl |
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: Two applications of sample.. |
| 詳細 | Nanodiscs were assembled with a lipid mixture containing 75 mol% DOPC, 15 mol% DOPS, 10 mol% PIP2. Complex was formed by co-elution via gel filtration chromatography. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 55.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 倍率(補正後): 45000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 45000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





























 Z
Z Y
Y X
X