+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-22518 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SpCas9 delta4CE Ternary Complex | |||||||||
 マップデータ マップデータ | SpCas9 delta4CE Ternary Complex | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | CRISPR-Cas / DNA-binding / engineered / RNA BINDING PROTEIN | |||||||||
| 生物種 |  Streptococcus pyogenes (化膿レンサ球菌) / Streptococcus pyogenes (化膿レンサ球菌) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.2 Å | |||||||||
 データ登録者 データ登録者 | Sham A / Laughlin TG / Savage DF | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Comprehensive deletion landscape of CRISPR-Cas9 identifies minimal RNA-guided DNA-binding modules. 著者: Arik Shams / Sean A Higgins / Christof Fellmann / Thomas G Laughlin / Benjamin L Oakes / Rachel Lew / Shin Kim / Maria Lukarska / Madeline Arnold / Brett T Staahl / Jennifer A Doudna / David F Savage /  要旨: Proteins evolve through the modular rearrangement of elements known as domains. Extant, multidomain proteins are hypothesized to be the result of domain accretion, but there has been limited ...Proteins evolve through the modular rearrangement of elements known as domains. Extant, multidomain proteins are hypothesized to be the result of domain accretion, but there has been limited experimental validation of this idea. Here, we introduce a technique for genetic minimization by iterative size-exclusion and recombination (MISER) for comprehensively making all possible deletions of a protein. Using MISER, we generate a deletion landscape for the CRISPR protein Cas9. We find that the catalytically-dead Streptococcus pyogenes Cas9 can tolerate large single deletions in the REC2, REC3, HNH, and RuvC domains, while still functioning in vitro and in vivo, and that these deletions can be stacked together to engineer minimal, DNA-binding effector proteins. In total, our results demonstrate that extant proteins retain significant modularity from the accretion process and, as genetic size is a major limitation for viral delivery systems, establish a general technique to improve genome editing and gene therapy-based therapeutics. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_22518.map.gz emd_22518.map.gz | 1.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-22518-v30.xml emd-22518-v30.xml emd-22518.xml emd-22518.xml | 26.5 KB 26.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_22518_fsc.xml emd_22518_fsc.xml | 4.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_22518.png emd_22518.png | 93.9 KB | ||
| マスクデータ |  emd_22518_msk_1.map emd_22518_msk_1.map | 8 MB |  マスクマップ マスクマップ | |
| その他 |  emd_22518_additional_1.map.gz emd_22518_additional_1.map.gz emd_22518_additional_2.map.gz emd_22518_additional_2.map.gz emd_22518_additional_3.map.gz emd_22518_additional_3.map.gz emd_22518_half_map_1.map.gz emd_22518_half_map_1.map.gz emd_22518_half_map_2.map.gz emd_22518_half_map_2.map.gz | 4.3 MB 6 MB 5.3 MB 6 MB 6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-22518 http://ftp.pdbj.org/pub/emdb/structures/EMD-22518 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22518 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22518 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_22518_validation.pdf.gz emd_22518_validation.pdf.gz | 628.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_22518_full_validation.pdf.gz emd_22518_full_validation.pdf.gz | 628.4 KB | 表示 | |
| XML形式データ |  emd_22518_validation.xml.gz emd_22518_validation.xml.gz | 10.2 KB | 表示 | |
| CIF形式データ |  emd_22518_validation.cif.gz emd_22518_validation.cif.gz | 13.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22518 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22518 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22518 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22518 | HTTPS FTP |
-関連構造データ
| 類似構造データ | |
|---|---|
| 電子顕微鏡画像生データ |  EMPIAR-10508 (タイトル: Cryo-EM structure of the SpCas9 delta4CE Ternary Complex EMPIAR-10508 (タイトル: Cryo-EM structure of the SpCas9 delta4CE Ternary ComplexData size: 1.5 TB Data #1: Unaligned multi-frame, non-gain-corrected frames in LZW-TIFF of SpCas9 delta4CE Ternary Complex [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_22518.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_22518.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | SpCas9 delta4CE Ternary Complex | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.8 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
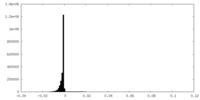
-マスク #1
| ファイル |  emd_22518_msk_1.map emd_22518_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
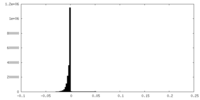
-追加マップ: #3
| ファイル | emd_22518_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: #1
| ファイル | emd_22518_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: #2
| ファイル | emd_22518_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
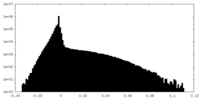
-ハーフマップ: #2
| ファイル | emd_22518_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_22518_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SpCas9 delta4CE Ternary Complex
| 全体 | 名称: SpCas9 delta4CE Ternary Complex |
|---|---|
| 要素 |
|
-超分子 #1: SpCas9 delta4CE Ternary Complex
| 超分子 | 名称: SpCas9 delta4CE Ternary Complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Streptococcus pyogenes (化膿レンサ球菌) Streptococcus pyogenes (化膿レンサ球菌) |
| 分子量 | 理論値: 176.65 KDa |
-分子 #1: SpCas9 delta4CE
| 分子 | 名称: SpCas9 delta4CE / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Streptococcus pyogenes (化膿レンサ球菌) Streptococcus pyogenes (化膿レンサ球菌) |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MKSSHHHHHH ENLYFQSNAT PKKKRKVGGS PKKKRKVGGS PKKKRKVGGS PKKKRKVGIH GVPAATMDKK YSIGLAIGTN SVGWAVITDE YKVPSKKFKV LGNTDRHSIK KNLIGALLFD SGETAEATRL KRTARRRYTR RKNRICYLQE IFSNEMAKVD DSFFHRLEES ...文字列: MKSSHHHHHH ENLYFQSNAT PKKKRKVGGS PKKKRKVGGS PKKKRKVGGS PKKKRKVGIH GVPAATMDKK YSIGLAIGTN SVGWAVITDE YKVPSKKFKV LGNTDRHSIK KNLIGALLFD SGETAEATRL KRTARRRYTR RKNRICYLQE IFSNEMAKVD DSFFHRLEES FLVEEDKKHE RHPIFGNIVD EVAYHEKYPT IYHLRKKLVD STDKADLRLI YLALAHMIKF RGHFLIEGDL NPDNSTSDAI LLSDILRVNT EITKAPLSAS MIKRYDEHHQ DLTLLKALVR QQLPEKYKEI FFDQSKNGYA GYIDGGASQE EFYKFIKPIL EKMDGTEELL VKLNREDLLR KQRTFDNGSI PHQIHLGELH AILRRQEDFY PFLKDNREKI EKILTFRIPY YVGPLARGNS RFAWMTRKSE ETITPWNFEE VVDKGASAQS FIERMTNFDK NLTSQKAQVS GQGDSLHEHI ANLAGSPAIK KGILQTVKVV DELVKVMGRH KPENIVIEMA RENQTTQKGQ KNSRERMKRI EEGIKELASD NLTKAERGGL SELDKAGFIK RQLVETRQIT KHVAQILDSR MNTKYDENDK LIREVKVITL KSKLVSDFRK DFQFYKVREI NNYHHAHDAY LNAVVGTALI KKYPKLESEF VASTVRKVLS MPQVNIVKKT EVQTGGFSKE SILPKRNSDK LIARKKDWDP KKYGGFDSPT VAYSVLVVAK VEKGKSKKLK SVKELLGITI MERSSFEKNP IDFLEAKGYK EVKKDLIIKL PKYSLFELEN GRKRMLASAG ELQKGNELAL PSKYVNFLYL ASHYEKLKGS PEDNEQKQLF VEQHKHYLDE IIEQISEFSK RVILADANLD KVLSAYNKHR DKPIREQAEN IIHLFTLTNL GAPAAFKYFD TTIDRKRYTS TKEVLDATLI HQSITGLYET RIDLSQLGGD GSPKKKRKVE DPKKKRKVDT QSPKGS |
-分子 #2: sgRNA
| 分子 | 名称: sgRNA / タイプ: rna / ID: 2 |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: UCAGCCACAG CUGGGCCUGG GUUUUAGAGC UAGAAAUAGC AAGUUAAAAU AAGGCUAGUC CGUUAUCAAC UUGAAAAAGU GGCACCGAGU CGGUGCUUUU |
-分子 #3: Target-strand
| 分子 | 名称: Target-strand / タイプ: dna / ID: 3 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: CTCACCTTCC TACGGTAGTC GGTGTCGACC CGGACCACCC GACAGTTTTA ACTCG |
-分子 #4: Non-target strand
| 分子 | 名称: Non-target strand / タイプ: dna / ID: 4 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: GAGTGGAAGG ATGCCATCAG CCACAGCTGG GCCTGGTGGG CTGTCAAAAT TGAGC |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.0053 mg/mL | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 支持フィルム - #0 - Film type ID: 1 / 支持フィルム - #0 - 材質: CARBON / 支持フィルム - #0 - トポロジー: HOLEY / 支持フィルム - #1 - Film type ID: 2 / 支持フィルム - #1 - 材質: CARBON / 支持フィルム - #1 - トポロジー: CONTINUOUS / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 15 sec. / 前処理 - 雰囲気: OTHER | ||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 289 K / 装置: FEI VITROBOT MARK IV / 詳細: 10 s incubation, blot 5 seconds. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 3400 / 平均電子線量: 60.0 e/Å2 詳細: collected using image-shift for a regular 3x3 array of holes per stage movement |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm 最大 デフォーカス(補正後): 3.8000000000000003 µm 最小 デフォーカス(補正後): 1.5 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 倍率(公称値): 45000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 温度因子: 395 / 当てはまり具合の基準: CC |
 ムービー
ムービー コントローラー
コントローラー












 Z
Z Y
Y X
X