+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | U2 snRNP after ATP-dependent remodelling | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | snRNP / Spliceosome / U2 snRNP / Splicing / NUCLEAR PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報U11/U12 snRNP / B-WICH complex / splicing factor binding / U12-type spliceosomal complex / RNA splicing, via transesterification reactions / U2-type spliceosomal complex / U2-type precatalytic spliceosome / U2-type prespliceosome assembly / U2 snRNP / SAGA complex ...U11/U12 snRNP / B-WICH complex / splicing factor binding / U12-type spliceosomal complex / RNA splicing, via transesterification reactions / U2-type spliceosomal complex / U2-type precatalytic spliceosome / U2-type prespliceosome assembly / U2 snRNP / SAGA complex / positive regulation of transcription by RNA polymerase III / U2-type prespliceosome / positive regulation of transcription by RNA polymerase I / precatalytic spliceosome / spliceosomal complex assembly / mRNA Splicing - Minor Pathway / regulation of RNA splicing / mRNA 3'-splice site recognition / U2 snRNA binding / regulation of DNA repair / catalytic step 2 spliceosome / mRNA Splicing - Major Pathway / RNA splicing / stem cell differentiation / spliceosomal complex / B-WICH complex positively regulates rRNA expression / negative regulation of protein catabolic process / mRNA processing / nuclear matrix / positive regulation of neuron projection development / mRNA splicing, via spliceosome / nuclear speck / chromatin remodeling / mRNA binding / protein-containing complex binding / nucleolus / positive regulation of DNA-templated transcription / positive regulation of transcription by RNA polymerase II / DNA binding / RNA binding / zinc ion binding / nucleoplasm / nucleus 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
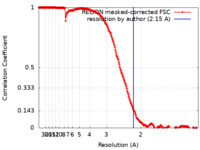
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.15 Å | |||||||||
 データ登録者 データ登録者 | Tholen J / Galej WP | |||||||||
| 資金援助 | European Union, 1件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2022 ジャーナル: Science / 年: 2022タイトル: Structural basis of branch site recognition by the human spliceosome. 著者: Jonas Tholen / Michal Razew / Felix Weis / Wojciech P Galej /   要旨: Recognition of the intron branch site (BS) by the U2 small nuclear ribonucleoprotein (snRNP) is a critical event during spliceosome assembly. In mammals, BS sequences are poorly conserved, and ...Recognition of the intron branch site (BS) by the U2 small nuclear ribonucleoprotein (snRNP) is a critical event during spliceosome assembly. In mammals, BS sequences are poorly conserved, and unambiguous intron recognition cannot be achieved solely through a base-pairing mechanism. We isolated human 17 U2 snRNP and reconstituted in vitro its adenosine 5´-triphosphate (ATP)–dependent remodeling and binding to the pre–messenger RNA substrate. We determined a series of high-resolution (2.0 to 2.2 angstrom) structures providing snapshots of the BS selection process. The substrate-bound U2 snRNP shows that SF3B6 stabilizes the BS:U2 snRNA duplex, which could aid binding of introns with poor sequence complementarity. ATP-dependent remodeling uncoupled from substrate binding captures U2 snRNA in a conformation that competes with BS recognition, providing a selection mechanism based on branch helix stability. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_13812.map.gz emd_13812.map.gz | 809.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-13812-v30.xml emd-13812-v30.xml emd-13812.xml emd-13812.xml | 32.9 KB 32.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_13812_fsc.xml emd_13812_fsc.xml | 22.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_13812.png emd_13812.png | 97.3 KB | ||
| マスクデータ |  emd_13812_msk_1.map emd_13812_msk_1.map | 1000 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-13812.cif.gz emd-13812.cif.gz | 9.6 KB | ||
| その他 |  emd_13812_additional_1.map.gz emd_13812_additional_1.map.gz emd_13812_half_map_1.map.gz emd_13812_half_map_1.map.gz emd_13812_half_map_2.map.gz emd_13812_half_map_2.map.gz | 935.7 MB 815.4 MB 818 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-13812 http://ftp.pdbj.org/pub/emdb/structures/EMD-13812 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13812 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13812 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_13812_validation.pdf.gz emd_13812_validation.pdf.gz | 908 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_13812_full_validation.pdf.gz emd_13812_full_validation.pdf.gz | 907.6 KB | 表示 | |
| XML形式データ |  emd_13812_validation.xml.gz emd_13812_validation.xml.gz | 30.8 KB | 表示 | |
| CIF形式データ |  emd_13812_validation.cif.gz emd_13812_validation.cif.gz | 41 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13812 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13812 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13812 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13812 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7q4pMC  7q3lC  7q4oC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
| 電子顕微鏡画像生データ |  EMPIAR-11000 (タイトル: Cryo-EM structure of human U2 snRNP after ATP-dependent remodeling EMPIAR-11000 (タイトル: Cryo-EM structure of human U2 snRNP after ATP-dependent remodelingData size: 1.5 TB Data #1: Unaligned multi-frame micrographs of the U2 snRNP after ATP-dependent remodeling [micrographs - multiframe] Data #2: Final polished particles of the U2 snRNP after ATP-dependent remodeling [picked particles - single frame - processed]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_13812.map.gz / 形式: CCP4 / 大きさ: 1000 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_13812.map.gz / 形式: CCP4 / 大きさ: 1000 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.64 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_13812_msk_1.map emd_13812_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Map postprocessed in relion with -37 B-factor.
| ファイル | emd_13812_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map postprocessed in relion with -37 B-factor. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_13812_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_13812_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Remodelled U2 snRNP
+超分子 #1: Remodelled U2 snRNP
+分子 #1: Splicing factor 3A subunit 2
+分子 #3: Splicing factor 3A subunit 3
+分子 #4: Splicing factor 3B subunit 1
+分子 #5: Splicing factor 3B subunit 2
+分子 #6: Splicing factor 3B subunit 3
+分子 #7: Splicing factor 3B subunit 5
+分子 #8: PHD finger-like domain-containing protein 5A
+分子 #2: U2 snRNA
+分子 #9: ZINC ION
+分子 #10: water
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.3 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.9 構成要素:
詳細: Sample after desalting may have also contained up to 5% glycerol. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) デジタル化 - サイズ - 横: 5760 pixel / デジタル化 - サイズ - 縦: 4092 pixel / 撮影したグリッド数: 2 / 実像数: 15531 / 平均露光時間: 1.0 sec. / 平均電子線量: 53.45 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: OTHER / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル |
| ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 空間: RECIPROCAL | ||||||||||||||||||
| 得られたモデル |  PDB-7q4p: |
 ムービー
ムービー コントローラー
コントローラー


















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)