+ データを開く
データを開く
- 基本情報
基本情報
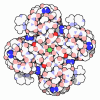
| 登録情報 | データベース: PDB / ID: 7b5y | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | S. agalactiae BusR in complex with its busAB-promotor DNA | |||||||||
 要素 要素 |
| |||||||||
 キーワード キーワード | DNA BINDING PROTEIN / Repressor / complex / GntR | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報monoatomic cation transmembrane transporter activity / potassium ion transport / DNA-binding transcription factor activity / DNA binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Streptococcus agalactiae (バクテリア) Streptococcus agalactiae (バクテリア) | |||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.1 Å | |||||||||
 データ登録者 データ登録者 | Bandera, A.M. / Witte, G. | |||||||||
| 資金援助 |  ドイツ, 2件 ドイツ, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2021 ジャーナル: Nucleic Acids Res / 年: 2021タイトル: BusR senses bipartite DNA binding motifs by a unique molecular ruler architecture. 著者: Adrian M Bandera / Joseph Bartho / Katja Lammens / David Jan Drexler / Jasmin Kleinschwärzer / Karl-Peter Hopfner / Gregor Witte /  要旨: The cyclic dinucleotide second messenger c-di-AMP is a major player in regulation of potassium homeostasis and osmolyte transport in a variety of bacteria. Along with various direct interactions with ...The cyclic dinucleotide second messenger c-di-AMP is a major player in regulation of potassium homeostasis and osmolyte transport in a variety of bacteria. Along with various direct interactions with proteins such as potassium channels, the second messenger also specifically binds to transcription factors, thereby altering the processes in the cell on the transcriptional level. We here describe the structural and biochemical characterization of BusR from the human pathogen Streptococcus agalactiae. BusR is a member of a yet structurally uncharacterized subfamily of the GntR family of transcription factors that downregulates transcription of the genes for the BusA (OpuA) glycine-betaine transporter upon c-di-AMP binding. We report crystal structures of full-length BusR, its apo and c-di-AMP bound effector domain, as well as cryo-EM structures of BusR bound to its operator DNA. Our structural data, supported by biochemical and biophysical data, reveal that BusR utilizes a unique domain assembly with a tetrameric coiled-coil in between the binding platforms, serving as a molecular ruler to specifically recognize a 22 bp separated bipartite binding motif. Binding of c-di-AMP to BusR induces a shift in equilibrium from an inactivated towards an activated state that allows BusR to bind the target DNA, leading to transcriptional repression. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7b5y.cif.gz 7b5y.cif.gz | 198.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7b5y.ent.gz pdb7b5y.ent.gz | 153.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7b5y.json.gz 7b5y.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/b5/7b5y https://data.pdbj.org/pub/pdb/validation_reports/b5/7b5y ftp://data.pdbj.org/pub/pdb/validation_reports/b5/7b5y ftp://data.pdbj.org/pub/pdb/validation_reports/b5/7b5y | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  12051MC  7b5tC  7b5uC  7b5wC  7oz3C C: 同じ文献を引用 ( M: このデータのモデリングに利用したマップデータ |
|---|---|
| 類似構造データ | |
| その他のデータベース |
|
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 23880.160 Da / 分子数: 4 / 由来タイプ: 組換発現 / 詳細: N-terminal residues GP result from purification tag 由来: (組換発現)  Streptococcus agalactiae (バクテリア) Streptococcus agalactiae (バクテリア)遺伝子: BM110_ORF1201, AX245_01365, C6N10_09995, F5043_05515, GD434_05225, RDF_1124 発現宿主:  #2: DNA鎖 | | 分子量: 14309.208 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  Streptococcus agalactiae (バクテリア) Streptococcus agalactiae (バクテリア)#3: DNA鎖 | | 分子量: 14020.027 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  Streptococcus agalactiae (バクテリア) Streptococcus agalactiae (バクテリア)#4: 化合物 | 研究の焦点であるリガンドがあるか | Y | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 0.123 MDa / 実験値: YES | ||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||
| 緩衝液 | pH: 6.5 / 詳細: degassed, filtered | ||||||||||||||||||||||||
| 緩衝液成分 | 濃度: 20 mM / 名称: hepes / 式: HEPES | ||||||||||||||||||||||||
| 試料 | 濃度: 0.5 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES / 詳細: homogeneous and monodisperse sample | ||||||||||||||||||||||||
| 試料支持 | グリッドの材料: GOLD / グリッドのサイズ: 200 divisions/in. / グリッドのタイプ: UltrAuFoil R2/2 | ||||||||||||||||||||||||
| 急速凍結 | 装置: LEICA EM GP / 凍結剤: ETHANE / 湿度: 95 % / 凍結前の試料温度: 283 K 詳細: 0.05% beta-octyl glycoside added prior to plunge freezing |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 45 e/Å2 / 検出モード: COUNTING フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 370421 / 詳細: CryoSparc blob-picker | ||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 7.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 20342 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: RIGID BODY FIT / 空間: REAL | ||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 7B5T Accession code: 7B5T / Source name: PDB / タイプ: experimental model |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj