+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4zs0 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Human Aurora A catalytic domain bound to SB-6-OH | |||||||||
 Components Components | Aurora kinase A | |||||||||
 Keywords Keywords | TRANSFERASE / Aurora / kinase / inhibitor | |||||||||
| Function / homology |  Function and homology information Function and homology informationInteraction between PHLDA1 and AURKA / regulation of centrosome cycle / axon hillock / spindle assembly involved in female meiosis I / cilium disassembly / spindle pole centrosome / histone H3S10 kinase activity / chromosome passenger complex / positive regulation of oocyte maturation / mitotic centrosome separation ...Interaction between PHLDA1 and AURKA / regulation of centrosome cycle / axon hillock / spindle assembly involved in female meiosis I / cilium disassembly / spindle pole centrosome / histone H3S10 kinase activity / chromosome passenger complex / positive regulation of oocyte maturation / mitotic centrosome separation / pronucleus / germinal vesicle / protein localization to centrosome / meiotic spindle / anterior/posterior axis specification / spindle organization / neuron projection extension / centrosome localization / positive regulation of mitochondrial fission / mitotic spindle pole / spindle midzone / SUMOylation of DNA replication proteins / negative regulation of protein binding / regulation of G2/M transition of mitotic cell cycle / positive regulation of mitotic nuclear division / protein serine/threonine/tyrosine kinase activity / positive regulation of mitotic cell cycle / liver regeneration / TP53 Regulates Transcription of Genes Involved in G2 Cell Cycle Arrest / molecular function activator activity / AURKA Activation by TPX2 / peptidyl-serine phosphorylation / regulation of signal transduction by p53 class mediator / mitotic spindle organization / regulation of cytokinesis / centriole / regulation of protein stability / APC/C:Cdh1 mediated degradation of Cdc20 and other APC/C:Cdh1 targeted proteins in late mitosis/early G1 / FBXL7 down-regulates AURKA during mitotic entry and in early mitosis / response to wounding / kinetochore / G2/M transition of mitotic cell cycle / spindle / spindle pole / mitotic spindle / protein autophosphorylation / Regulation of PLK1 Activity at G2/M Transition / mitotic cell cycle / positive regulation of proteasomal ubiquitin-dependent protein catabolic process / microtubule cytoskeleton / midbody / Regulation of TP53 Activity through Phosphorylation / basolateral plasma membrane / protein phosphorylation / microtubule / proteasome-mediated ubiquitin-dependent protein catabolic process / protein kinase activity / non-specific serine/threonine protein kinase / postsynaptic density / ciliary basal body / protein heterodimerization activity / negative regulation of gene expression / protein serine kinase activity / cell division / protein serine/threonine kinase activity / apoptotic process / ubiquitin protein ligase binding / centrosome / protein kinase binding / negative regulation of apoptotic process / perinuclear region of cytoplasm / glutamatergic synapse / nucleoplasm / ATP binding / nucleus / cytosol Similarity search - Function | |||||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | |||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 3 Å MOLECULAR REPLACEMENT / Resolution: 3 Å | |||||||||
 Authors Authors | Marcaida, M.J. / Kilchmann, F. / Schick, T. / Reymond, J.L. | |||||||||
| Funding support |  Switzerland, 2items Switzerland, 2items
| |||||||||
 Citation Citation |  Journal: J.Med.Chem. / Year: 2016 Journal: J.Med.Chem. / Year: 2016Title: Discovery of a Selective Aurora A Kinase Inhibitor by Virtual Screening. Authors: Kilchmann, F. / Marcaida, M.J. / Kotak, S. / Schick, T. / Boss, S.D. / Awale, M. / Gonczy, P. / Reymond, J.L. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4zs0.cif.gz 4zs0.cif.gz | 121.4 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4zs0.ent.gz pdb4zs0.ent.gz | 94.4 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4zs0.json.gz 4zs0.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/zs/4zs0 https://data.pdbj.org/pub/pdb/validation_reports/zs/4zs0 ftp://data.pdbj.org/pub/pdb/validation_reports/zs/4zs0 ftp://data.pdbj.org/pub/pdb/validation_reports/zs/4zs0 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  4ztqC  4ztrC  4ztsC  1ol5S S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein | Mass: 32948.781 Da / Num. of mol.: 1 / Fragment: Catalytic domain, UNP residues 122-403 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) Homo sapiens (human)Gene: AURKA, AIK, AIRK1, ARK1, AURA, AYK1, BTAK, IAK1, STK15, STK6 Production host:  References: UniProt: O14965, non-specific serine/threonine protein kinase |
|---|---|
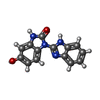
| #2: Chemical | ChemComp-4QV / |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION X-RAY DIFFRACTION |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.58 Å3/Da / Density % sol: 52.4 % |
|---|---|
| Crystal grow | Temperature: 291 K / Method: vapor diffusion, hanging drop / pH: 8 / Details: 4% v/v Tacsimate pH 8.0, 12% w/v PEG 3350 |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06DA / Wavelength: 1 Å / Beamline: X06DA / Wavelength: 1 Å |
| Detector | Type: DECTRIS PILATUS 2M / Detector: PIXEL / Date: Dec 5, 2013 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1 Å / Relative weight: 1 |
| Reflection | Resolution: 3→44.4 Å / Num. obs: 7543 / % possible obs: 99.97 % / Redundancy: 8.8 % / Rmerge(I) obs: 0.076 / Net I/σ(I): 18.5 |
| Reflection shell | Resolution: 3→3.1 Å / Redundancy: 8.3 % / Rmerge(I) obs: 0.6 / Mean I/σ(I) obs: 3.5 / % possible all: 100 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 1OL5 Resolution: 3→44.4 Å / Cor.coef. Fo:Fc: 0.932 / Cor.coef. Fo:Fc free: 0.912 / SU B: 46.074 / SU ML: 0.374 / Cross valid method: THROUGHOUT / ESU R Free: 0.413 / Stereochemistry target values: MAXIMUM LIKELIHOOD / Details: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.2 Å / Solvent model: MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 87.831 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: 1 / Resolution: 3→44.4 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
|
 Movie
Movie Controller
Controller



















 PDBj
PDBj