+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | MicroED structure of the C11 cysteine protease clostripain | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Hydrolase / protease / thiol protease | |||||||||
| 機能・相同性 | clostripain / Peptidase C11, Clostripain Clostridium species / Peptidase C11, clostripain / Clostripain family / cysteine-type endopeptidase activity / proteolysis / Clostripain 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Hathewaya histolytica (バクテリア) Hathewaya histolytica (バクテリア) | |||||||||
| 手法 | 電子線結晶学 / クライオ電子顕微鏡法 / 解像度: 2.5 Å | |||||||||
 データ登録者 データ登録者 | Ruma YN / Bu G / Hattne J / Gonen T | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: J Struct Biol X / 年: 2024 ジャーナル: J Struct Biol X / 年: 2024タイトル: MicroED structure of the C11 cysteine protease clostripain. 著者: Yasmeen N Ruma / Guanhong Bu / Johan Hattne / Tamir Gonen /  要旨: Clostripain secreted from is the founding member of the C11 family of Clan CD cysteine peptidases, which is an important group of peptidases secreted by numerous bacteria. Clostripain is an arginine- ...Clostripain secreted from is the founding member of the C11 family of Clan CD cysteine peptidases, which is an important group of peptidases secreted by numerous bacteria. Clostripain is an arginine-specific endopeptidase. Because of its efficacy as a cysteine peptidase, it is widely used in laboratory settings. Despite its importance the structure of clostripain remains unsolved. Here we describe the first structure of an active form of clostripain determined at 2.5 Å resolution using microcrystal electron diffraction (MicroED). The structure was determined from a single nanocrystal after focused ion beam milling. The structure of clostripain shows a typical Clan CD α/β/α sandwich architecture and the Cys231/His176 catalytic dyad in the active site. It has a large electronegative substrate binding pocket showing its ability to accommodate large and diverse substrates. A loop in the heavy chain formed between residues 452 and 457 is potentially important for substrate binding. In conclusion, this result demonstrates the importance of MicroED to determine the unknown structure of macromolecules such as clostripain, which can be further used as a platform to study substrate binding and design of potential inhibitors against this class of peptidases. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
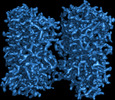
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_45623.map.gz emd_45623.map.gz | 4.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-45623-v30.xml emd-45623-v30.xml emd-45623.xml emd-45623.xml | 15.1 KB 15.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_45623.png emd_45623.png | 204.3 KB | ||
| Filedesc metadata |  emd-45623.cif.gz emd-45623.cif.gz | 6.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-45623 http://ftp.pdbj.org/pub/emdb/structures/EMD-45623 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-45623 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-45623 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_45623_validation.pdf.gz emd_45623_validation.pdf.gz | 616.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_45623_full_validation.pdf.gz emd_45623_full_validation.pdf.gz | 615.7 KB | 表示 | |
| XML形式データ |  emd_45623_validation.xml.gz emd_45623_validation.xml.gz | 4.4 KB | 表示 | |
| CIF形式データ |  emd_45623_validation.cif.gz emd_45623_validation.cif.gz | 4.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45623 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45623 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45623 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45623 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9cipMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_45623.map.gz / 形式: CCP4 / 大きさ: 5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_45623.map.gz / 形式: CCP4 / 大きさ: 5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ |
| ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 18 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Clostripain
| 全体 | 名称: Clostripain |
|---|---|
| 要素 |
|
-超分子 #1: Clostripain
| 超分子 | 名称: Clostripain / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Hathewaya histolytica (バクテリア) Hathewaya histolytica (バクテリア) |
| 分子量 | 理論値: 59 KDa |
-分子 #1: Clostripain
| 分子 | 名称: Clostripain / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Hathewaya histolytica (バクテリア) Hathewaya histolytica (バクテリア) |
| 分子量 | 理論値: 59.805293 KDa |
| 配列 | 文字列: MLRRKVSTLL MTALITTSFL NSKPVYANPV TKSKDNNLKE VQQVTSKSNK NKNQKVTIMY YCDADNNLEG SLLNDIEEMK TGYKDSPNL NLIALVDRSP RYSSDEKVLG EDFSDTRLYK IEHNKANRLD GKNEFPEIST TSKYEANMGD PEVLKKFIDY C KSNYEADK ...文字列: MLRRKVSTLL MTALITTSFL NSKPVYANPV TKSKDNNLKE VQQVTSKSNK NKNQKVTIMY YCDADNNLEG SLLNDIEEMK TGYKDSPNL NLIALVDRSP RYSSDEKVLG EDFSDTRLYK IEHNKANRLD GKNEFPEIST TSKYEANMGD PEVLKKFIDY C KSNYEADK YVLIMANHGG GAREKSNPRL NRAICWDDSN LDKNGEADCL YMGEISDHLT EKQSVDLLAF DACLMGTAEV AY QYRPGNG GFSADTLVAS SPVVWGPGFK YDKIFDRIKA GGGTNNEDDL TLGGKEQNFD PATITNEQLG ALFVEEQRDS THA NGRYDQ HLSFYDLKKA ESVKRAIDNL AVNLSNENKK SEIEKLRGSG IHTDLMHYFD EYSEGEWVEY PYFDVYDLCE KINK SENFS SKTKDLASNA MNKLNEMIVY SFGDPSNNFK EGKNGLSIFL PNGDKKYSTY YTSTKIPHWT MQSWYNSIDT VKYGL NPYG KLSWCKDGQD PEINKVGNWF ELLDSWFDKT NDVTGGVNHY QW UniProtKB: Clostripain |
-分子 #2: SODIUM ION
| 分子 | 名称: SODIUM ION / タイプ: ligand / ID: 2 / コピー数: 7 |
|---|---|
| 分子量 | 理論値: 22.99 Da |
-分子 #3: water
| 分子 | 名称: water / タイプ: ligand / ID: 3 / コピー数: 6 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 電子線結晶学 |
| 試料の集合状態 | 3D array |
- 試料調製
試料調製
| 緩衝液 | pH: 5.6 構成要素:
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: Quantifoil R2/2 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 45 sec. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 293 K / 装置: LEICA EM GP | ||||||||||||
| 結晶化 | 温度: 293.0 K / 時間: 1.0 DAY |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 93.0 K / 最高: 93.0 K |
| 特殊光学系 | エネルギーフィルター - 名称: TFS Selectris / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 1 / 実像数: 252 / 回折像の数: 252 / 平均露光時間: 5.0 sec. / 平均電子線量: 0.04 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: DIFFRACTION / 最大 デフォーカス(公称値): 0.0 µm / 最小 デフォーカス(公称値): 0.0 µm / カメラ長: 2500 mm |
| 試料ステージ | ホルダー冷却材: NITROGEN / 傾斜角度: -20.0, 70.0 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.5 Å / 解像度の算出法: DIFFRACTION PATTERN/LAYERLINES |
|---|---|
| Molecular replacement | ソフトウェア - 名称: PHENIX (ver. 1.21.1_5287) |
| Merging software list | ソフトウェア - 名称: XSCALE (ver. Jun 30, 2023) |
| Crystallography statistics | Number intensities measured: 131476 / Number structure factors: 32113 / Fourier space coverage: 86.8 / R merge: 0.279 / Overall phase error: 34.49 / Overall phase residual: 0 / Phase error rejection criteria: 0 / High resolution: 2.5 Å / 殻 - Shell ID: 1 / 殻 - High resolution: 2.5 Å / 殻 - Low resolution: 2.56 Å / 殻 - Number structure factors: 2318 / 殻 - Phase residual: 54.5 / 殻 - Fourier space coverage: 86.5 / 殻 - Multiplicity: 4.1 |
 ムービー
ムービー コントローラー
コントローラー



 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)