+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of human claudin-4 complex with Clostridium perfringens enterotoxin C-terminal domain and sFab COP-1 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  Claudin (クローディン) / Claudin (クローディン) /  Fab / Fab /  Toxin (毒素) / Toxin (毒素) /  MEMBRANE PROTEIN (膜タンパク質) MEMBRANE PROTEIN (膜タンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of metallopeptidase activity / calcium-independent cell-cell adhesion via plasma membrane cell-adhesion molecules / Tight junction interactions / bicellular tight junction assembly / apicolateral plasma membrane / regulation of cell morphogenesis /  密着結合 / positive regulation of wound healing / renal absorption / 密着結合 / positive regulation of wound healing / renal absorption /  chloride channel activity ...positive regulation of metallopeptidase activity / calcium-independent cell-cell adhesion via plasma membrane cell-adhesion molecules / Tight junction interactions / bicellular tight junction assembly / apicolateral plasma membrane / regulation of cell morphogenesis / chloride channel activity ...positive regulation of metallopeptidase activity / calcium-independent cell-cell adhesion via plasma membrane cell-adhesion molecules / Tight junction interactions / bicellular tight junction assembly / apicolateral plasma membrane / regulation of cell morphogenesis /  密着結合 / positive regulation of wound healing / renal absorption / 密着結合 / positive regulation of wound healing / renal absorption /  chloride channel activity / chloride channel activity /  chloride channel complex / lateral plasma membrane / bicellular tight junction / establishment of skin barrier / basal plasma membrane / response to progesterone / female pregnancy / chloride channel complex / lateral plasma membrane / bicellular tight junction / establishment of skin barrier / basal plasma membrane / response to progesterone / female pregnancy /  概日リズム / transmembrane signaling receptor activity / cell-cell junction / 概日リズム / transmembrane signaling receptor activity / cell-cell junction /  toxin activity / toxin activity /  細胞接着 / positive regulation of cell migration / apical plasma membrane / structural molecule activity / extracellular region / identical protein binding / 細胞接着 / positive regulation of cell migration / apical plasma membrane / structural molecule activity / extracellular region / identical protein binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) / Homo sapiens (ヒト) /   Clostridium perfringens (ウェルシュ菌) / synthetic construct (人工物) Clostridium perfringens (ウェルシュ菌) / synthetic construct (人工物) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 5.3 Å クライオ電子顕微鏡法 / 解像度: 5.3 Å | |||||||||
 データ登録者 データ登録者 | Vecchio AJ | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: To be published ジャーナル: To be publishedタイトル: Cryo-EM structures of a synthetic antibody against 22 kDa claudin-4 reveal its complex with Clostridium perfringens enterotoxin 著者: Vecchio AJ #1:  ジャーナル: bioRxiv / 年: 2023 ジャーナル: bioRxiv / 年: 2023タイトル: Cryo-EM structures of a synthetic antibody against 22 kDa claudin-4 reveal its complex with 著者: Erramilli SK / Dominik PK / Ogbu CP / Kossiakoff AA / Vecchio AJ | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_41915.map.gz emd_41915.map.gz | 250.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-41915-v30.xml emd-41915-v30.xml emd-41915.xml emd-41915.xml | 22 KB 22 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_41915_fsc.xml emd_41915_fsc.xml | 23.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_41915.png emd_41915.png | 33.6 KB | ||
| マスクデータ |  emd_41915_msk_1.map emd_41915_msk_1.map | 512 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-41915.cif.gz emd-41915.cif.gz | 7 KB | ||
| その他 |  emd_41915_half_map_1.map.gz emd_41915_half_map_1.map.gz emd_41915_half_map_2.map.gz emd_41915_half_map_2.map.gz | 474.5 MB 474.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-41915 http://ftp.pdbj.org/pub/emdb/structures/EMD-41915 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41915 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41915 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_41915.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_41915.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.507 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_41915_msk_1.map emd_41915_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
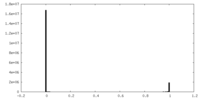
| 投影像・断面図 |
| ||||||||||||
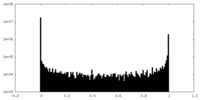
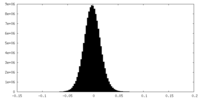
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_41915_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
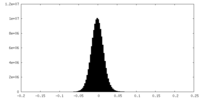
| 投影像・断面図 |
| ||||||||||||
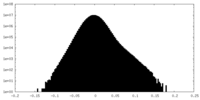
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_41915_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Human claudin-4 complex with Clostridium perfringens enterotoxin ...
| 全体 | 名称: Human claudin-4 complex with Clostridium perfringens enterotoxin C-terminal domain and sFab COP-1 |
|---|---|
| 要素 |
|
-超分子 #1: Human claudin-4 complex with Clostridium perfringens enterotoxin ...
| 超分子 | 名称: Human claudin-4 complex with Clostridium perfringens enterotoxin C-terminal domain and sFab COP-1 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 詳細: Assembled complex of 4 proteins (Fab is 2 proteins) expressed from insect cells and E coli |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 100 KDa |
-分子 #1: Claudin-4
| 分子 | 名称: Claudin-4 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 22.613852 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MASMGLQVMG IALAVLGWLA VMLCCALPMW RVTAFIGSNI VTSQTIWEGL WMNCVVQSTG QMQCKVYDSL LALPQDLQAA RALVIISII VAALGVLLSV VGGKCTNCLE DESAKAKTMI VAGVVFLLAG LMVIVPVSWT AHNIIQDFYN PLVASGQKRE M GASLYVGW ...文字列: MASMGLQVMG IALAVLGWLA VMLCCALPMW RVTAFIGSNI VTSQTIWEGL WMNCVVQSTG QMQCKVYDSL LALPQDLQAA RALVIISII VAALGVLLSV VGGKCTNCLE DESAKAKTMI VAGVVFLLAG LMVIVPVSWT AHNIIQDFYN PLVASGQKRE M GASLYVGW AASGLLLLGG GLLCCNCPPR TDKPYSAKYS AARSAAASNY VGLVPR UniProtKB:  Claudin-4 Claudin-4 |
-分子 #2: Heat-labile enterotoxin B chain
| 分子 | 名称: Heat-labile enterotoxin B chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Clostridium perfringens (ウェルシュ菌) Clostridium perfringens (ウェルシュ菌) |
| 分子量 | 理論値: 14.044594 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: GSDEILDLAA ATERLNLTDA LNSNPAGNLY DWRSSNSYPW TQKLNLHLTI TATGQKYRIL ASKIVDFNIY SNNFNNLVKL EQSLGDGVK DHYVDISLDA GQYVLVMKAN SSYSGNYPYS ILFQKF UniProtKB: Heat-labile enterotoxin B chain |
-分子 #3: COP-1 sFab Light Chain
| 分子 | 名称: COP-1 sFab Light Chain / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 23.258783 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: SDIQMTQSPS SLSASVGDRV TITCRASQSV SSAVAWYQQK PGKAPKLLIY SASSLYSGVP SRFSGSRSGT DFTLTISSLQ PEDFATYYC QQSSSSLITF GQGTKVEIKR TVAAPSVFIF PPSDSQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD ...文字列: SDIQMTQSPS SLSASVGDRV TITCRASQSV SSAVAWYQQK PGKAPKLLIY SASSLYSGVP SRFSGSRSGT DFTLTISSLQ PEDFATYYC QQSSSSLITF GQGTKVEIKR TVAAPSVFIF PPSDSQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD SKDSTYSLSS TLTLSKADYE KHKVYACEVT HQGLSSPVTK SFNRGEC |
-分子 #4: COP-1 sFab Heavy Chain
| 分子 | 名称: COP-1 sFab Heavy Chain / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 28.064498 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MKKNIAFLLA SMFVFSIATN AYAEISEVQL VESGGGLVQP GGSLRLSCAA SGFNFSSSYI HWVRQAPGKG LEWVASISSS SGSTSYADS VKGRFTISAD TSKNTAYLQM NSLRAEDTAV YYCARWFHPW WWWEYLFRGA IDYWGQGTLV TVSSASTKGP S VFPLAPSS ...文字列: MKKNIAFLLA SMFVFSIATN AYAEISEVQL VESGGGLVQP GGSLRLSCAA SGFNFSSSYI HWVRQAPGKG LEWVASISSS SGSTSYADS VKGRFTISAD TSKNTAYLQM NSLRAEDTAV YYCARWFHPW WWWEYLFRGA IDYWGQGTLV TVSSASTKGP S VFPLAPSS KSTSGGTAAL GCLVKDYFPE PVTVSWNSGA LTSGVHTFPA VLQSSGLYSL SSVVTVPSSS LGTQTYICNV NH KPSNTKV DKKVEPKSCD KTHT |
-分子 #5: Lauryl Maltose Neopentyl Glycol
| 分子 | 名称: Lauryl Maltose Neopentyl Glycol / タイプ: ligand / ID: 5 / コピー数: 1 / 式: AV0 |
|---|---|
| 分子量 | 理論値: 1.005188 KDa |
| Chemical component information |  ChemComp-AV0: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 6 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 詳細: 20 mM Hepes pH 7.4, 100 mM NaCl, and 0.003% LMNG |
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 278 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.2 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 92000 Bright-field microscopy / 最大 デフォーカス(公称値): 2.2 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 92000 |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 1073 / 平均電子線量: 60.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー








 Z
Z Y
Y X
X