+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-30499 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
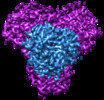
| タイトル | Cryo-EM structure of bicarbonate transporter SbtA in complex with PII-like signaling protein SbtB from Synechocystis sp. PCC 6803 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 | Na+-dependent bicarbonate transporter superfamily / Na+-dependent bicarbonate transporter superfamily / Nitrogen regulatory PII-like, alpha/beta / Nitrogen regulatory protein PII/ATP phosphoribosyltransferase, C-terminal / plasma membrane-derived thylakoid membrane / membrane / Slr1512 protein / Membrane-associated protein slr1513 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.15 Å | |||||||||
 データ登録者 データ登録者 | Liu XY / Jiang YL / Wang L / Hou WT / Chen Y / Zhou CZ | |||||||||
| 資金援助 |  中国, 2件 中国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell Discov / 年: 2021 ジャーナル: Cell Discov / 年: 2021タイトル: Structures of cyanobacterial bicarbonate transporter SbtA and its complex with PII-like SbtB. 著者: Xiao-Yu Liu / Wen-Tao Hou / Liang Wang / Bo Li / Yu Chen / Yuxing Chen / Yong-Liang Jiang / Cong-Zhao Zhou /  | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_30499.map.gz emd_30499.map.gz | 28.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-30499-v30.xml emd-30499-v30.xml emd-30499.xml emd-30499.xml | 13.5 KB 13.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_30499.png emd_30499.png | 225.3 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-30499 http://ftp.pdbj.org/pub/emdb/structures/EMD-30499 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30499 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30499 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_30499_validation.pdf.gz emd_30499_validation.pdf.gz | 504.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_30499_full_validation.pdf.gz emd_30499_full_validation.pdf.gz | 504.1 KB | 表示 | |
| XML形式データ |  emd_30499_validation.xml.gz emd_30499_validation.xml.gz | 5.7 KB | 表示 | |
| CIF形式データ |  emd_30499_validation.cif.gz emd_30499_validation.cif.gz | 6.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30499 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30499 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30499 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30499 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_30499.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_30499.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.04 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : SbtA-SbtB complex
| 全体 | 名称: SbtA-SbtB complex |
|---|---|
| 要素 |
|
-超分子 #1: SbtA-SbtB complex
| 超分子 | 名称: SbtA-SbtB complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  株: PCC 6803 substr. Kazusa |
| 組換発現 | 生物種:  |
| 分子量 | 理論値: 150 KDa |
-分子 #1: Slr1512 protein
| 分子 | 名称: Slr1512 protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: PCC 6803 substr. Kazusa |
| 分子量 | 理論値: 39.671246 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MDFLSNFLTD FVGQLQSPTL AFLIGGMVIA ALGTQLVIPE AISTIIVFML LTKIGLTGGM AIRNSNLTEM LLPVAFSVIL GILIVFIAR FTLAKLPNVR TVDALATGGL FGAVSGSTMA AALTTLEESK ISYEAWAGAL YPFMDIPALV TAIVVANIYL N KRKRKSAA ...文字列: MDFLSNFLTD FVGQLQSPTL AFLIGGMVIA ALGTQLVIPE AISTIIVFML LTKIGLTGGM AIRNSNLTEM LLPVAFSVIL GILIVFIAR FTLAKLPNVR TVDALATGGL FGAVSGSTMA AALTTLEESK ISYEAWAGAL YPFMDIPALV TAIVVANIYL N KRKRKSAA ASIEESFSKQ PVAAGDYGDQ TDYPRTRQEY LSQQEPEDNR VKIWPIIEES LQGPALSAML LGLALGIFTK PE SVYEGFY DPLFRGLLSI LMLIMGMEAW SRIGELRKVA QWYVVYSLIA PIVHGFIAFG LGMIAHYATG FSLGGVVVLA VIA ASSSDI SGPPTLRAGI PSANPSAYIG SSTAIGTPIA IGVCIPLFIG LAQTLGAG |
-分子 #2: Membrane-associated protein slr1513
| 分子 | 名称: Membrane-associated protein slr1513 / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: PCC 6803 substr. Kazusa |
| 分子量 | 理論値: 12.02181 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MAKPANKLVI VTEKILLKKI AKIIDESGAK GYTVMNTGGK GSRNVRSSGQ PNTSDIEANI KFEILTETRE MAEEIADRVA VKYFNDYAG IIYICSAEVL YGHTFCGPEG C |
-分子 #3: SODIUM ION
| 分子 | 名称: SODIUM ION / タイプ: ligand / ID: 3 / コピー数: 3 |
|---|---|
| 分子量 | 理論値: 22.99 Da |
-分子 #4: ADENOSINE MONOPHOSPHATE
| 分子 | 名称: ADENOSINE MONOPHOSPHATE / タイプ: ligand / ID: 4 / コピー数: 3 / 式: AMP |
|---|---|
| 分子量 | 理論値: 347.221 Da |
| Chemical component information |  ChemComp-AMP: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 / 詳細: 25 mM Tris-HCl pH=8.0, 300 mM NaCl, 5% glycerol |
|---|---|
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 281 K |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | プロトコル: AB INITIO MODEL |
|---|---|
| 得られたモデル |  PDB-7cyf: |
 ムービー
ムービー コントローラー
コントローラー