+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-30161 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Linker Histone Defines Structure and Self-Association Behaviour of the 177 bp Human Chromatosome | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of transcription regulatory region DNA binding / negative regulation of DNA recombination / Apoptosis induced DNA fragmentation / chromosome condensation / nucleosomal DNA binding / Formation of Senescence-Associated Heterochromatin Foci (SAHF) / minor groove of adenine-thymine-rich DNA binding / negative regulation of megakaryocyte differentiation / protein localization to CENP-A containing chromatin / nucleosome binding ...positive regulation of transcription regulatory region DNA binding / negative regulation of DNA recombination / Apoptosis induced DNA fragmentation / chromosome condensation / nucleosomal DNA binding / Formation of Senescence-Associated Heterochromatin Foci (SAHF) / minor groove of adenine-thymine-rich DNA binding / negative regulation of megakaryocyte differentiation / protein localization to CENP-A containing chromatin / nucleosome binding / Chromatin modifying enzymes / Replacement of protamines by nucleosomes in the male pronucleus / CENP-A containing nucleosome / Packaging Of Telomere Ends / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine / transcription repressor complex / Deposition of new CENPA-containing nucleosomes at the centromere / Recognition and association of DNA glycosylase with site containing an affected pyrimidine / Cleavage of the damaged pyrimidine / telomere organization / Interleukin-7 signaling / Inhibition of DNA recombination at telomere / RNA Polymerase I Promoter Opening / Meiotic synapsis / Assembly of the ORC complex at the origin of replication / Regulation of endogenous retroelements by the Human Silencing Hub (HUSH) complex / SUMOylation of chromatin organization proteins / DNA methylation / Condensation of Prophase Chromosomes / epigenetic regulation of gene expression / Chromatin modifications during the maternal to zygotic transition (MZT) / SIRT1 negatively regulates rRNA expression / HCMV Late Events / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / innate immune response in mucosa / PRC2 methylates histones and DNA / Regulation of endogenous retroelements by KRAB-ZFP proteins / Defective pyroptosis / HDMs demethylate histones / Regulation of endogenous retroelements by Piwi-interacting RNAs (piRNAs) / HDACs deacetylate histones / Nonhomologous End-Joining (NHEJ) / RNA Polymerase I Promoter Escape / chromatin DNA binding / Transcriptional regulation by small RNAs / Formation of the beta-catenin:TCF transactivating complex / euchromatin / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / G2/M DNA damage checkpoint / Metalloprotease DUBs / NoRC negatively regulates rRNA expression / B-WICH complex positively regulates rRNA expression / DNA Damage/Telomere Stress Induced Senescence / PKMTs methylate histone lysines / Meiotic recombination / Pre-NOTCH Transcription and Translation / RMTs methylate histone arginines / Activation of anterior HOX genes in hindbrain development during early embryogenesis / Transcriptional regulation of granulopoiesis / UCH proteinases / HCMV Early Events / antimicrobial humoral immune response mediated by antimicrobial peptide / structural constituent of chromatin / antibacterial humoral response / E3 ubiquitin ligases ubiquitinate target proteins / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks / nucleosome / heterochromatin formation / RUNX1 regulates transcription of genes involved in differentiation of HSCs / nucleosome assembly / actin cytoskeleton / Processing of DNA double-strand break ends / HATs acetylate histones / Senescence-Associated Secretory Phenotype (SASP) / Factors involved in megakaryocyte development and platelet production / chromatin organization / MLL4 and MLL3 complexes regulate expression of PPARG target genes in adipogenesis and hepatic steatosis / double-stranded DNA binding / Oxidative Stress Induced Senescence / defense response to Gram-negative bacterium / gene expression / killing of cells of another organism / Estrogen-dependent gene expression / chromosome, telomeric region / Ub-specific processing proteases / defense response to Gram-positive bacterium / nuclear body / cadherin binding / Amyloid fiber formation / protein heterodimerization activity / negative regulation of cell population proliferation / chromatin / Golgi apparatus / protein-containing complex / extracellular space / DNA binding / RNA binding / extracellular exosome 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
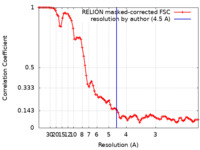
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.5 Å | |||||||||
 データ登録者 データ登録者 | Wang S / Vogirala VK / Soman A / Sandin S / Liu ZB | |||||||||
| 資金援助 |  シンガポール, 2件 シンガポール, 2件
| |||||||||
 引用 引用 |  ジャーナル: Sci Rep / 年: 2021 ジャーナル: Sci Rep / 年: 2021タイトル: Linker histone defines structure and self-association behaviour of the 177 bp human chromatosome. 著者: Sai Wang / Vinod K Vogirala / Aghil Soman / Nikolay V Berezhnoy / Zhehui Barry Liu / Andrew S W Wong / Nikolay Korolev / Chun-Jen Su / Sara Sandin / Lars Nordenskiöld /    要旨: Linker histones play essential roles in the regulation and maintenance of the dynamic chromatin structure of higher eukaryotes. The influence of human histone H1.0 on the nucleosome structure and ...Linker histones play essential roles in the regulation and maintenance of the dynamic chromatin structure of higher eukaryotes. The influence of human histone H1.0 on the nucleosome structure and biophysical properties of the resulting chromatosome were investigated and compared with the 177-bp nucleosome using Cryo-EM and SAXS. The 4.5 Å Cryo-EM chromatosome structure showed that the linker histone binds at the nucleosome dyad interacting with both linker DNA arms but in a tilted manner leaning towards one of the linker sides. The chromatosome is laterally compacted and rigid in the dyad and linker DNA area, in comparison with the nucleosome where linker DNA region is more flexible and displays structural variability. In solution, the chromatosomes appear slightly larger than the nucleosomes, with the volume increase compared to the bound linker histone, according to solution SAXS measurements. SAXS X-ray diffraction characterisation of Mg-precipitated samples showed that the different shapes of the 177 chromatosome enabled the formation of a highly ordered lamello-columnar phase when precipitated by Mg, indicating the influence of linker histone on the nucleosome stacking. The biological significance of linker histone, therefore, may be affected by the change in the polyelectrolyte and DNA conformation properties of the chromatosomes, in comparison to nucleosomes. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_30161.map.gz emd_30161.map.gz | 48.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-30161-v30.xml emd-30161-v30.xml emd-30161.xml emd-30161.xml | 10.1 KB 10.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_30161_fsc.xml emd_30161_fsc.xml | 8.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_30161.png emd_30161.png | 68.7 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-30161 http://ftp.pdbj.org/pub/emdb/structures/EMD-30161 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30161 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30161 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_30161_validation.pdf.gz emd_30161_validation.pdf.gz | 380.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_30161_full_validation.pdf.gz emd_30161_full_validation.pdf.gz | 380.5 KB | 表示 | |
| XML形式データ |  emd_30161_validation.xml.gz emd_30161_validation.xml.gz | 10.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30161 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30161 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30161 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30161 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_30161.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_30161.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : ternary complex of 177bp nucleosome with linker histone H1
| 全体 | 名称: ternary complex of 177bp nucleosome with linker histone H1 |
|---|---|
| 要素 |
|
-超分子 #1: ternary complex of 177bp nucleosome with linker histone H1
| 超分子 | 名称: ternary complex of 177bp nucleosome with linker histone H1 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  |
| 分子量 | 理論値: 242 KDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.58 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) #0 - 平均電子線量: 80.0 e/Å2 / #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) #1 - 平均電子線量: 80.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)