+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-22987 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Adeno-associated virus serotype 5 at 2.1 Angstroms resolution, AAV5 | |||||||||
 マップデータ マップデータ | 2.1A Native AAV5 virus like particle sharpened map. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | AAV5 / AAV / AAV-5 / Adeno Associated Virus / VIRUS LIKE PARTICLE / parvovirus / virus / gene therapy | |||||||||
| 機能・相同性 | Phospholipase A2-like domain / Phospholipase A2-like domain / Parvovirus coat protein VP2 / Parvovirus coat protein VP1/VP2 / Parvovirus coat protein VP2 / Capsid/spike protein, ssDNA virus / T=1 icosahedral viral capsid / structural molecule activity / Capsid protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Adeno-associated virus - 5 (アデノ随伴ウイルス) / Adeno-associated virus - 5 (アデノ随伴ウイルス) /   Adeno-associated virus (アデノ随伴ウイルス) Adeno-associated virus (アデノ随伴ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.1 Å | |||||||||
 データ登録者 データ登録者 | Silveria M / Chapman MS | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Viruses / 年: 2020 ジャーナル: Viruses / 年: 2020タイトル: The Structure of an AAV5-AAVR Complex at 2.5 Å Resolution: Implications for Cellular Entry and Immune Neutralization of AAV Gene Therapy Vectors. 著者: Mark A Silveria / Edward E Large / Grant M Zane / Tommi A White / Michael S Chapman /  要旨: Adeno-Associated Virus is the leading vector for gene therapy. Although it is the vector for all in vivo gene therapies approved for clinical use by the US Food and Drug Administration, its biology ...Adeno-Associated Virus is the leading vector for gene therapy. Although it is the vector for all in vivo gene therapies approved for clinical use by the US Food and Drug Administration, its biology is still not yet fully understood. It has been shown that different serotypes of AAV bind to their cellular receptor, AAVR, in different ways. Previously we have reported a 2.4Å structure of AAV2 bound to AAVR that shows ordered structure for only one of the two AAVR domains with which AAV2 interacts. In this study we present a 2.5Å resolution structure of AAV5 bound to AAVR. AAV5 binds to the first polycystic kidney disease (PKD) domain of AAVR that was not ordered in the AAV2 structure. Interactions of AAV5 with AAVR are analyzed in detail, and the implications for AAV2 binding are explored through molecular modeling. Moreover, we find that binding sites for the antibodies ADK5a, ADK5b, and 3C5 on AAV5 overlap with the binding site of AAVR. These insights provide a structural foundation for development of gene therapy agents to better evade immune neutralization without disrupting cellular entry. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_22987.map.gz emd_22987.map.gz | 203.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-22987-v30.xml emd-22987-v30.xml emd-22987.xml emd-22987.xml | 22 KB 22 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_22987.png emd_22987.png | 257.9 KB | ||
| マスクデータ |  emd_22987_msk_1.map emd_22987_msk_1.map | 729 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-22987.cif.gz emd-22987.cif.gz | 7.1 KB | ||
| その他 |  emd_22987_additional_1.map.gz emd_22987_additional_1.map.gz emd_22987_half_map_1.map.gz emd_22987_half_map_1.map.gz emd_22987_half_map_2.map.gz emd_22987_half_map_2.map.gz | 576.9 MB 577.2 MB 577.2 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-22987 http://ftp.pdbj.org/pub/emdb/structures/EMD-22987 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22987 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22987 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_22987_validation.pdf.gz emd_22987_validation.pdf.gz | 1.1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_22987_full_validation.pdf.gz emd_22987_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  emd_22987_validation.xml.gz emd_22987_validation.xml.gz | 21.2 KB | 表示 | |
| CIF形式データ |  emd_22987_validation.cif.gz emd_22987_validation.cif.gz | 25.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22987 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22987 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22987 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22987 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_22987.map.gz / 形式: CCP4 / 大きさ: 729 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_22987.map.gz / 形式: CCP4 / 大きさ: 729 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 2.1A Native AAV5 virus like particle sharpened map. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.5325 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
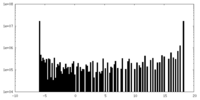
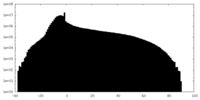
| ファイル |  emd_22987_msk_1.map emd_22987_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: 2.1A Native AAV5 virus like particle unsharpened map.
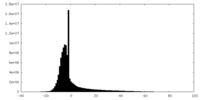
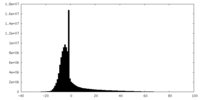
| ファイル | emd_22987_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 2.1A Native AAV5 virus like particle unsharpened map. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: 2.1A Native AAV5 virus like particle sharpened map.
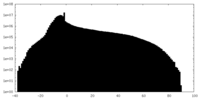
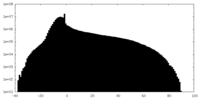
| ファイル | emd_22987_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 2.1A Native AAV5 virus like particle sharpened map. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: 2.1A Native AAV5 virus like particle half map...
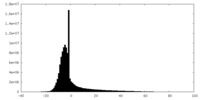
| ファイル | emd_22987_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 2.1A Native AAV5 virus like particle half map 2 of 2 in 222a viewing frame. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Adeno-associated virus
| 全体 | 名称:   Adeno-associated virus (アデノ随伴ウイルス) Adeno-associated virus (アデノ随伴ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Adeno-associated virus
| 超分子 | 名称: Adeno-associated virus / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: Expressed using SF9 cells with a pfastbac LIC vector. Purified with cesium chloride ultracentrifugation. NCBI-ID: 272636 / 生物種: Adeno-associated virus / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: Yes |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 3.746 MDa |
| ウイルス殻 | Shell ID: 1 / 直径: 250.0 Å / T番号(三角分割数): 1 |
-分子 #1: Capsid protein
| 分子 | 名称: Capsid protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Adeno-associated virus - 5 (アデノ随伴ウイルス) Adeno-associated virus - 5 (アデノ随伴ウイルス) |
| 分子量 | 理論値: 80.366211 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: SFVDHPPDWL EEVGEGLREF LGLEAGPPKP KPNQQHQDQA RGLVLPGYNY LGPGNGLDRG EPVNRADEVA REHDISYNEQ LEAGDNPYL KYNHADAEFQ EKLADDTSFG GNLGKAVFQA KKRVLEPFGL VEEGAKTAPT GKRIDDHFPK RKKARTEEDS K PSTSSDAE ...文字列: SFVDHPPDWL EEVGEGLREF LGLEAGPPKP KPNQQHQDQA RGLVLPGYNY LGPGNGLDRG EPVNRADEVA REHDISYNEQ LEAGDNPYL KYNHADAEFQ EKLADDTSFG GNLGKAVFQA KKRVLEPFGL VEEGAKTAPT GKRIDDHFPK RKKARTEEDS K PSTSSDAE AGPSGSQQLQ IPAQPASSLG ADTMSAGGGG PLGDNNQGAD GVGNASGDWH CDSTWMGDRV VTKSTRTWVL PS YNNHQYR EIKSGSVDGS NANAYFGYST PWGYFDFNRF HSHWSPRDWQ RLINNYWGFR PRSLRVKIFN IQVKEVTVQD STT TIANNL TSTVQVFTDD DYQLPYVVGN GTEGCLPAFP PQVFTLPQYG YATLNRDNTE NPTERSSFFC LEYFPSKMLR TGNN FEFTY NFEEVPFHSS FAPSQNLFKL ANPLVDQYLY RFVSTNNTGG VQFNKNLAGR YANTYKNWFP GPMGRTQGWN LGSGV NRAS VSAFATTNRM ELEGASYQVP PQPNGMTNNL QGSNTYALEN TMIFNSQPAN PGTTATYLEG NMLITSESET QPVNRV AYN VGGQMATNNQ SSTTAPATGT YNLQEIVPGS VWMERDVYLQ GPIWAKIPET GAHFHPSPAM GGFGLKHPPP MMLIKNT PV PGNITSFSDV PVSSFITQYS TGQVTVEMEW ELKKENSKRW NPEIQYTNNY NDPQFVDFAP DSTGEYRTTR PIGTRYLT R PL UniProtKB: Capsid protein |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.75 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
| ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 293 K / 装置: FEI VITROBOT MARK IV 詳細: Two 2uL aliquots applied to grid (manual blotting between), prior to automated 3 second blot before plunging.. | ||||||||||||
| 詳細 | Monodisperse |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 93.0 K / 最高: 93.0 K |
| 詳細 | Coma-free alignment and objective astigmatism where corrected using Sherpa (Thermo Fisher, Inc.). |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 検出モード: INTEGRATING / デジタル化 - サイズ - 横: 11520 pixel / デジタル化 - サイズ - 縦: 8184 pixel / 撮影したグリッド数: 1 / 実像数: 9490 / 平均電子線量: 31.7 e/Å2 / 詳細: Pixel size was 0.5295 angstrom. |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): -2.7 µm 最小 デフォーカス(公称値): -0.7000000000000001 µm 倍率(公称値): 81000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 詳細 | Stand-alone RSRef was used for refinement of magnification, resolution, envelope correction and atomic B-factors. This was alternated with RSRef-embedded CNS was used for molecular dynamics optimization (1st round) and stereochemically-restrained all-atom least-squares optimization. |
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: Least-squares residual |
| 得られたモデル |  PDB-7kp3: |
 ムービー
ムービー コントローラー
コントローラー


















 Z
Z Y
Y X
X