+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-22230 | |||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | R. capsulatus CIII2CIV tripartite super-complex, conformation B (SC-1B) | |||||||||||||||||||||||||||
 マップデータ マップデータ | CIII2CIV tripartite super-complex, conformation B (SC-1B) | |||||||||||||||||||||||||||
 試料 試料 |
| |||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報cytochrome-c oxidase / : / respiratory chain complex III / oxidative phosphorylation / cytochrome-c oxidase / quinol-cytochrome-c reductase / ubiquinol-cytochrome-c reductase activity / cytochrome-c oxidase activity / : / photosynthesis ...cytochrome-c oxidase / : / respiratory chain complex III / oxidative phosphorylation / cytochrome-c oxidase / quinol-cytochrome-c reductase / ubiquinol-cytochrome-c reductase activity / cytochrome-c oxidase activity / : / photosynthesis / respiratory electron transport chain / proton transmembrane transport / 2 iron, 2 sulfur cluster binding / electron transfer activity / oxidoreductase activity / heme binding / membrane / metal ion binding / plasma membrane 類似検索 - 分子機能 | |||||||||||||||||||||||||||
| 生物種 |  Rhodobacter capsulatus SB 1003 (バクテリア) / Rhodobacter capsulatus SB 1003 (バクテリア) /  Rhodobacter capsulatus (strain ATCC BAA-309 / NBRC 16581 / SB1003) (バクテリア) Rhodobacter capsulatus (strain ATCC BAA-309 / NBRC 16581 / SB1003) (バクテリア) | |||||||||||||||||||||||||||
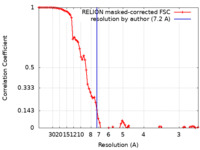
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.2 Å | |||||||||||||||||||||||||||
 データ登録者 データ登録者 | Steimle S / Van Eeuwen T / Ozturk Y / Kim HJ / Braitbard M / Selamoglu N / Garcia BA / Schneidman-Duhovny D / Murakami K / Daldal F | |||||||||||||||||||||||||||
| 資金援助 |  米国, 米国,  イスラエル, 8件 イスラエル, 8件
| |||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Cryo-EM structures of engineered active bc-cbb type CIIICIV super-complexes and electronic communication between the complexes. 著者: Stefan Steimle / Trevor van Eeuwen / Yavuz Ozturk / Hee Jong Kim / Merav Braitbard / Nur Selamoglu / Benjamin A Garcia / Dina Schneidman-Duhovny / Kenji Murakami / Fevzi Daldal /    要旨: Respiratory electron transport complexes are organized as individual entities or combined as large supercomplexes (SC). Gram-negative bacteria deploy a mitochondrial-like cytochrome (cyt) bc (Complex ...Respiratory electron transport complexes are organized as individual entities or combined as large supercomplexes (SC). Gram-negative bacteria deploy a mitochondrial-like cytochrome (cyt) bc (Complex III, CIII), and may have specific cbb-type cyt c oxidases (Complex IV, CIV) instead of the canonical aa-type CIV. Electron transfer between these complexes is mediated by soluble (c) and membrane-anchored (c) cyts. Here, we report the structure of an engineered bc-cbb type SC (CIIICIV, 5.2 Å resolution) and three conformers of native CIII (3.3 Å resolution). The SC is active in vivo and in vitro, contains all catalytic subunits and cofactors, and two extra transmembrane helices attributed to cyt c and the assembly factor CcoH. The cyt c is integral to SC, its cyt domain is mobile and it conveys electrons to CIV differently than cyt c. The successful production of a native-like functional SC and determination of its structure illustrate the characteristics of membrane-confined and membrane-external respiratory electron transport pathways in Gram-negative bacteria. | |||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_22230.map.gz emd_22230.map.gz | 4.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-22230-v30.xml emd-22230-v30.xml emd-22230.xml emd-22230.xml | 25.3 KB 25.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_22230_fsc.xml emd_22230_fsc.xml | 8.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_22230.png emd_22230.png | 140 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-22230 http://ftp.pdbj.org/pub/emdb/structures/EMD-22230 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22230 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22230 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_22230_validation.pdf.gz emd_22230_validation.pdf.gz | 348 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_22230_full_validation.pdf.gz emd_22230_full_validation.pdf.gz | 347.6 KB | 表示 | |
| XML形式データ |  emd_22230_validation.xml.gz emd_22230_validation.xml.gz | 10.3 KB | 表示 | |
| CIF形式データ |  emd_22230_validation.cif.gz emd_22230_validation.cif.gz | 13.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22230 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22230 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22230 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22230 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6xkzMC  6xi0C  6xktC  6xkuC  6xkvC  6xkwC  6xkxC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10735 (タイトル: Cryo-EM structures of engineered active bc1-cbb3 type CIII2CIV super-complexes and electronic communication between the complexes EMPIAR-10735 (タイトル: Cryo-EM structures of engineered active bc1-cbb3 type CIII2CIV super-complexes and electronic communication between the complexesData size: 35.8 TB Data #1: tripartite SC - dataset 1 [micrographs - multiframe] Data #2: tripartite SC - dataset 2 [micrographs - multiframe] Data #3: tripartite SC - dataset 3 [micrographs - multiframe] Data #4: tripartite SC - dataset 4 [micrographs - multiframe] Data #5: tripartite SC - dataset 5 [micrographs - multiframe] Data #6: tripartite SC - dataset 6 [micrographs - multiframe] Data #7: tripartite SC - dataset 7 [micrographs - multiframe] Data #8: bipartite SC - dataset 1 [micrographs - single frame] Data #9: bipartite SC - dataset 2 [micrographs - multiframe] Data #10: bipartite SC - dataset 3 [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_22230.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_22230.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CIII2CIV tripartite super-complex, conformation B (SC-1B) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.32 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : CIII2CIV tripartite super-complex, conformation B (SC-1B)
+超分子 #1: CIII2CIV tripartite super-complex, conformation B (SC-1B)
+超分子 #2: CIII2
+超分子 #3: CIV
+分子 #1: Ubiquinol-cytochrome c reductase iron-sulfur subunit
+分子 #2: Cytochrome b
+分子 #3: Cytochrome c1
+分子 #4: Cytochrome c oxidase, Cbb3-type, subunit I
+分子 #5: Cytochrome c oxidase, Cbb3-type, subunit II
+分子 #6: Cbb3-type cytochrome c oxidase subunit CcoP,Cytochrome c-type cyt cy
+分子 #7: FE2/S2 (INORGANIC) CLUSTER
+分子 #8: HEME C
+分子 #9: COPPER (II) ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 |
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 400 / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)