+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 202d | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SOLUTION STRUCTURE OF THE MENOGARIL-DNA COMPLEX | ||||||||||||||||||
 要素 要素 | DNA (5'-D(* キーワード キーワードDNA / MENOGARIL | 機能・相同性 | MENOGARIL / DNA |  機能・相同性情報 機能・相同性情報手法 | 溶液NMR / MOLECULAR DYNAMICS, MATRIX RELAXATION |  データ登録者 データ登録者Chen, H. / Patel, D.J. |  引用 引用ジャーナル: J.Am.Chem.Soc. / 年: 1995 タイトル: Solution Structure of the Menogaril-DNA Complex 著者: Chen, H. / Patel, D.J. #1:  ジャーナル: Biochemistry / 年: 1989 ジャーナル: Biochemistry / 年: 1989タイトル: Antitumor Drug Nogalamycin Binds DNA in Both Grooves Simultaneously: Molecular Structure of Nogalamycin-DNA Complex 著者: Liaw, Y.-C. / Gao, Y.-G. / Robinson, H. / Van Der Marel, G.A. / Van Boom, J.H. / Wang, A.H. 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  202d.cif.gz 202d.cif.gz | 64.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb202d.ent.gz pdb202d.ent.gz | 50.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  202d.json.gz 202d.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  202d_validation.pdf.gz 202d_validation.pdf.gz | 441.3 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  202d_full_validation.pdf.gz 202d_full_validation.pdf.gz | 474.6 KB | 表示 | |
| XML形式データ |  202d_validation.xml.gz 202d_validation.xml.gz | 6.1 KB | 表示 | |
| CIF形式データ |  202d_validation.cif.gz 202d_validation.cif.gz | 7.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/02/202d https://data.pdbj.org/pub/pdb/validation_reports/02/202d ftp://data.pdbj.org/pub/pdb/validation_reports/02/202d ftp://data.pdbj.org/pub/pdb/validation_reports/02/202d | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 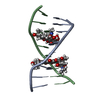
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 2426.617 Da / 分子数: 2 / 由来タイプ: 合成 / 詳細: CHEMICALLY SYNTHESIZED /  キーワード: DEOXYRIBONUCLEIC ACID キーワード: DEOXYRIBONUCLEIC ACID#2: 化合物 | |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR |
|---|---|
| NMR実験の詳細 | Text: MENOGARIL WAS PROVIDED BY UPJOHN CO., KALAMAZOO, MICHIGAN. |
- 試料調製
試料調製
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
|---|
- 解析
解析
| 精密化 | 手法: MOLECULAR DYNAMICS, MATRIX RELAXATION / ソフトェア番号: 1 詳細: TWO STARTING STRUCTURES WERE GENERATED BY MANUALLY DOCKING THE DRUG ONTO A- AND B-FORM DNA USING INSIGHT II AND WERE SUBSEQUENTLY REFINED BY DISTANCE-RESTRAINED MOLECULAR DYNAMICS USING A SET ...詳細: TWO STARTING STRUCTURES WERE GENERATED BY MANUALLY DOCKING THE DRUG ONTO A- AND B-FORM DNA USING INSIGHT II AND WERE SUBSEQUENTLY REFINED BY DISTANCE-RESTRAINED MOLECULAR DYNAMICS USING A SET OF INTER-PROTON DISTANCE RESTRAINTS DERIVED FROM THE NMR DATA. TWO INITIAL VELOCITY SEEDS WERE USED FOR EACH STARTING STRUCTURE WHICH YIELDS FOUR DISTANCE-REFINED STRUCTURES. THEY WERE REFINED FURTHER USING RELAXATION-MATRIX BASED NOE INTENSITY-RESTRAINED MOLECULAR DYNAMICS. THE FINAL FOUR STRUCTURES WERE OBTAINED BY TAKING THE AVERAGE COORDINATES OF THE LAST 1.0 PS OF THE DYNAMICS DURING RELAXATION MATRIX REFINEMENT AND ENERGY MINIMIZED. THE R(1/6) VALUE WAS USED TO REFINE THE STRUCTURE DURING RELAXATION MATRIX REFINEMENT. THE SUMMATIONS RUN THROUGH ALL OBSERVED, QUANTIFIABLE NOE CROSSPEAKS IN NOESY SPECTRA RECORDED IN D2O AND MIXING TIMES OF 30, 60, 100, 150 AND 200 MS. THE R(1/6) FACTOR AND THE RMS DEVIATIONS FROM IDEAL GEOMETRY FOR THE FOUR FINAL STRUCTURES ARE: MODEL1 MODEL2 MODEL3 MODEL4 R(1/6) FACTOR 0.039 0.038 0.038 0.036 BOND (ANG) 0.012 0.012 0.012 0.011 ANGLES (DEG) 3.833 3.818 3.776 3.684 IMPROPERS (DEG) 0.251 0.250 0.286 0.219 |
|---|---|
| NMRアンサンブル | コンフォーマー選択の基準: all calculated structures submitted 計算したコンフォーマーの数: 4 / 登録したコンフォーマーの数: 4 |
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj



