+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of C. thermophilum RNA exosome core | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | nuclease / RNA degradation / RNA metabolism / RNA binding / RNA BINDING PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報TRAMP-dependent tRNA surveillance pathway / CUT catabolic process / nuclear polyadenylation-dependent rRNA catabolic process / U1 snRNA 3'-end processing / nuclear polyadenylation-dependent mRNA catabolic process / U5 snRNA 3'-end processing / cytoplasmic exosome (RNase complex) / nuclear exosome (RNase complex) / poly(A)-dependent snoRNA 3'-end processing / U4 snRNA 3'-end processing ...TRAMP-dependent tRNA surveillance pathway / CUT catabolic process / nuclear polyadenylation-dependent rRNA catabolic process / U1 snRNA 3'-end processing / nuclear polyadenylation-dependent mRNA catabolic process / U5 snRNA 3'-end processing / cytoplasmic exosome (RNase complex) / nuclear exosome (RNase complex) / poly(A)-dependent snoRNA 3'-end processing / U4 snRNA 3'-end processing / : / exonucleolytic trimming to generate mature 3'-end of 5.8S rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / : / nuclear mRNA surveillance / rRNA catabolic process / RNA processing / rRNA processing / nucleolus / RNA binding / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Thermochaetoides thermophila DSM 1495 (菌類) Thermochaetoides thermophila DSM 1495 (菌類) | |||||||||
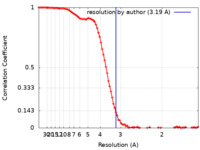
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.19 Å | |||||||||
 データ登録者 データ登録者 | Lazzaretti D / Liebau J / Pilsl M / Sprangers R | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: Biorxiv / 年: 2024 ジャーナル: Biorxiv / 年: 2024タイトル: Beyond static structures: quantitative dynamics in the eukaryotic RNA exosome complex 著者: Liebau J / Lazzaretti D / Bichler A / Pilsl M / Sprangers R | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_18825.map.gz emd_18825.map.gz | 49.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-18825-v30.xml emd-18825-v30.xml emd-18825.xml emd-18825.xml | 32 KB 32 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_18825_fsc.xml emd_18825_fsc.xml | 11.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_18825.png emd_18825.png | 92.5 KB | ||
| Filedesc metadata |  emd-18825.cif.gz emd-18825.cif.gz | 8.8 KB | ||
| その他 |  emd_18825_additional_1.map.gz emd_18825_additional_1.map.gz emd_18825_half_map_1.map.gz emd_18825_half_map_1.map.gz emd_18825_half_map_2.map.gz emd_18825_half_map_2.map.gz | 56.6 MB 49.7 MB 49.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-18825 http://ftp.pdbj.org/pub/emdb/structures/EMD-18825 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18825 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18825 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_18825_validation.pdf.gz emd_18825_validation.pdf.gz | 921.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_18825_full_validation.pdf.gz emd_18825_full_validation.pdf.gz | 920.8 KB | 表示 | |
| XML形式データ |  emd_18825_validation.xml.gz emd_18825_validation.xml.gz | 15.9 KB | 表示 | |
| CIF形式データ |  emd_18825_validation.cif.gz emd_18825_validation.cif.gz | 21 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18825 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18825 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18825 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18825 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8r1oMC  8pelC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_18825.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_18825.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.772 Å | ||||||||||||||||||||||||||||||||||||
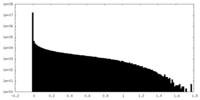
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Post-processed map (deepEMhancer)
| ファイル | emd_18825_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Post-processed map (deepEMhancer) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
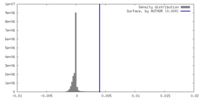
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_18825_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
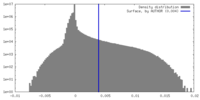
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_18825_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
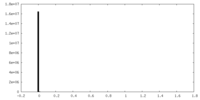
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : RNA exosome core (Exo9)
+超分子 #1: RNA exosome core (Exo9)
+分子 #1: Rrp45
+分子 #2: Exoribonuclease phosphorolytic domain-containing protein
+分子 #3: Exoribonuclease-like protein
+分子 #4: Exoribonuclease phosphorolytic domain-containing protein
+分子 #5: Exoribonuclease phosphorolytic domain-containing protein
+分子 #6: Exosome complex component MTR3
+分子 #7: Ribosomal RNA-processing protein 40
+分子 #8: Putative exosome complex protein
+分子 #9: Putative exosome 3'->5 protein
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.53 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
詳細: 20 mM Na-Phosphate buffer pH 7.5, 300 mM NaCl, 1 mM DTT | |||||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 200 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.039 kPa 詳細: Grids were glow discharged twice at 15 mA, 0.39 mBar, for 100 seconds each time | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV 詳細: Sample volume 3 ul Wait time 5 s, Blot time 5 s, Delay time 0 s Force 12. | |||||||||||||||
| 詳細 | Sample frozen directly after S200 size exclusion column |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL CRYO ARM 200 |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: In-column Omega Filter エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3838 pixel / デジタル化 - サイズ - 縦: 3710 pixel / デジタル化 - 画像ごとのフレーム数: 1-40 / 撮影したグリッド数: 1 / 実像数: 6579 / 平均露光時間: 6.5 sec. / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.2 µm / 最小 デフォーカス(公称値): 0.6 µm / 倍率(公称値): 60000 |
| 試料ステージ | 試料ホルダーモデル: JEOL CRYOSPECPORTER / ホルダー冷却材: NITROGEN |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)