+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Toroidal Dps-DNA assembly | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Co-crystal / DNA / Dps / biocrystallization / DNA BINDING PROTEIN | |||||||||
| 生物種 |  | |||||||||
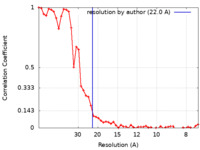
| 手法 | サブトモグラム平均法 / クライオ電子顕微鏡法 / 解像度: 22.0 Å | |||||||||
 データ登録者 データ登録者 | Chesnokov YM | |||||||||
| 資金援助 |  ロシア, 1件 ロシア, 1件
| |||||||||
 引用 引用 |  ジャーナル: Int J Mol Sci / 年: 2023 ジャーナル: Int J Mol Sci / 年: 2023タイトル: Morphological Diversity of Dps Complex with Genomic DNA. 著者: Yuri Chesnokov / Roman Kamyshinsky / Andrey Mozhaev / Eleonora Shtykova / Alexander Vasiliev / Ivan Orlov / Liubov Dadinova /  要旨: In response to adverse environmental factors, cells actively produce Dps proteins which form ordered complexes (biocrystals) with bacterial DNA to protect the genome. The effect of ...In response to adverse environmental factors, cells actively produce Dps proteins which form ordered complexes (biocrystals) with bacterial DNA to protect the genome. The effect of biocrystallization has been described extensively in the scientific literature; furthermore, to date, the structure of the Dps-DNA complex has been established in detail in vitro using plasmid DNA. In the present work, for the first time, Dps complexes with genomic DNA were studied in vitro using cryo-electron tomography. We demonstrate that genomic DNA forms one-dimensional crystals or filament-like assemblies which transform into weakly ordered complexes with triclinic unit cells, similar to what is observed for plasmid DNA. Changing such environmental factors as pH and KCl and MgCl concentrations leads to the formation of cylindrical structures. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_16438.map.gz emd_16438.map.gz | 7.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-16438-v30.xml emd-16438-v30.xml emd-16438.xml emd-16438.xml | 16.4 KB 16.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_16438_fsc.xml emd_16438_fsc.xml | 6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_16438.png emd_16438.png | 176 KB | ||
| マスクデータ |  emd_16438_msk_1.map emd_16438_msk_1.map | 8 MB |  マスクマップ マスクマップ | |
| その他 |  emd_16438_half_map_1.map.gz emd_16438_half_map_1.map.gz emd_16438_half_map_2.map.gz emd_16438_half_map_2.map.gz | 6 MB 6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-16438 http://ftp.pdbj.org/pub/emdb/structures/EMD-16438 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16438 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16438 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_16438_validation.pdf.gz emd_16438_validation.pdf.gz | 1005.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_16438_full_validation.pdf.gz emd_16438_full_validation.pdf.gz | 1004.6 KB | 表示 | |
| XML形式データ |  emd_16438_validation.xml.gz emd_16438_validation.xml.gz | 10.7 KB | 表示 | |
| CIF形式データ |  emd_16438_validation.cif.gz emd_16438_validation.cif.gz | 14.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16438 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16438 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16438 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16438 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_16438.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_16438.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
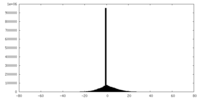
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 3.7 Å | ||||||||||||||||||||||||||||||||||||
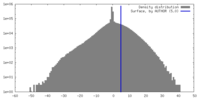
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_16438_msk_1.map emd_16438_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
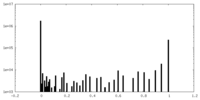
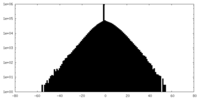
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_16438_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
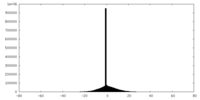
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_16438_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
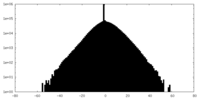
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Dps-DNA assembly
| 全体 | 名称: Dps-DNA assembly |
|---|---|
| 要素 |
|
-超分子 #1: Dps-DNA assembly
| 超分子 | 名称: Dps-DNA assembly / タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 220 KDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | 3D array |
- 試料調製
試料調製
| 濃度 | 3.1 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||
| グリッド | モデル: EMS Lacey Carbon / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: LACEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 20 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.026000000000000002 kPa | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 293 K / 装置: FEI VITROBOT MARK IV / 詳細: 2.5 s blot. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 検出モード: INTEGRATING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 実像数: 2 / 平均露光時間: 2.5 sec. / 平均電子線量: 2.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 最大 デフォーカス(補正後): 8.0 µm / 最小 デフォーカス(補正後): 6.0 µm / 倍率(補正後): 37837 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 0.01 mm / 最大 デフォーカス(公称値): 8.0 µm / 最小 デフォーカス(公称値): 6.0 µm / 倍率(公称値): 18000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: HELIUM |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
|---|
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)