+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
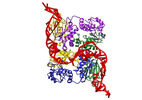
| タイトル | CryoEM structure of bacterial RapZ.GlmZ complex central to the control of cell envelope biogenesis | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | endonuclease RNase E / adaptor protein RapZ / small regulatory RNA GlmZ / RNA BINDING PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RNA destabilization / carbohydrate derivative binding / protein homotetramerization / molecular adaptor activity / GTP binding / protein-containing complex / RNA binding / ATP binding / identical protein binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.28 Å | |||||||||
 データ登録者 データ登録者 | Islam MS / Hardwick HW / Chirgadze DY / Luisi BF | |||||||||
| 資金援助 |  英国, 1件 英国, 1件
| |||||||||
 引用 引用 |  ジャーナル: EMBO J / 年: 2023 ジャーナル: EMBO J / 年: 2023タイトル: Structure of a bacterial ribonucleoprotein complex central to the control of cell envelope biogenesis. 著者: Md Saiful Islam / Steven W Hardwick / Laura Quell / Svetlana Durica-Mitic / Dimitri Y Chirgadze / Boris Görke / Ben F Luisi /   要旨: Biogenesis of the essential precursor of the bacterial cell envelope, glucosamine-6-phosphate (GlcN6P), is controlled by intricate post-transcriptional networks mediated by GlmZ, a small regulatory ...Biogenesis of the essential precursor of the bacterial cell envelope, glucosamine-6-phosphate (GlcN6P), is controlled by intricate post-transcriptional networks mediated by GlmZ, a small regulatory RNA (sRNA). GlmZ stimulates translation of the mRNA encoding GlcN6P synthtase in Escherichia coli, but when bound by RapZ protein, the sRNA becomes inactivated through cleavage by the endoribonuclease RNase E. Here, we report the cryoEM structure of the RapZ:GlmZ complex, revealing a complementary match of the RapZ tetrameric quaternary structure to structural repeats in the sRNA. The nucleic acid is contacted by RapZ mostly through a highly conserved domain that shares an evolutionary relationship with phosphofructokinase and suggests links between metabolism and riboregulation. We also present the structure of a precleavage intermediate formed between the binary RapZ:GlmZ complex and RNase E that reveals how GlmZ is presented and recognised by the enzyme. The structures provide a framework for understanding how other encounter complexes might guide recognition and action of endoribonucleases on target transcripts, and how structured substrates in polycistronic precursors may be recognised for processing by RNase E. #1:  ジャーナル: Biorxiv / 年: 2022 ジャーナル: Biorxiv / 年: 2022タイトル: Structure of a bacterial ribonucleoprotein complex central to the control of cell envelope biogenesis 著者: Islam MS / Hardwick SW / Quell L / Chirgadze DY / Gorke B / Luisi BF | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15784.map.gz emd_15784.map.gz | 344.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15784-v30.xml emd-15784-v30.xml emd-15784.xml emd-15784.xml | 17 KB 17 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_15784.png emd_15784.png | 73.4 KB | ||
| Filedesc metadata |  emd-15784.cif.gz emd-15784.cif.gz | 5.8 KB | ||
| その他 |  emd_15784_half_map_1.map.gz emd_15784_half_map_1.map.gz emd_15784_half_map_2.map.gz emd_15784_half_map_2.map.gz | 344.6 MB 344.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15784 http://ftp.pdbj.org/pub/emdb/structures/EMD-15784 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15784 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15784 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_15784_validation.pdf.gz emd_15784_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_15784_full_validation.pdf.gz emd_15784_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_15784_validation.xml.gz emd_15784_validation.xml.gz | 16.7 KB | 表示 | |
| CIF形式データ |  emd_15784_validation.cif.gz emd_15784_validation.cif.gz | 19.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15784 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15784 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15784 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15784 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8b0iMC  8b0jC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15784.map.gz / 形式: CCP4 / 大きさ: 371.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15784.map.gz / 形式: CCP4 / 大きさ: 371.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.652 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_15784_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_15784_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : RapZ tetramer, GlmZ stem loops I & II
| 全体 | 名称: RapZ tetramer, GlmZ stem loops I & II |
|---|---|
| 要素 |
|
-超分子 #1: RapZ tetramer, GlmZ stem loops I & II
| 超分子 | 名称: RapZ tetramer, GlmZ stem loops I & II / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all / 詳細: In vitro reconstituted RapZ and GlmZ complex |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: RNase adapter protein RapZ
| 分子 | 名称: RNase adapter protein RapZ / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 32.53832 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MVLMIVSGRS GSGKSVALRA LEDMGFYCVD NLPVVLLPDL ARTLADREIS AAVSIDVRNM PESPEIFEQA MSNLPDAFSP QLLFLDADR NTLIRRYSDT RRLHPLSSKN LSLESAIDKE SDLLEPLRSR ADLIVDTSEM SVHELAEMLR TRLLGKRERE L TMVFESFG ...文字列: MVLMIVSGRS GSGKSVALRA LEDMGFYCVD NLPVVLLPDL ARTLADREIS AAVSIDVRNM PESPEIFEQA MSNLPDAFSP QLLFLDADR NTLIRRYSDT RRLHPLSSKN LSLESAIDKE SDLLEPLRSR ADLIVDTSEM SVHELAEMLR TRLLGKRERE L TMVFESFG FKHGIPIDAD YVFDVRFLPN PHWDPKLRPM TGLDKPVAAF LDRHTEVHNF IYQTRSYLEL WLPMLETNNR SY LTVAIGC TGGKHRSVYI AEQLADYFRS RGKNVQSRHR TLEKRKP UniProtKB: RNase adapter protein RapZ |
-分子 #2: GlmZ small regulatory RNA
| 分子 | 名称: GlmZ small regulatory RNA / タイプ: rna / ID: 2 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 66.061859 KDa |
| 配列 | 文字列: GUAGAUGCUC AUUCCAUCUC UUAUGUUCGC CUUAGUGCCU CAUAAACUCC GGAAUGACGC AGAGCCGUUU ACGGUGCUUA UCGUCCACU GACAGAUGUC GCUUAUGCCU CAUCAGACAC CAUGGACACA ACGUUGAGUG AAGCACCCAC UUGUUGUCAU A CAGACCUG ...文字列: GUAGAUGCUC AUUCCAUCUC UUAUGUUCGC CUUAGUGCCU CAUAAACUCC GGAAUGACGC AGAGCCGUUU ACGGUGCUUA UCGUCCACU GACAGAUGUC GCUUAUGCCU CAUCAGACAC CAUGGACACA ACGUUGAGUG AAGCACCCAC UUGUUGUCAU A CAGACCUG UUUUAACGCC UGCUCCGUUA AUAAGAGCAG GCGUUUUUU |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | 3D array |
- 試料調製
試料調製
| 濃度 | 5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 / 詳細: 25 mM HEPES pH 7.5, 300 KCl, and 1 mM MgCl2 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 120 sec. |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 47.3 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: DIFFRACTION / 最大 デフォーカス(公称値): 0.3 µm / 最小 デフォーカス(公称値): 0.1 µm |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




 X (Sec.)
X (Sec.) Y (Row.)
Y (Row.) Z (Col.)
Z (Col.)