+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 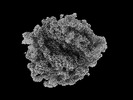 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the E.coli 50S ribosomal subunit in complex with the antibiotic Myxovalargin A. | |||||||||
 マップデータ マップデータ | Masked post processed map | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報transcriptional attenuation / endoribonuclease inhibitor activity / RNA-binding transcription regulator activity / positive regulation of ribosome biogenesis / negative regulation of cytoplasmic translation / DnaA-L2 complex / translation repressor activity / negative regulation of DNA-templated DNA replication initiation / mRNA regulatory element binding translation repressor activity / ribosome assembly ...transcriptional attenuation / endoribonuclease inhibitor activity / RNA-binding transcription regulator activity / positive regulation of ribosome biogenesis / negative regulation of cytoplasmic translation / DnaA-L2 complex / translation repressor activity / negative regulation of DNA-templated DNA replication initiation / mRNA regulatory element binding translation repressor activity / ribosome assembly / assembly of large subunit precursor of preribosome / cytosolic ribosome assembly / ribosomal large subunit assembly / response to reactive oxygen species / regulation of cell growth / DNA-templated transcription termination / response to radiation / mRNA 5'-UTR binding / large ribosomal subunit / ribosome binding / transferase activity / 5S rRNA binding / large ribosomal subunit rRNA binding / cytosolic large ribosomal subunit / cytoplasmic translation / tRNA binding / rRNA binding / negative regulation of translation / ribosome / structural constituent of ribosome / translation / response to antibiotic / negative regulation of DNA-templated transcription / mRNA binding / DNA binding / RNA binding / zinc ion binding / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |    Myxococcus fulvus (バクテリア) Myxococcus fulvus (バクテリア) | |||||||||
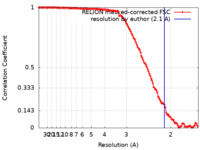
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.1 Å | |||||||||
 データ登録者 データ登録者 | Koller TO / Beckert B / Wilson DN | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: J Am Chem Soc / 年: 2023 ジャーナル: J Am Chem Soc / 年: 2023タイトル: The Myxobacterial Antibiotic Myxovalargin: Biosynthesis, Structural Revision, Total Synthesis, and Molecular Characterization of Ribosomal Inhibition. 著者: Timm O Koller / Ullrich Scheid / Teresa Kösel / Jennifer Herrmann / Daniel Krug / Helena I M Boshoff / Bertrand Beckert / Joanna C Evans / Jan Schlemmer / Becky Sloan / Danielle M Weiner / ...著者: Timm O Koller / Ullrich Scheid / Teresa Kösel / Jennifer Herrmann / Daniel Krug / Helena I M Boshoff / Bertrand Beckert / Joanna C Evans / Jan Schlemmer / Becky Sloan / Danielle M Weiner / Laura E Via / Atica Moosa / Thomas R Ioerger / Michael Graf / Boris Zinshteyn / Maha Abdelshahid / Fabian Nguyen / Stefan Arenz / Franziska Gille / Maik Siebke / Tim Seedorf / Oliver Plettenburg / Rachel Green / Anna-Luisa Warnke / Joachim Ullrich / Ralf Warrass / Clifton E Barry / Digby F Warner / Valerie Mizrahi / Andreas Kirschning / Daniel N Wilson / Rolf Müller /    要旨: Resistance of bacterial pathogens against antibiotics is declared by WHO as a major global health threat. As novel antibacterial agents are urgently needed, we re-assessed the broad-spectrum ...Resistance of bacterial pathogens against antibiotics is declared by WHO as a major global health threat. As novel antibacterial agents are urgently needed, we re-assessed the broad-spectrum myxobacterial antibiotic myxovalargin and found it to be extremely potent against . To ensure compound supply for further development, we studied myxovalargin biosynthesis in detail enabling production via fermentation of a native producer. Feeding experiments as well as functional genomics analysis suggested a structural revision, which was eventually corroborated by the development of a concise total synthesis. The ribosome was identified as the molecular target based on resistant mutant sequencing, and a cryo-EM structure revealed that myxovalargin binds within and completely occludes the exit tunnel, consistent with a mode of action to arrest translation during a late stage of translation initiation. These studies open avenues for structure-based scaffold improvement toward development as an antibacterial agent. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14121.map.gz emd_14121.map.gz | 23 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14121-v30.xml emd-14121-v30.xml emd-14121.xml emd-14121.xml | 52.1 KB 52.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14121_fsc.xml emd_14121_fsc.xml | 12.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14121.png emd_14121.png | 78.8 KB | ||
| その他 |  emd_14121_additional_1.map.gz emd_14121_additional_1.map.gz emd_14121_additional_2.map.gz emd_14121_additional_2.map.gz emd_14121_half_map_1.map.gz emd_14121_half_map_1.map.gz emd_14121_half_map_2.map.gz emd_14121_half_map_2.map.gz | 166.4 MB 139.8 MB 140.5 MB 140.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14121 http://ftp.pdbj.org/pub/emdb/structures/EMD-14121 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14121 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14121 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_14121_validation.pdf.gz emd_14121_validation.pdf.gz | 783.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_14121_full_validation.pdf.gz emd_14121_full_validation.pdf.gz | 783.3 KB | 表示 | |
| XML形式データ |  emd_14121_validation.xml.gz emd_14121_validation.xml.gz | 20.1 KB | 表示 | |
| CIF形式データ |  emd_14121_validation.cif.gz emd_14121_validation.cif.gz | 26.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14121 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14121 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14121 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14121 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7qq3MC  8b7yC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14121.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14121.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Masked post processed map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.828 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: post processed map
| ファイル | emd_14121_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | post processed map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: 3D refined map
| ファイル | emd_14121_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3D refined map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_14121_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_14121_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Cryo-EM structure of the E.coli 50S ribosomal subunit in complex ...
+超分子 #1: Cryo-EM structure of the E.coli 50S ribosomal subunit in complex ...
+分子 #1: 23S ribosomal RNA
+分子 #2: 5S ribosomal RNA
+分子 #3: 50S ribosomal protein L2
+分子 #4: 50S ribosomal protein L3
+分子 #5: 50S ribosomal protein L4
+分子 #6: 50S ribosomal protein L6
+分子 #7: 50S ribosomal protein L13
+分子 #8: 50S ribosomal protein L14
+分子 #9: 50S ribosomal protein L15
+分子 #10: 50S ribosomal protein L16
+分子 #11: 50S ribosomal protein L17
+分子 #12: 50S ribosomal protein L18
+分子 #13: 50S ribosomal protein L19
+分子 #14: 50S ribosomal protein L20
+分子 #15: 50S ribosomal protein L21
+分子 #16: 50S ribosomal protein L22
+分子 #17: 50S ribosomal protein L23
+分子 #18: 50S ribosomal protein L24
+分子 #19: 50S ribosomal protein L25
+分子 #20: 50S ribosomal protein L27
+分子 #21: 50S ribosomal protein L28
+分子 #22: 50S ribosomal protein L29
+分子 #23: 50S ribosomal protein L30
+分子 #24: 50S ribosomal protein L32
+分子 #25: 50S ribosomal protein L33
+分子 #26: 50S ribosomal protein L34
+分子 #27: 50S ribosomal protein L35
+分子 #28: 50S ribosomal protein L36
+分子 #29: Myxovalargin A
+分子 #30: MAGNESIUM ION
+分子 #31: ZINC ION
+分子 #32: water
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
詳細: Solutions were made fresh, pH was adjusted with potassium hydroxide at 4 degrees celcius and sterile filtered. | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: Quantifoil R3/3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 支持フィルム - Film thickness: 300.0 nm | |||||||||||||||||||||
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: 2 seconds blotting before plunging.. | |||||||||||||||||||||
| 詳細 | 7 OD(A260/mL) were applied to the grid. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 44.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー








 Z
Z Y
Y X
X