+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-12675 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | GLIC, pentameric ligand gated ion channel, pH 3 State 2 | |||||||||
 マップデータ マップデータ | 3D Refined map for pH 3 data State 2 | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報sodium channel activity / potassium channel activity / transmembrane transporter complex / extracellular ligand-gated monoatomic ion channel activity / transmembrane signaling receptor activity / identical protein binding / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Gloeobacter violaceus (バクテリア) Gloeobacter violaceus (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 | |||||||||
 データ登録者 データ登録者 | Rovsnik U / Zhuang Y / Forsberg BO / Carroni M / Yvonnesdotter L / Howard RJ / Lindahl E | |||||||||
| 資金援助 |  スウェーデン, 2件 スウェーデン, 2件
| |||||||||
 引用 引用 |  ジャーナル: Life Sci Alliance / 年: 2021 ジャーナル: Life Sci Alliance / 年: 2021タイトル: Dynamic closed states of a ligand-gated ion channel captured by cryo-EM and simulations. 著者: Urška Rovšnik / Yuxuan Zhuang / Björn O Forsberg / Marta Carroni / Linnea Yvonnesdotter / Rebecca J Howard / Erik Lindahl /   要旨: Ligand-gated ion channels are critical mediators of electrochemical signal transduction across evolution. Biophysical and pharmacological characterization of these receptor proteins relies on high- ...Ligand-gated ion channels are critical mediators of electrochemical signal transduction across evolution. Biophysical and pharmacological characterization of these receptor proteins relies on high-quality structures in multiple, subtly distinct functional states. However, structural data in this family remain limited, particularly for resting and intermediate states on the activation pathway. Here, we report cryo-electron microscopy (cryo-EM) structures of the proton-activated ligand-gated ion channel (GLIC) under three pH conditions. Decreased pH was associated with improved resolution and side chain rearrangements at the subunit/domain interface, particularly involving functionally important residues in the β1-β2 and M2-M3 loops. Molecular dynamics simulations substantiated flexibility in the closed-channel extracellular domains relative to the transmembrane ones and supported electrostatic remodeling around E35 and E243 in proton-induced gating. Exploration of secondary cryo-EM classes further indicated a low-pH population with an expanded pore. These results allow us to define distinct protonation and activation steps in pH-stimulated conformational cycling in GLIC, including interfacial rearrangements largely conserved in the pentameric channel family. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_12675.map.gz emd_12675.map.gz | 49.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-12675-v30.xml emd-12675-v30.xml emd-12675.xml emd-12675.xml | 15.2 KB 15.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_12675.png emd_12675.png | 34.2 KB | ||
| マスクデータ |  emd_12675_msk_1.map emd_12675_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| その他 |  emd_12675_additional_1.map.gz emd_12675_additional_1.map.gz emd_12675_half_map_1.map.gz emd_12675_half_map_1.map.gz emd_12675_half_map_2.map.gz emd_12675_half_map_2.map.gz | 9.3 MB 49.7 MB 49.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-12675 http://ftp.pdbj.org/pub/emdb/structures/EMD-12675 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12675 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12675 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_12675_validation.pdf.gz emd_12675_validation.pdf.gz | 464 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_12675_full_validation.pdf.gz emd_12675_full_validation.pdf.gz | 463.6 KB | 表示 | |
| XML形式データ |  emd_12675_validation.xml.gz emd_12675_validation.xml.gz | 12.3 KB | 表示 | |
| CIF形式データ |  emd_12675_validation.cif.gz emd_12675_validation.cif.gz | 14.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12675 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12675 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12675 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12675 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_12675.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_12675.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3D Refined map for pH 3 data State 2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_12675_msk_1.map emd_12675_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
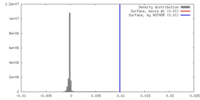
| 密度ヒストグラム |
-追加マップ: Postprocessed map for pH 3 data State 2
| ファイル | emd_12675_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Postprocessed map for pH 3 data State 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
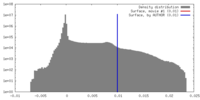
| 密度ヒストグラム |
-ハーフマップ: Half map 2 for pH 3 data state 2
| ファイル | emd_12675_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 for pH 3 data state 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 1 for pH 3 data state 2
| ファイル | emd_12675_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 for pH 3 data state 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
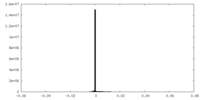
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Pentameric ion channel
| 全体 | 名称: Pentameric ion channel |
|---|---|
| 要素 |
|
-超分子 #1: Pentameric ion channel
| 超分子 | 名称: Pentameric ion channel / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Gloeobacter violaceus (バクテリア) Gloeobacter violaceus (バクテリア) |
| 組換発現 | 生物種:  |
-分子 #1: Proton-gated ion channel
| 分子 | 名称: Proton-gated ion channel / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 配列 | 文字列: AQDMVSPPPP IADEPLTVNT GIYLIECYSL DDKAETFKVN AFLSLSWKDR RLAFDPVRSG VRVKTYEPEA IWIPEIRFVN VENARDADVV DISVSPDGTV QYLERFSARV LSPLDFRRYP FDSQTLHIYL IVRSVDTRNI VLAVDLEKVG KNDDVFLTGW DIESFTAVVK ...文字列: AQDMVSPPPP IADEPLTVNT GIYLIECYSL DDKAETFKVN AFLSLSWKDR RLAFDPVRSG VRVKTYEPEA IWIPEIRFVN VENARDADVV DISVSPDGTV QYLERFSARV LSPLDFRRYP FDSQTLHIYL IVRSVDTRNI VLAVDLEKVG KNDDVFLTGW DIESFTAVVK PANFALEDRL ESKLDYQLRI SRQYFSYIPN IILPMLFILF ISWTAFWSTS YEANVTLVVS TLIAHIAFNI LVETNLPKTP YMTYTGAIIF MIYLFYFVAV IEVTVQHYLK VESQPARAAS ITRASRIAFP VVFLLANIIL AFLFFGF |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3 mg/mL |
|---|---|
| 緩衝液 | pH: 3 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 45.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 使用した粒子像数: 23000 |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー






















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)