+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1216 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-electron tomographic structure of an immunodeficiency virus envelope complex in situ. | |||||||||
 マップデータ マップデータ | This is the volume of the averaged SIV envelope complex | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Simian immunodeficiency virus (サル免疫不全ウイルス) / viral envelope (unknown) Simian immunodeficiency virus (サル免疫不全ウイルス) / viral envelope (unknown) | |||||||||
| 手法 | サブトモグラム平均法 / クライオ電子顕微鏡法 / ネガティブ染色法 / 解像度: 28.0 Å | |||||||||
 データ登録者 データ登録者 | Zanetti G / Briggs JAG / Gruenewald K / Sattentau Q / Fuller SD | |||||||||
 引用 引用 |  ジャーナル: PLoS Pathog / 年: 2006 ジャーナル: PLoS Pathog / 年: 2006タイトル: Cryo-electron tomographic structure of an immunodeficiency virus envelope complex in situ. 著者: Giulia Zanetti / John A G Briggs / Kay Grünewald / Quentin J Sattentau / Stephen D Fuller /  要旨: The envelope glycoprotein (Env) complexes of the human and simian immunodeficiency viruses (HIV and SIV, respectively) mediate viral entry and are a target for neutralizing antibodies. The receptor ...The envelope glycoprotein (Env) complexes of the human and simian immunodeficiency viruses (HIV and SIV, respectively) mediate viral entry and are a target for neutralizing antibodies. The receptor binding surfaces of Env are in large part sterically occluded or conformationally masked prior to receptor binding. Knowledge of the unliganded, trimeric Env structure is key for an understanding of viral entry and immune escape, and for the design of vaccines to elicit neutralizing antibodies. We have used cryo-electron tomography and averaging to obtain the structure of the SIV Env complex prior to fusion. Our result reveals novel details of Env organisation, including tight interaction between monomers in the gp41 trimer, associated with a three-lobed, membrane-distal gp120 trimer. A cavity exists at the gp41-gp120 trimer interface. Our model for the spike structure agrees with previously predicted interactions between gp41 monomers, and furthers our understanding of gp120 interactions within an intact spike. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1216.map.gz emd_1216.map.gz | 519.4 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1216-v30.xml emd-1216-v30.xml emd-1216.xml emd-1216.xml | 18 KB 18 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1216.gif 1216.gif | 7.4 KB | ||
| マスクデータ |  emd_1216_msk_1.map emd_1216_msk_1.map emd_1216_msk_2.map emd_1216_msk_2.map | 977.7 KB 977.7 KB |  マスクマップ マスクマップ | |
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1216 http://ftp.pdbj.org/pub/emdb/structures/EMD-1216 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1216 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1216 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1216_validation.pdf.gz emd_1216_validation.pdf.gz | 212.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1216_full_validation.pdf.gz emd_1216_full_validation.pdf.gz | 211.4 KB | 表示 | |
| XML形式データ |  emd_1216_validation.xml.gz emd_1216_validation.xml.gz | 5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1216 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1216 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1216 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1216 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1216.map.gz / 形式: CCP4 / 大きさ: 955.1 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1216.map.gz / 形式: CCP4 / 大きさ: 955.1 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | This is the volume of the averaged SIV envelope complex | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 5.47 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
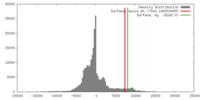
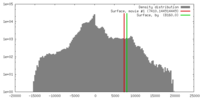
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-セグメンテーションマップ: The mask for the averaged SIV envelope complex
| 注釈 | The mask for the averaged SIV envelope complex | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ファイル |  emd_1216_msk_1.map emd_1216_msk_1.map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-セグメンテーションマップ: Protein with the mask applied is the simple...
| 注釈 | Protein with the mask applied is the simple multiplication of the spike protein map (emd_1216.map) with the mask (emd_1216_mask_1.map) | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ファイル |  emd_1216_msk_2.map emd_1216_msk_2.map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Simian Immunodeficiency Virus mne Envelope Complex
| 全体 | 名称: Simian Immunodeficiency Virus mne Envelope Complex |
|---|---|
| 要素 |
|
-超分子 #1000: Simian Immunodeficiency Virus mne Envelope Complex
| 超分子 | 名称: Simian Immunodeficiency Virus mne Envelope Complex / タイプ: sample / ID: 1000 詳細: The envelope complex wasn't purified but it was analysed on the virus 集合状態: trimer of Gp120 and trimer of Gp41 and membrane Number unique components: 3 |
|---|---|
| 分子量 | 実験値: 500 KDa / 理論値: 500 KDa 手法: sum of individual components is an underestimate due to the presence of the membrane |
-超分子 #1: viral envelope
| 超分子 | 名称: viral envelope / タイプ: virus / ID: 1 / Name.synonym: viral membrane / 詳細: viral membrane / 生物種: viral envelope / データベース: NCBI / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No / Syn species name: viral membrane |
|---|---|
| 宿主 | 生物種:  |
| ウイルス殻 | Shell ID: 1 / 名称: membrane / 直径: 1200 Å |
-分子 #1: gp120
| 分子 | 名称: gp120 / タイプ: protein_or_peptide / ID: 1 / Name.synonym: SIV envelope receptor binding protein / 詳細: trimeric / コピー数: 3 / 集合状態: trimer / 組換発現: No / データベース: NCBI |
|---|---|
| 由来(天然) | 生物種:  Simian immunodeficiency virus (サル免疫不全ウイルス) Simian immunodeficiency virus (サル免疫不全ウイルス)株: SIVMneCL8 / 別称: SIVmne / 細胞: HuT 78 / 細胞中の位置: viral membrane |
| 分子量 | 実験値: 120 KDa / 理論値: 120 KDa |
-分子 #2: gp41
| 分子 | 名称: gp41 / タイプ: protein_or_peptide / ID: 2 / Name.synonym: SIV envelope transmembrane protein / 詳細: trimeric / コピー数: 3 / 集合状態: trimer / 組換発現: No / データベース: NCBI |
|---|---|
| 由来(天然) | 生物種:  Simian immunodeficiency virus (サル免疫不全ウイルス) Simian immunodeficiency virus (サル免疫不全ウイルス)株: SIVMneCL8 / 別称: SIVmne / 細胞: HuT 78 / 細胞中の位置: viral membrane |
| 分子量 | 実験値: 41 KDa / 理論値: 41 KDa |
-実験情報
-構造解析
| 手法 | ネガティブ染色法, クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1 mg/mL |
|---|---|
| 緩衝液 | pH: 7.2 / 詳細: PBS |
| 染色 | タイプ: NEGATIVE 詳細: Samples were mixed with BSA adsorbed 10 nm colloidal gold and vitrified for cryoelectron microscopy. |
| グリッド | 詳細: holey carbon film |
| 凍結 | 凍結剤: ETHANE / 装置: HOMEMADE PLUNGER / 詳細: Vitrification instrument: home built / 手法: blot for two seconds before plunging |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI/PHILIPS CM300FEG/ST |
|---|---|
| 温度 | 平均: 77 K |
| 特殊光学系 | エネルギーフィルター - 名称: GATAN GIF 2002 エネルギーフィルター - エネルギー下限: 0.0 eV エネルギーフィルター - エネルギー上限: 20.0 eV |
| 詳細 | We collected a tilt series |
| 日付 | 2005年10月1日 |
| 撮影 | カテゴリ: CCD / フィルム・検出器のモデル: GENERIC GATAN / デジタル化 - サンプリング間隔: 30 µm / 実像数: 3 / 平均電子線量: 57 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.0 mm / 最大 デフォーカス(公称値): 0.6 µm / 最小 デフォーカス(公称値): 0.4 µm / 倍率(公称値): 27500 |
| 試料ステージ | 試料ホルダー: eucentric / 試料ホルダーモデル: GATAN LIQUID NITROGEN / Tilt series - Axis1 - Min angle: 69.0 ° / Tilt series - Axis1 - Max angle: 63 ° |
- 画像解析
画像解析
| 詳細 | Average number of projections used in the 3D reconstructions: 2986. |
|---|---|
| 最終 再構成 | アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 28.0 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: TOM 詳細: envelope complexes were averaged to give a final map of 28A resolution as determined by FSC at 0.5 cut-off. |
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| ソフトウェア | 名称: URO |
| 詳細 | PDBEntryID_givenInChain. Protocol: rigid body. The gp120 monomer was manually fitted and three-fold symmetry was imposed during fitting with URO |
| 精密化 | 空間: RECIPROCAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: quadratic misfit |
 ムービー
ムービー コントローラー
コントローラー









 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)