+検索条件
-Structure paper
| タイトル | Molecular basis for different substrate-binding sites and chaperone functions of the BRICHOS domain. |
|---|---|
| ジャーナル・号・ページ | Protein Sci, Vol. 33, Issue 7, Page e5063, Year 2024 |
| 掲載日 | 2024年6月12日 |
 著者 著者 | Gefei Chen / Yu Wang / Zihan Zheng / Wangshu Jiang / Axel Leppert / Xueying Zhong / Anna Belorusova / Gregg Siegal / Caroline Jegerschöld / Philip J B Koeck / Axel Abelein / Hans Hebert / Stefan D Knight / Jan Johansson /    |
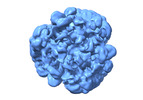
| PubMed 要旨 | Proteins can misfold into fibrillar or amorphous aggregates and molecular chaperones act as crucial guardians against these undesirable processes. The BRICHOS chaperone domain, found in several ...Proteins can misfold into fibrillar or amorphous aggregates and molecular chaperones act as crucial guardians against these undesirable processes. The BRICHOS chaperone domain, found in several otherwise unrelated proproteins that contain amyloidogenic regions, effectively inhibits amyloid formation and toxicity but can in some cases also prevent non-fibrillar, amorphous protein aggregation. Here, we elucidate the molecular basis behind the multifaceted chaperone activities of the BRICHOS domain from the Bri2 proprotein. High-confidence AlphaFold2 and RoseTTAFold predictions suggest that the intramolecular amyloidogenic region (Bri23) is part of the hydrophobic core of the proprotein, where it occupies the proposed amyloid binding site, explaining the markedly reduced ability of the proprotein to prevent an exogenous amyloidogenic peptide from aggregating. However, the BRICHOS-Bri23 complex maintains its ability to form large polydisperse oligomers that prevent amorphous protein aggregation. A cryo-EM-derived model of the Bri2 BRICHOS oligomer is compatible with surface-exposed hydrophobic motifs that get exposed and come together during oligomerization, explaining its effects against amorphous aggregation. These findings provide a molecular basis for the BRICHOS chaperone domain function, where distinct surfaces are employed against different forms of protein aggregation. |
 リンク リンク |  Protein Sci / Protein Sci /  PubMed:38864729 / PubMed:38864729 /  PubMed Central PubMed Central |
| 手法 | EM (単粒子) |
| 解像度 | 3.4 Å |
| 構造データ | EMDB-19395, PDB-8rnu: |
| 由来 |
|
 キーワード キーワード | CHAPERONE / anti-amyloid / dementia / Bri2 |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について




 homo sapiens (ヒト)
homo sapiens (ヒト)