+検索条件
-Structure paper
| タイトル | Structural basis of CXC chemokine receptor 2 activation and signalling. |
|---|---|
| ジャーナル・号・ページ | Nature, Vol. 585, Issue 7823, Page 135-140, Year 2020 |
| 掲載日 | 2020年7月1日 |
 著者 著者 | Kaiwen Liu / Lijie Wu / Shuguang Yuan / Meng Wu / Yueming Xu / Qianqian Sun / Shu Li / Suwen Zhao / Tian Hua / Zhi-Jie Liu /  |
| PubMed 要旨 | Chemokines and their receptors mediate cell migration, which influences multiple fundamental biological processes and disease conditions such as inflammation and cancer. Although ample effort has ...Chemokines and their receptors mediate cell migration, which influences multiple fundamental biological processes and disease conditions such as inflammation and cancer. Although ample effort has been invested into the structural investigation of the chemokine receptors and receptor-chemokine recognition, less is known about endogenous chemokine-induced receptor activation and G-protein coupling. Here we present the cryo-electron microscopy structures of interleukin-8 (IL-8, also known as CXCL8)-activated human CXC chemokine receptor 2 (CXCR2) in complex with G protein, along with a crystal structure of CXCR2 bound to a designed allosteric antagonist. Our results reveal a unique shallow mode of binding between CXCL8 and CXCR2, and also show the interactions between CXCR2 and G protein. Further structural analysis of the inactive and active states of CXCR2 reveals a distinct activation process and the competitive small-molecule antagonism of chemokine receptors. In addition, our results provide insights into how a G-protein-coupled receptor is activated by an endogenous protein molecule, which will assist in the rational development of therapeutics that target the chemokine system for better pharmacological profiles. |
 リンク リンク |  Nature / Nature /  PubMed:32610344 PubMed:32610344 |
| 手法 | EM (単粒子) / X線回折 |
| 解像度 | 3.2 - 3.5 Å |
| 構造データ |  PDB-6lfl: |
| 化合物 | 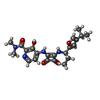 ChemComp-EBX:  ChemComp-CLR: |
| 由来 |
|
 キーワード キーワード | MEMBRANE PROTEIN / G protein-coupled receptor / G protein coupled-receptor |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について







 homo sapiens (ヒト)
homo sapiens (ヒト)
 pyrococcus abyssi (strain ge5 / orsay) (古細菌)
pyrococcus abyssi (strain ge5 / orsay) (古細菌)