+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-32044 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of human KCNQ4-ML213 complex with PIP2 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | KCNQ4 / ML213 / PIP2 / cryo-EM / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Voltage gated Potassium channels / Sensory processing of sound by outer hair cells of the cochlea / Sensory processing of sound by inner hair cells of the cochlea / inner ear morphogenesis / negative regulation of high voltage-gated calcium channel activity / positive regulation of cyclic-nucleotide phosphodiesterase activity / negative regulation of calcium ion export across plasma membrane / regulation of cardiac muscle cell action potential / positive regulation of ryanodine-sensitive calcium-release channel activity / regulation of cell communication by electrical coupling involved in cardiac conduction ...Voltage gated Potassium channels / Sensory processing of sound by outer hair cells of the cochlea / Sensory processing of sound by inner hair cells of the cochlea / inner ear morphogenesis / negative regulation of high voltage-gated calcium channel activity / positive regulation of cyclic-nucleotide phosphodiesterase activity / negative regulation of calcium ion export across plasma membrane / regulation of cardiac muscle cell action potential / positive regulation of ryanodine-sensitive calcium-release channel activity / regulation of cell communication by electrical coupling involved in cardiac conduction / negative regulation of peptidyl-threonine phosphorylation / negative regulation of ryanodine-sensitive calcium-release channel activity / protein phosphatase activator activity / : / adenylate cyclase binding / voltage-gated potassium channel activity / catalytic complex / carbohydrate transmembrane transporter activity / potassium channel activity / detection of calcium ion / regulation of cardiac muscle contraction / regulation of cardiac muscle contraction by regulation of the release of sequestered calcium ion / voltage-gated potassium channel complex / regulation of release of sequestered calcium ion into cytosol by sarcoplasmic reticulum / : / titin binding / positive regulation of protein autophosphorylation / regulation of calcium-mediated signaling / sperm midpiece / calcium channel complex / potassium ion transmembrane transport / substantia nigra development / adenylate cyclase activator activity / regulation of heart rate / sarcomere / protein serine/threonine kinase activator activity / basal plasma membrane / regulation of cytokinesis / positive regulation of peptidyl-threonine phosphorylation / spindle microtubule / sensory perception of sound / positive regulation of protein serine/threonine kinase activity / potassium ion transport / spindle pole / response to calcium ion / calcium-dependent protein binding / G2/M transition of mitotic cell cycle / myelin sheath / outer membrane-bounded periplasmic space / vesicle / transmembrane transporter binding / G protein-coupled receptor signaling pathway / centrosome / calcium ion binding / protein kinase binding / protein-containing complex / nucleus / plasma membrane / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.79 Å | |||||||||
 データ登録者 データ登録者 | Xu F / Zheng Y | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Neuron / 年: 2022 ジャーナル: Neuron / 年: 2022タイトル: Structural insights into the lipid and ligand regulation of a human neuronal KCNQ channel. 著者: You Zheng / Heng Liu / Yuxin Chen / Shaowei Dong / Fang Wang / Shengyi Wang / Geng-Lin Li / Yilai Shu / Fei Xu /  要旨: The KCNQ family (KCNQ1-KCNQ5) of voltage-gated potassium channels plays critical roles in many physiological and pathological processes. It is known that the channel opening of all KCNQs relies on ...The KCNQ family (KCNQ1-KCNQ5) of voltage-gated potassium channels plays critical roles in many physiological and pathological processes. It is known that the channel opening of all KCNQs relies on the signaling lipid molecule phosphatidylinositol 4,5-bisphosphate (PIP2). However, the molecular mechanism of PIP2 in modulating the opening of the four neuronal KCNQ channels (KCNQ2-KCNQ5), which are essential for regulating neuronal excitability, remains largely elusive. Here, we report the cryoelectron microscopy (cryo-EM) structures of human KCNQ4 determined in complex with the activator ML213 in the absence or presence of PIP2. Two PIP2 molecules are identified in the open-state structure of KCNQ4, which act as a bridge to couple the voltage-sensing domain (VSD) and pore domain (PD) of KCNQ4 leading to the channel opening. Our findings reveal the binding sites and activation mechanisms of ML213 and PIP2 for neuronal KCNQ channels, providing a framework for therapeutic intervention targeting on these important channels. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32044.map.gz emd_32044.map.gz | 96.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32044-v30.xml emd-32044-v30.xml emd-32044.xml emd-32044.xml | 12.7 KB 12.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_32044.png emd_32044.png | 70.7 KB | ||
| Filedesc metadata |  emd-32044.cif.gz emd-32044.cif.gz | 6.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32044 http://ftp.pdbj.org/pub/emdb/structures/EMD-32044 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32044 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32044 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_32044_validation.pdf.gz emd_32044_validation.pdf.gz | 543.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_32044_full_validation.pdf.gz emd_32044_full_validation.pdf.gz | 543.2 KB | 表示 | |
| XML形式データ |  emd_32044_validation.xml.gz emd_32044_validation.xml.gz | 6.4 KB | 表示 | |
| CIF形式データ |  emd_32044_validation.cif.gz emd_32044_validation.cif.gz | 7.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32044 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32044 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32044 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32044 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32044.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32044.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : KCNQ4-ML213 complex with PIP2
| 全体 | 名称: KCNQ4-ML213 complex with PIP2 |
|---|---|
| 要素 |
|
-超分子 #1: KCNQ4-ML213 complex with PIP2
| 超分子 | 名称: KCNQ4-ML213 complex with PIP2 / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Potassium voltage-gated channel subfamily KQT member 4,Maltodextr...
| 分子 | 名称: Potassium voltage-gated channel subfamily KQT member 4,Maltodextrin-binding protein タイプ: protein_or_peptide / ID: 1 詳細: The fusion protein of Potassium voltage-gated channel subfamily KQT member 4, linker, and Maltodextrin-binding protein コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: B / BL21-DE3 |
| 分子量 | 理論値: 116.541383 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MDYKDDDDKA EAPPRRLGLG PPPGDAPRAE LVALTAVQSE QGEAGGGGSP RRLGLLGSPL PPGAPLPGPG SGSGSACGQR SSAAHKRYR RLQNWVYNVL ERPRGWAFVY HVFIFLLVFS CLVLSVLSTI QEHQELANEC LLILEFVMIV VFGLEYIVRV W SAGCCCRY ...文字列: MDYKDDDDKA EAPPRRLGLG PPPGDAPRAE LVALTAVQSE QGEAGGGGSP RRLGLLGSPL PPGAPLPGPG SGSGSACGQR SSAAHKRYR RLQNWVYNVL ERPRGWAFVY HVFIFLLVFS CLVLSVLSTI QEHQELANEC LLILEFVMIV VFGLEYIVRV W SAGCCCRY RGWQGRFRFA RKPFCVIDFI VFVASVAVIA AGTQGNIFAT SALRSMRFLQ ILRMVRMDRR GGTWKLLGSV VY AHSKELI TAWYIGFLVL IFASFLVYLA EKDANSDFSS YADSLWWGTI TLTTIGYGDK TPHTWLGRVL AAGFALLGIS FFA LPAGIL GSGFALKVQE QHRQKHFEKR RMPAANLIQA AWRLYSTDMS RAYLTATWYY YDSILPSFRE LALLFEHVQR ARNG GLRPL EVRRAPVPDG APSRYPPVAT CHRPGSTSFC PGESSRMGIK DRIRMGSSQR RTGPSKQHLA PPTMPTSPSS EQVGE ATSP TKVQKSWSFN DRTRFRASLR LKPRTSAEDA PSEEVAEEKS YQCELTVDDI MPAVKTVIRS IRILKFLVAK RKFKET LRP YDVKDVIEQY SAGHLDMLGR IKSLQTRVDQ IVGRGPGDRK AREKGDKGPS DAEVVDEISM MGRVVKVEKQ VQSIEHK LD LLLGFYSRCL RSGTSALEVL FQGPMAKIEE GKLVIWINGD KGYNGLAEVG KKFEKDTGIK VTVEHPDKLE EKFPQVAA T GDGPDIIFWA HDRFGGYAQS GLLAEITPDK AFQDKLYPFT WDAVRYNGKL IAYPIAVEAL SLIYNKDLLP NPPKTWEEI PALDKELKAK GKSALMFNLQ EPYFTWPLIA ADGGYAFKYE NGKYDIKDVG VDNAGAKAGL TFLVDLIKNK HMNADTDYSI AEAAFNKGE TAMTINGPWA WSNIDTSKVN YGVTVLPTFK GQPSKPFVGV LSAGINAASP NKELAKEFLE NYLLTDEGLE A VNKDKPLG AVALKSYEEE LAKDPRIAAT MENAQKGEIM PNIPQMSAFW YAVRTAVINA ASGRQTVDEA LKDAQTNAAA EH HHHHHHH HH UniProtKB: Potassium voltage-gated channel subfamily KQT member 4, Maltodextrin-binding protein |
-分子 #2: Calmodulin-3
| 分子 | 名称: Calmodulin-3 / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 16.852545 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MADQLTEEQI AEFKEAFSLF DKDGDGTITT KELGTVMRSL GQNPTEAELQ DMINEVDADG NGTIDFPEFL TMMARKMKDT DSEEEIREA FRVFDKDGNG YISAAELRHV MTNLGEKLTD EEVDEMIREA DIDGDGQVNY EEFVQMMTAK UniProtKB: Calmodulin-3 |
-分子 #3: [(2R)-1-octadecanoyloxy-3-[oxidanyl-[(1R,2R,3S,4R,5R,6S)-2,3,6-tr...
| 分子 | 名称: [(2R)-1-octadecanoyloxy-3-[oxidanyl-[(1R,2R,3S,4R,5R,6S)-2,3,6-tris(oxidanyl)-4,5-diphosphonooxy-cyclohexyl]oxy-phospho ryl]oxy-propan-2-yl] (8Z)-icosa-5,8,11,14-tetraenoate タイプ: ligand / ID: 3 / コピー数: 8 / 式: PT5 |
|---|---|
| 分子量 | 理論値: 1.047088 KDa |
-分子 #4: POTASSIUM ION
| 分子 | 名称: POTASSIUM ION / タイプ: ligand / ID: 4 / コピー数: 4 / 式: K |
|---|---|
| 分子量 | 理論値: 39.098 Da |
-分子 #5: (1S,2S,4R)-N-(2,4,6-trimethylphenyl)bicyclo[2.2.1]heptane-2-carboxamid
| 分子 | 名称: (1S,2S,4R)-N-(2,4,6-trimethylphenyl)bicyclo[2.2.1]heptane-2-carboxamid タイプ: ligand / ID: 5 / コピー数: 4 / 式: 7YV |
|---|---|
| 分子量 | 理論値: 257.371 Da |
| Chemical component information | 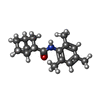 ChemComp-7YV: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 16.8 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: DARK FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.79 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 133661 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















