[English] 日本語
 Yorodumi
Yorodumi- PDB-6mdq: Crystal structure of equine serum albumin in complex with testosterone -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6mdq | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of equine serum albumin in complex with testosterone | ||||||
 Components Components | Serum albumin | ||||||
 Keywords Keywords |  TRANSPORT PROTEIN / TRANSPORT PROTEIN /  Albumin / Equine Serum Albumin / Albumin / Equine Serum Albumin /  Testosterone / CSGID / Testosterone / CSGID /  Structural Genomics / Center for Structural Genomics of Infectious Diseases Structural Genomics / Center for Structural Genomics of Infectious Diseases | ||||||
| Function / homology |  Function and homology information Function and homology informationcellular response to calcium ion starvation /  enterobactin binding / negative regulation of mitochondrial depolarization / enterobactin binding / negative regulation of mitochondrial depolarization /  toxic substance binding / cellular response to starvation / toxic substance binding / cellular response to starvation /  fatty acid binding / fatty acid binding /  pyridoxal phosphate binding / protein-containing complex / pyridoxal phosphate binding / protein-containing complex /  DNA binding / DNA binding /  extracellular space ...cellular response to calcium ion starvation / extracellular space ...cellular response to calcium ion starvation /  enterobactin binding / negative regulation of mitochondrial depolarization / enterobactin binding / negative regulation of mitochondrial depolarization /  toxic substance binding / cellular response to starvation / toxic substance binding / cellular response to starvation /  fatty acid binding / fatty acid binding /  pyridoxal phosphate binding / protein-containing complex / pyridoxal phosphate binding / protein-containing complex /  DNA binding / DNA binding /  extracellular space / extracellular space /  metal ion binding / metal ion binding /  cytoplasm cytoplasmSimilarity search - Function | ||||||
| Biological species |   Equus caballus (horse) Equus caballus (horse) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.15 Å MOLECULAR REPLACEMENT / Resolution: 2.15 Å | ||||||
 Authors Authors | Czub, M.P. / Majorek, K.A. / Shabalin, I.G. / Handing, K.B. / Venkataramany, B.S. / Cymborowski, M.T. / Satchell, K.J. / Joachimiak, A. / Minor, W. / Center for Structural Genomics of Infectious Diseases (CSGID) | ||||||
| Funding support |  United States, 1items United States, 1items
| ||||||
 Citation Citation |  Journal: Chem Sci / Year: 2019 Journal: Chem Sci / Year: 2019Title: Testosterone meets albumin - the molecular mechanism of sex hormone transport by serum albumins. Authors: Czub, M.P. / Venkataramany, B.S. / Majorek, K.A. / Handing, K.B. / Porebski, P.J. / Beeram, S.R. / Suh, K. / Woolfork, A.G. / Hage, D.S. / Shabalin, I.G. / Minor, W. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6mdq.cif.gz 6mdq.cif.gz | 248.2 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6mdq.ent.gz pdb6mdq.ent.gz | 198.1 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6mdq.json.gz 6mdq.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/md/6mdq https://data.pdbj.org/pub/pdb/validation_reports/md/6mdq ftp://data.pdbj.org/pub/pdb/validation_reports/md/6mdq ftp://data.pdbj.org/pub/pdb/validation_reports/md/6mdq | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  3v08S S: Starting model for refinement |
|---|---|
| Similar structure data | |
| Other databases |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein |  Mass: 65768.086 Da / Num. of mol.: 1 / Source method: isolated from a natural source / Source: (natural)   Equus caballus (horse) / References: UniProt: P35747 Equus caballus (horse) / References: UniProt: P35747 | ||||||
|---|---|---|---|---|---|---|---|
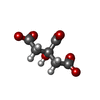
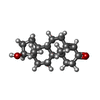
| #2: Chemical |  Citric acid Citric acid#3: Chemical |  Testosterone Testosterone#4: Water | ChemComp-HOH / |  Water WaterSequence details | this mutation is characteristic for Equus ferus przewalskii, a rare subspecies of wild horse from ...this mutation is characteristic for Equus ferus przewalskii, a rare subspecies of wild horse from central Asia. See NCBI database, accession code: XP_008524663.1 | |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.79 Å3/Da / Density % sol: 55.91 % |
|---|---|
Crystal grow | Temperature: 289 K / Method: vapor diffusion, sitting drop / pH: 7 Details: 0.2 ul of 15 mg/ml protein was mixed with 0.2 ul of the well condition (1.8 M ammonium dihydrogen citrate, pH 7.0) and equilibrated against well solution in 96-Well sitting drop ...Details: 0.2 ul of 15 mg/ml protein was mixed with 0.2 ul of the well condition (1.8 M ammonium dihydrogen citrate, pH 7.0) and equilibrated against well solution in 96-Well sitting drop crystallization plate (Swissci). Testosterone powder was added to the crystallization drop |
-Data collection
| Diffraction | Mean temperature: 100 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 21-ID-F / Wavelength: 0.97872 Å / Beamline: 21-ID-F / Wavelength: 0.97872 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: MARMOSAIC 225 mm CCD / Detector: CCD / Date: Jul 6, 2011 / Details: Beryllium Lenses | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Monochromator: Diamond [111] / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength : 0.97872 Å / Relative weight: 1 : 0.97872 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 2.15→50 Å / Num. obs: 39149 / % possible obs: 99.7 % / Redundancy: 7.6 % / Rmerge(I) obs: 0.071 / Rpim(I) all: 0.028 / Rrim(I) all: 0.076 / Χ2: 0.981 / Net I/σ(I): 10 / Num. measured all: 298193 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 3V08 Resolution: 2.15→50 Å / Cor.coef. Fo:Fc: 0.966 / Cor.coef. Fo:Fc free: 0.947 / SU B: 12.041 / SU ML: 0.15 / SU R Cruickshank DPI: 0.2083 / Cross valid method: THROUGHOUT / σ(F): 0 / ESU R: 0.208 / ESU R Free: 0.178 Details: U VALUES : WITH TLS ADDED HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.2 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 209.58 Å2 / Biso mean: 64.487 Å2 / Biso min: 34.79 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 2.15→50 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 2.15→2.206 Å / Rfactor Rfree error: 0 / Total num. of bins used: 20
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller






















 PDBj
PDBj