| 登録情報 | データベース: PDB / ID: 5vih
|
|---|
| タイトル | Crystal structure of GluN1/GluN2A NMDA receptor agonist binding domains with glycine and antagonist, 4-fluorophenyl-ACEPC |
|---|
 要素 要素 | (Glutamate receptor ionotropic, NMDA ...) x 2 |
|---|
 キーワード キーワード |  TRANSPORT PROTEIN (運搬体タンパク質) / TRANSPORT PROTEIN (運搬体タンパク質) /  RECEPTOR (受容体) / RECEPTOR (受容体) /  NMDA receptor (NMDA型グルタミン酸受容体) / NMDA receptor (NMDA型グルタミン酸受容体) /  Antagonist (受容体拮抗薬) Antagonist (受容体拮抗薬) |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
neurotransmitter receptor transport, plasma membrane to endosome / regulation of response to alcohol / response to ammonium ion / receptor recycling / directional locomotion /  conditioned place preference / pons maturation / conditioned place preference / pons maturation /  regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment ...neurotransmitter receptor transport, plasma membrane to endosome / regulation of response to alcohol / response to ammonium ion / receptor recycling / directional locomotion / regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment ...neurotransmitter receptor transport, plasma membrane to endosome / regulation of response to alcohol / response to ammonium ion / receptor recycling / directional locomotion /  conditioned place preference / pons maturation / conditioned place preference / pons maturation /  regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment / EPHB-mediated forward signaling / Assembly and cell surface presentation of NMDA receptors / response to hydrogen sulfide / olfactory learning / serotonin metabolic process / regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment / EPHB-mediated forward signaling / Assembly and cell surface presentation of NMDA receptors / response to hydrogen sulfide / olfactory learning / serotonin metabolic process /  conditioned taste aversion / conditioned taste aversion /  樹状突起 / regulation of respiratory gaseous exchange / protein localization to postsynaptic membrane / response to other organism / positive regulation of inhibitory postsynaptic potential / propylene metabolic process / response to glycine / regulation of ARF protein signal transduction / cellular response to magnesium ion / response to methylmercury / 樹状突起 / regulation of respiratory gaseous exchange / protein localization to postsynaptic membrane / response to other organism / positive regulation of inhibitory postsynaptic potential / propylene metabolic process / response to glycine / regulation of ARF protein signal transduction / cellular response to magnesium ion / response to methylmercury /  睡眠 / voltage-gated monoatomic cation channel activity / cellular response to dsRNA / dendritic spine organization / response to carbohydrate / locomotion / regulation of monoatomic cation transmembrane transport / response to morphine / cellular response to lipid / 睡眠 / voltage-gated monoatomic cation channel activity / cellular response to dsRNA / dendritic spine organization / response to carbohydrate / locomotion / regulation of monoatomic cation transmembrane transport / response to morphine / cellular response to lipid /  NMDA glutamate receptor activity / Synaptic adhesion-like molecules / RAF/MAP kinase cascade / NMDA selective glutamate receptor complex / glutamate-gated calcium ion channel activity / parallel fiber to Purkinje cell synapse / response to manganese ion / calcium ion transmembrane import into cytosol / NMDA glutamate receptor activity / Synaptic adhesion-like molecules / RAF/MAP kinase cascade / NMDA selective glutamate receptor complex / glutamate-gated calcium ion channel activity / parallel fiber to Purkinje cell synapse / response to manganese ion / calcium ion transmembrane import into cytosol /  regulation of NMDA receptor activity / protein heterotetramerization / regulation of NMDA receptor activity / protein heterotetramerization /  glutamate binding / cellular response to zinc ion / positive regulation of reactive oxygen species biosynthetic process / neuromuscular process / glutamate binding / cellular response to zinc ion / positive regulation of reactive oxygen species biosynthetic process / neuromuscular process /  regulation of synapse assembly / regulation of synapse assembly /  活動電位 / 活動電位 /  glycine binding / positive regulation of calcium ion transport into cytosol / regulation of dendrite morphogenesis / male mating behavior / glycine binding / positive regulation of calcium ion transport into cytosol / regulation of dendrite morphogenesis / male mating behavior /  regulation of axonogenesis / spinal cord development / dopamine metabolic process / suckling behavior / regulation of axonogenesis / spinal cord development / dopamine metabolic process / suckling behavior /  startle response / monoatomic cation transmembrane transport / regulation of neuronal synaptic plasticity / response to amine / modulation of excitatory postsynaptic potential / response to lithium ion / startle response / monoatomic cation transmembrane transport / regulation of neuronal synaptic plasticity / response to amine / modulation of excitatory postsynaptic potential / response to lithium ion /  social behavior / social behavior /  学習 / positive regulation of excitatory postsynaptic potential / monoatomic cation transport / ligand-gated monoatomic ion channel activity / 学習 / positive regulation of excitatory postsynaptic potential / monoatomic cation transport / ligand-gated monoatomic ion channel activity /  excitatory synapse / cellular response to glycine / positive regulation of dendritic spine maintenance / response to light stimulus / Unblocking of NMDA receptors, glutamate binding and activation / neuron development / positive regulation of protein targeting to membrane / regulation of postsynaptic membrane potential / excitatory synapse / cellular response to glycine / positive regulation of dendritic spine maintenance / response to light stimulus / Unblocking of NMDA receptors, glutamate binding and activation / neuron development / positive regulation of protein targeting to membrane / regulation of postsynaptic membrane potential /  phosphatase binding / phosphatase binding /  glutamate receptor binding / glutamate receptor binding /  postsynaptic density, intracellular component / calcium ion homeostasis / cellular response to manganese ion / postsynaptic density, intracellular component / calcium ion homeostasis / cellular response to manganese ion /  prepulse inhibition / multicellular organismal response to stress / prepulse inhibition / multicellular organismal response to stress /  long-term memory / monoatomic cation channel activity / regulation of neuron apoptotic process / presynaptic active zone membrane / long-term memory / monoatomic cation channel activity / regulation of neuron apoptotic process / presynaptic active zone membrane /  synaptic cleft / glutamate-gated receptor activity / response to fungicide / sensory perception of pain / synaptic cleft / glutamate-gated receptor activity / response to fungicide / sensory perception of pain /  cell adhesion molecule binding / dendrite membrane / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / response to amphetamine / ionotropic glutamate receptor signaling pathway / cell adhesion molecule binding / dendrite membrane / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / response to amphetamine / ionotropic glutamate receptor signaling pathway /  excitatory postsynaptic potential / hippocampal mossy fiber to CA3 synapse類似検索 - 分子機能 excitatory postsynaptic potential / hippocampal mossy fiber to CA3 synapse類似検索 - 分子機能 : / : / Glutamate [NMDA] receptor, epsilon subunit, C-terminal / N-methyl D-aspartate receptor 2B3 C-terminus / Bacterial extracellular solute-binding proteins, family 3 / Solute-binding protein family 3/N-terminal domain of MltF /  Ionotropic glutamate receptor, metazoa / Ligated ion channel L-glutamate- and glycine-binding site / : / Ionotropic glutamate receptor, metazoa / Ligated ion channel L-glutamate- and glycine-binding site / : /  リガンド依存性イオンチャネル ...: / : / Glutamate [NMDA] receptor, epsilon subunit, C-terminal / N-methyl D-aspartate receptor 2B3 C-terminus / Bacterial extracellular solute-binding proteins, family 3 / Solute-binding protein family 3/N-terminal domain of MltF / リガンド依存性イオンチャネル ...: / : / Glutamate [NMDA] receptor, epsilon subunit, C-terminal / N-methyl D-aspartate receptor 2B3 C-terminus / Bacterial extracellular solute-binding proteins, family 3 / Solute-binding protein family 3/N-terminal domain of MltF /  Ionotropic glutamate receptor, metazoa / Ligated ion channel L-glutamate- and glycine-binding site / : / Ionotropic glutamate receptor, metazoa / Ligated ion channel L-glutamate- and glycine-binding site / : /  リガンド依存性イオンチャネル / リガンド依存性イオンチャネル /  Ionotropic glutamate receptor, L-glutamate and glycine-binding domain / Ligated ion channel L-glutamate- and glycine-binding site / Ionotropic glutamate receptor, L-glutamate and glycine-binding domain / Ligated ion channel L-glutamate- and glycine-binding site /  Ionotropic glutamate receptor / Eukaryotic homologues of bacterial periplasmic substrate binding proteins. / Ionotropic glutamate receptor / Eukaryotic homologues of bacterial periplasmic substrate binding proteins. /  Receptor, ligand binding region / Receptor family ligand binding region / Periplasmic binding protein-like II / Periplasmic binding protein-like I / D-Maltodextrin-Binding Protein; domain 2 / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 Receptor, ligand binding region / Receptor family ligand binding region / Periplasmic binding protein-like II / Periplasmic binding protein-like I / D-Maltodextrin-Binding Protein; domain 2 / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 Chem-5DZ /  グリシン / DI(HYDROXYETHYL)ETHER / Glutamate receptor ionotropic, NMDA 1 / Glutamate receptor ionotropic, NMDA 2A類似検索 - 構成要素 グリシン / DI(HYDROXYETHYL)ETHER / Glutamate receptor ionotropic, NMDA 1 / Glutamate receptor ionotropic, NMDA 2A類似検索 - 構成要素 |
|---|
| 生物種 |    Rattus norvegicus (ドブネズミ) Rattus norvegicus (ドブネズミ) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.4 Å 分子置換 / 解像度: 2.4 Å |
|---|
 データ登録者 データ登録者 | Mou, T.-C. / Conti, P. / Pinto, A. / Tamborini, L. / Sprang, S.R. / Hansen, K.B. |
|---|
| 資金援助 |  米国, 1件 米国, 1件 | 組織 | 認可番号 | 国 |
|---|
| National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) | P20GM103546 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: Proc. Natl. Acad. Sci. U.S.A. / 年: 2017 ジャーナル: Proc. Natl. Acad. Sci. U.S.A. / 年: 2017
タイトル: Structural basis of subunit selectivity for competitive NMDA receptor antagonists with preference for GluN2A over GluN2B subunits.
著者: Lind, G.E. / Mou, T.C. / Tamborini, L. / Pomper, M.G. / De Micheli, C. / Conti, P. / Pinto, A. / Hansen, K.B. |
|---|
| 履歴 | | 登録 | 2017年4月16日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2017年4月26日 | Provider: repository / タイプ: Initial release |
|---|
| 置き換え | 2017年5月17日 | ID: 5DE4 |
|---|
| 改定 1.1 | 2017年5月17日 | Group: Other |
|---|
| 改定 1.2 | 2017年8月2日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.pdbx_database_id_DOI / _citation.title / _citation.year |
|---|
| 改定 1.3 | 2017年8月16日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.journal_abbrev / _citation.pdbx_database_id_PubMed ..._citation.journal_abbrev / _citation.pdbx_database_id_PubMed / _citation.title / _citation_author.name |
|---|
| 改定 1.4 | 2017年8月23日 | Group: Database references / カテゴリ: citation
Item: _citation.journal_volume / _citation.page_first / _citation.page_last |
|---|
| 改定 1.5 | 2017年9月20日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.6 | 2020年1月1日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.7 | 2023年10月4日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード TRANSPORT PROTEIN (運搬体タンパク質) /
TRANSPORT PROTEIN (運搬体タンパク質) /  RECEPTOR (受容体) /
RECEPTOR (受容体) /  NMDA receptor (NMDA型グルタミン酸受容体) /
NMDA receptor (NMDA型グルタミン酸受容体) /  Antagonist (受容体拮抗薬)
Antagonist (受容体拮抗薬) 機能・相同性情報
機能・相同性情報 conditioned place preference / pons maturation /
conditioned place preference / pons maturation /  regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment ...neurotransmitter receptor transport, plasma membrane to endosome / regulation of response to alcohol / response to ammonium ion / receptor recycling / directional locomotion /
regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment ...neurotransmitter receptor transport, plasma membrane to endosome / regulation of response to alcohol / response to ammonium ion / receptor recycling / directional locomotion /  conditioned place preference / pons maturation /
conditioned place preference / pons maturation /  regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment / EPHB-mediated forward signaling / Assembly and cell surface presentation of NMDA receptors / response to hydrogen sulfide / olfactory learning / serotonin metabolic process /
regulation of cell communication / positive regulation of Schwann cell migration / response to environmental enrichment / EPHB-mediated forward signaling / Assembly and cell surface presentation of NMDA receptors / response to hydrogen sulfide / olfactory learning / serotonin metabolic process /  conditioned taste aversion /
conditioned taste aversion /  樹状突起 / regulation of respiratory gaseous exchange / protein localization to postsynaptic membrane / response to other organism / positive regulation of inhibitory postsynaptic potential / propylene metabolic process / response to glycine / regulation of ARF protein signal transduction / cellular response to magnesium ion / response to methylmercury /
樹状突起 / regulation of respiratory gaseous exchange / protein localization to postsynaptic membrane / response to other organism / positive regulation of inhibitory postsynaptic potential / propylene metabolic process / response to glycine / regulation of ARF protein signal transduction / cellular response to magnesium ion / response to methylmercury /  睡眠 / voltage-gated monoatomic cation channel activity / cellular response to dsRNA / dendritic spine organization / response to carbohydrate / locomotion / regulation of monoatomic cation transmembrane transport / response to morphine / cellular response to lipid /
睡眠 / voltage-gated monoatomic cation channel activity / cellular response to dsRNA / dendritic spine organization / response to carbohydrate / locomotion / regulation of monoatomic cation transmembrane transport / response to morphine / cellular response to lipid /  NMDA glutamate receptor activity / Synaptic adhesion-like molecules / RAF/MAP kinase cascade / NMDA selective glutamate receptor complex / glutamate-gated calcium ion channel activity / parallel fiber to Purkinje cell synapse / response to manganese ion / calcium ion transmembrane import into cytosol /
NMDA glutamate receptor activity / Synaptic adhesion-like molecules / RAF/MAP kinase cascade / NMDA selective glutamate receptor complex / glutamate-gated calcium ion channel activity / parallel fiber to Purkinje cell synapse / response to manganese ion / calcium ion transmembrane import into cytosol /  regulation of NMDA receptor activity / protein heterotetramerization /
regulation of NMDA receptor activity / protein heterotetramerization /  glutamate binding / cellular response to zinc ion / positive regulation of reactive oxygen species biosynthetic process / neuromuscular process /
glutamate binding / cellular response to zinc ion / positive regulation of reactive oxygen species biosynthetic process / neuromuscular process /  regulation of synapse assembly /
regulation of synapse assembly /  活動電位 /
活動電位 /  glycine binding / positive regulation of calcium ion transport into cytosol / regulation of dendrite morphogenesis / male mating behavior /
glycine binding / positive regulation of calcium ion transport into cytosol / regulation of dendrite morphogenesis / male mating behavior /  regulation of axonogenesis / spinal cord development / dopamine metabolic process / suckling behavior /
regulation of axonogenesis / spinal cord development / dopamine metabolic process / suckling behavior /  startle response / monoatomic cation transmembrane transport / regulation of neuronal synaptic plasticity / response to amine / modulation of excitatory postsynaptic potential / response to lithium ion /
startle response / monoatomic cation transmembrane transport / regulation of neuronal synaptic plasticity / response to amine / modulation of excitatory postsynaptic potential / response to lithium ion /  social behavior /
social behavior /  学習 / positive regulation of excitatory postsynaptic potential / monoatomic cation transport / ligand-gated monoatomic ion channel activity /
学習 / positive regulation of excitatory postsynaptic potential / monoatomic cation transport / ligand-gated monoatomic ion channel activity /  excitatory synapse / cellular response to glycine / positive regulation of dendritic spine maintenance / response to light stimulus / Unblocking of NMDA receptors, glutamate binding and activation / neuron development / positive regulation of protein targeting to membrane / regulation of postsynaptic membrane potential /
excitatory synapse / cellular response to glycine / positive regulation of dendritic spine maintenance / response to light stimulus / Unblocking of NMDA receptors, glutamate binding and activation / neuron development / positive regulation of protein targeting to membrane / regulation of postsynaptic membrane potential /  phosphatase binding /
phosphatase binding /  glutamate receptor binding /
glutamate receptor binding /  postsynaptic density, intracellular component / calcium ion homeostasis / cellular response to manganese ion /
postsynaptic density, intracellular component / calcium ion homeostasis / cellular response to manganese ion /  prepulse inhibition / multicellular organismal response to stress /
prepulse inhibition / multicellular organismal response to stress /  long-term memory / monoatomic cation channel activity / regulation of neuron apoptotic process / presynaptic active zone membrane /
long-term memory / monoatomic cation channel activity / regulation of neuron apoptotic process / presynaptic active zone membrane /  synaptic cleft / glutamate-gated receptor activity / response to fungicide / sensory perception of pain /
synaptic cleft / glutamate-gated receptor activity / response to fungicide / sensory perception of pain /  cell adhesion molecule binding / dendrite membrane / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / response to amphetamine / ionotropic glutamate receptor signaling pathway /
cell adhesion molecule binding / dendrite membrane / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / response to amphetamine / ionotropic glutamate receptor signaling pathway /  excitatory postsynaptic potential / hippocampal mossy fiber to CA3 synapse
excitatory postsynaptic potential / hippocampal mossy fiber to CA3 synapse
 Rattus norvegicus (ドブネズミ)
Rattus norvegicus (ドブネズミ) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.4 Å
分子置換 / 解像度: 2.4 Å  データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: Proc. Natl. Acad. Sci. U.S.A. / 年: 2017
ジャーナル: Proc. Natl. Acad. Sci. U.S.A. / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5vih.cif.gz
5vih.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5vih.ent.gz
pdb5vih.ent.gz PDB形式
PDB形式 5vih.json.gz
5vih.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/vi/5vih
https://data.pdbj.org/pub/pdb/validation_reports/vi/5vih ftp://data.pdbj.org/pub/pdb/validation_reports/vi/5vih
ftp://data.pdbj.org/pub/pdb/validation_reports/vi/5vih リンク
リンク 集合体
集合体
 要素
要素
 Rattus norvegicus (ドブネズミ) / 遺伝子: Grin1, Nmdar1 / 発現宿主:
Rattus norvegicus (ドブネズミ) / 遺伝子: Grin1, Nmdar1 / 発現宿主: 
 Escherichia coli (大腸菌) / 参照: UniProt: P35439
Escherichia coli (大腸菌) / 参照: UniProt: P35439
 Rattus norvegicus (ドブネズミ) / 遺伝子: Grin2a / 発現宿主:
Rattus norvegicus (ドブネズミ) / 遺伝子: Grin2a / 発現宿主: 
 Escherichia coli (大腸菌) / 参照: UniProt: Q00959
Escherichia coli (大腸菌) / 参照: UniProt: Q00959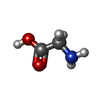





 グリシン
グリシン ジエチレングリコール
ジエチレングリコール 水
水 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 19-ID / 波長: 0.987 Å
/ ビームライン: 19-ID / 波長: 0.987 Å : 0.987 Å / 相対比: 1
: 0.987 Å / 相対比: 1  解析
解析 :
:  分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー


















 PDBj
PDBj







