| 登録情報 | データベース: PDB / ID: 5o2z
|
|---|
| タイトル | Domain swap dimer of the G167R variant of gelsolin second domain |
|---|
 要素 要素 | Gelsolin |
|---|
 キーワード キーワード |  STRUCTURAL PROTEIN (タンパク質) / STRUCTURAL PROTEIN (タンパク質) /  Amyloidosis (アミロイドーシス) / Amyloidosis (アミロイドーシス) /  Gelsolin / 3D domain swap / dimer / pathological mutant Gelsolin / 3D domain swap / dimer / pathological mutant |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.7 Å 分子置換 / 解像度: 1.7 Å |
|---|
 データ登録者 データ登録者 | Boni, F. / Milani, M. / Mastrangelo, E. / de Rosa, M. |
|---|
| 資金援助 |  イタリア, 1件 イタリア, 1件 | 組織 | 認可番号 | 国 |
|---|
| Fondazione Telethon | GEP15070 |  イタリア イタリア |
|
|---|
 引用 引用 |  ジャーナル: Hum. Mol. Genet. / 年: 2018 ジャーナル: Hum. Mol. Genet. / 年: 2018
タイトル: Gelsolin pathogenic Gly167Arg mutation promotes domain-swap dimerization of the protein.
著者: Boni, F. / Milani, M. / Barbiroli, A. / Diomede, L. / Mastrangelo, E. / de Rosa, M. |
|---|
| 履歴 | | 登録 | 2017年5月23日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2017年11月8日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2018年1月3日 | Group: Database references / カテゴリ: citation
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation.year |
|---|
| 改定 1.2 | 2019年8月14日 | Group: Data collection / カテゴリ: reflns / reflns_shell
Item: _reflns.pdbx_Rrim_I_all / _reflns_shell.pdbx_Rrim_I_all |
|---|
| 改定 1.3 | 2024年1月17日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_asym_id / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_asym_id / _pdbx_struct_conn_angle.ptnr2_auth_comp_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr2_label_atom_id / _pdbx_struct_conn_angle.ptnr2_label_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_symmetry |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素
 キーワード
キーワード STRUCTURAL PROTEIN (タンパク質) /
STRUCTURAL PROTEIN (タンパク質) /  Amyloidosis (アミロイドーシス) /
Amyloidosis (アミロイドーシス) /  Gelsolin / 3D domain swap / dimer / pathological mutant
Gelsolin / 3D domain swap / dimer / pathological mutant 機能・相同性情報
機能・相同性情報 renal protein absorption / positive regulation of keratinocyte apoptotic process / positive regulation of protein processing in phagocytic vesicle / positive regulation of actin nucleation / phosphatidylinositol 3-kinase catalytic subunit binding / positive regulation of cysteine-type endopeptidase activity involved in apoptotic signaling pathway ...striated muscle atrophy / regulation of establishment of T cell polarity / regulation of plasma membrane raft polarization / regulation of receptor clustering /
renal protein absorption / positive regulation of keratinocyte apoptotic process / positive regulation of protein processing in phagocytic vesicle / positive regulation of actin nucleation / phosphatidylinositol 3-kinase catalytic subunit binding / positive regulation of cysteine-type endopeptidase activity involved in apoptotic signaling pathway ...striated muscle atrophy / regulation of establishment of T cell polarity / regulation of plasma membrane raft polarization / regulation of receptor clustering /  renal protein absorption / positive regulation of keratinocyte apoptotic process / positive regulation of protein processing in phagocytic vesicle / positive regulation of actin nucleation / phosphatidylinositol 3-kinase catalytic subunit binding / positive regulation of cysteine-type endopeptidase activity involved in apoptotic signaling pathway / actin cap /
renal protein absorption / positive regulation of keratinocyte apoptotic process / positive regulation of protein processing in phagocytic vesicle / positive regulation of actin nucleation / phosphatidylinositol 3-kinase catalytic subunit binding / positive regulation of cysteine-type endopeptidase activity involved in apoptotic signaling pathway / actin cap /  regulation of podosome assembly / sequestering of actin monomers /
regulation of podosome assembly / sequestering of actin monomers /  myosin II binding / negative regulation of viral entry into host cell / actin filament severing / actin filament capping / barbed-end actin filament capping / actin polymerization or depolymerization / actin filament depolymerization / cell projection assembly / cardiac muscle cell contraction /
myosin II binding / negative regulation of viral entry into host cell / actin filament severing / actin filament capping / barbed-end actin filament capping / actin polymerization or depolymerization / actin filament depolymerization / cell projection assembly / cardiac muscle cell contraction /  podosome / Sensory processing of sound by outer hair cells of the cochlea / relaxation of cardiac muscle /
podosome / Sensory processing of sound by outer hair cells of the cochlea / relaxation of cardiac muscle /  phagocytosis, engulfment / cortical actin cytoskeleton / hepatocyte apoptotic process /
phagocytosis, engulfment / cortical actin cytoskeleton / hepatocyte apoptotic process /  cilium assembly /
cilium assembly /  筋形質 / Caspase-mediated cleavage of cytoskeletal proteins / phagocytic vesicle /
筋形質 / Caspase-mediated cleavage of cytoskeletal proteins / phagocytic vesicle /  phosphatidylinositol-4,5-bisphosphate binding / response to muscle stretch / actin filament polymerization /
phosphatidylinositol-4,5-bisphosphate binding / response to muscle stretch / actin filament polymerization /  central nervous system development / actin filament organization / protein destabilization / cellular response to type II interferon /
central nervous system development / actin filament organization / protein destabilization / cellular response to type II interferon /  actin filament binding /
actin filament binding /  マイクロフィラメント /
マイクロフィラメント /  lamellipodium /
lamellipodium /  actin binding / secretory granule lumen / ficolin-1-rich granule lumen / amyloid fibril formation / blood microparticle / Amyloid fiber formation /
actin binding / secretory granule lumen / ficolin-1-rich granule lumen / amyloid fibril formation / blood microparticle / Amyloid fiber formation /  focal adhesion /
focal adhesion /  calcium ion binding / Neutrophil degranulation / positive regulation of gene expression /
calcium ion binding / Neutrophil degranulation / positive regulation of gene expression /  extracellular space / extracellular exosome / extracellular region /
extracellular space / extracellular exosome / extracellular region /  細胞膜 /
細胞膜 /  細胞質基質 /
細胞質基質 /  細胞質
細胞質
 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.7 Å
分子置換 / 解像度: 1.7 Å  データ登録者
データ登録者 イタリア, 1件
イタリア, 1件  引用
引用 ジャーナル: Hum. Mol. Genet. / 年: 2018
ジャーナル: Hum. Mol. Genet. / 年: 2018 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5o2z.cif.gz
5o2z.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5o2z.ent.gz
pdb5o2z.ent.gz PDB形式
PDB形式 5o2z.json.gz
5o2z.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/o2/5o2z
https://data.pdbj.org/pub/pdb/validation_reports/o2/5o2z ftp://data.pdbj.org/pub/pdb/validation_reports/o2/5o2z
ftp://data.pdbj.org/pub/pdb/validation_reports/o2/5o2z
 リンク
リンク 集合体
集合体
 要素
要素 / AGEL / Actin-depolymerizing factor / ADF / Brevin
/ AGEL / Actin-depolymerizing factor / ADF / Brevin
 Homo sapiens (ヒト) / 遺伝子: GSN / プラスミド: pET28b / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: GSN / プラスミド: pET28b / 発現宿主: 
 Escherichia coli BL21 (大腸菌) / 参照: UniProt: P06396
Escherichia coli BL21 (大腸菌) / 参照: UniProt: P06396
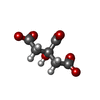









 クエン酸
クエン酸 酢酸塩
酢酸塩 グリセリン
グリセリン 水
水 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  ESRF
ESRF  / ビームライン: ID30B / 波長: 1.0109 Å
/ ビームライン: ID30B / 波長: 1.0109 Å : 1.0109 Å / 相対比: 1
: 1.0109 Å / 相対比: 1  解析
解析 :
:  分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj












